Mol:FLIG1LNI0006
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 33 36 0 0 0 0 0 0 0 0999 V2000 | + | 33 36 0 0 0 0 0 0 0 0999 V2000 |
| − | -2.8431 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8431 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8431 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8431 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2868 -0.8592 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2868 -0.8592 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7305 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7305 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7305 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7305 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2868 0.4255 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2868 0.4255 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1742 -0.8592 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1742 -0.8592 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6179 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6179 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6179 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6179 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1742 0.4255 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1742 0.4255 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.0618 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.0618 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.0618 -1.5459 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.0618 -1.5459 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5330 -1.8893 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5330 -1.8893 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1278 -1.5459 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1278 -1.5459 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1278 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1278 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5330 -0.5157 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5330 -0.5157 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1725 -1.5457 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1725 -1.5457 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7843 -1.9250 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7843 -1.9250 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5394 0.1043 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5394 0.1043 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2868 -1.5013 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2868 -1.5013 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.3992 0.4254 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3992 0.4254 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7220 -0.5160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7220 -0.5160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3162 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3162 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9104 -0.5160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9104 -0.5160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9104 0.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9104 0.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5046 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5046 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2868 1.0676 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2868 1.0676 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8961 1.4194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8961 1.4194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8961 2.1220 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8961 2.1220 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2876 2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2876 2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.5046 2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5046 2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1156 -2.0608 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1156 -2.0608 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8301 -2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8301 -2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 8 11 1 0 0 0 0 | + | 8 11 1 0 0 0 0 |
| − | 11 12 2 0 0 0 0 | + | 11 12 2 0 0 0 0 |
| − | 12 13 1 0 0 0 0 | + | 12 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 11 1 0 0 0 0 | + | 16 11 1 0 0 0 0 |
| − | 7 17 2 0 0 0 0 | + | 7 17 2 0 0 0 0 |
| − | 14 18 1 0 0 0 0 | + | 14 18 1 0 0 0 0 |
| − | 9 19 1 0 0 0 0 | + | 9 19 1 0 0 0 0 |
| − | 19 16 1 0 0 0 0 | + | 19 16 1 0 0 0 0 |
| − | 3 20 1 0 0 0 0 | + | 3 20 1 0 0 0 0 |
| − | 1 21 1 0 0 0 0 | + | 1 21 1 0 0 0 0 |
| − | 15 22 1 0 0 0 0 | + | 15 22 1 0 0 0 0 |
| − | 22 23 1 0 0 0 0 | + | 22 23 1 0 0 0 0 |
| − | 23 24 2 0 0 0 0 | + | 23 24 2 0 0 0 0 |
| − | 24 25 1 0 0 0 0 | + | 24 25 1 0 0 0 0 |
| − | 24 26 1 0 0 0 0 | + | 24 26 1 0 0 0 0 |
| − | 6 27 1 0 0 0 0 | + | 6 27 1 0 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 29 2 0 0 0 0 | + | 28 29 2 0 0 0 0 |
| − | 29 30 1 0 0 0 0 | + | 29 30 1 0 0 0 0 |
| − | 29 31 1 0 0 0 0 | + | 29 31 1 0 0 0 0 |
| − | 13 32 1 0 0 0 0 | + | 13 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 32 33 | + | M SAL 1 2 32 33 |
| − | M SBL 1 1 35 | + | M SBL 1 1 35 |
| − | M SMT 1 OCH3 | + | M SMT 1 OCH3 |
| − | M SBV 1 35 -6.6182 4.3672 | + | M SBV 1 35 -6.6182 4.3672 |
| − | S SKP 8 | + | S SKP 8 |
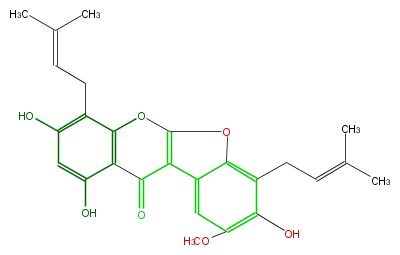
| − | ID FLIG1LNI0006 | + | ID FLIG1LNI0006 |
| − | KNApSAcK_ID C00010070 | + | KNApSAcK_ID C00010070 |
| − | NAME 8-Dimethylallyllisetin;8-Prenyllisetin | + | NAME 8-Dimethylallyllisetin;8-Prenyllisetin |
| − | CAS_RN 126513-21-1 | + | CAS_RN 126513-21-1 |
| − | FORMULA C26H26O7 | + | FORMULA C26H26O7 |
| − | EXACTMASS 450.167853186 | + | EXACTMASS 450.167853186 |
| − | AVERAGEMASS 450.48043999999993 | + | AVERAGEMASS 450.48043999999993 |
| − | SMILES Oc(c12)cc(O)c(CC=C(C)C)c1Oc(o4)c(c(c43)cc(OC)c(c(CC=C(C)C)3)O)C2=O | + | SMILES Oc(c12)cc(O)c(CC=C(C)C)c1Oc(o4)c(c(c43)cc(OC)c(c(CC=C(C)C)3)O)C2=O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
33 36 0 0 0 0 0 0 0 0999 V2000
-2.8431 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8431 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2868 -0.8592 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.7305 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.7305 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2868 0.4255 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1742 -0.8592 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6179 -0.5380 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6179 0.1043 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1742 0.4255 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.0618 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.0618 -1.5459 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.5330 -1.8893 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1278 -1.5459 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1278 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.5330 -0.5157 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1725 -1.5457 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7843 -1.9250 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.5394 0.1043 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.2868 -1.5013 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.3992 0.4254 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7220 -0.5160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3162 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.9104 -0.5160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.9104 0.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5046 -0.8591 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2868 1.0676 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8961 1.4194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8961 2.1220 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2876 2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.5046 2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.1156 -2.0608 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.8301 -2.4733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
8 11 1 0 0 0 0
11 12 2 0 0 0 0
12 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 11 1 0 0 0 0
7 17 2 0 0 0 0
14 18 1 0 0 0 0
9 19 1 0 0 0 0
19 16 1 0 0 0 0
3 20 1 0 0 0 0
1 21 1 0 0 0 0
15 22 1 0 0 0 0
22 23 1 0 0 0 0
23 24 2 0 0 0 0
24 25 1 0 0 0 0
24 26 1 0 0 0 0
6 27 1 0 0 0 0
27 28 1 0 0 0 0
28 29 2 0 0 0 0
29 30 1 0 0 0 0
29 31 1 0 0 0 0
13 32 1 0 0 0 0
32 33 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 32 33
M SBL 1 1 35
M SMT 1 OCH3
M SBV 1 35 -6.6182 4.3672
S SKP 8
ID FLIG1LNI0006
KNApSAcK_ID C00010070
NAME 8-Dimethylallyllisetin;8-Prenyllisetin
CAS_RN 126513-21-1
FORMULA C26H26O7
EXACTMASS 450.167853186
AVERAGEMASS 450.48043999999993
SMILES Oc(c12)cc(O)c(CC=C(C)C)c1Oc(o4)c(c(c43)cc(OC)c(c(CC=C(C)C)3)O)C2=O
M END