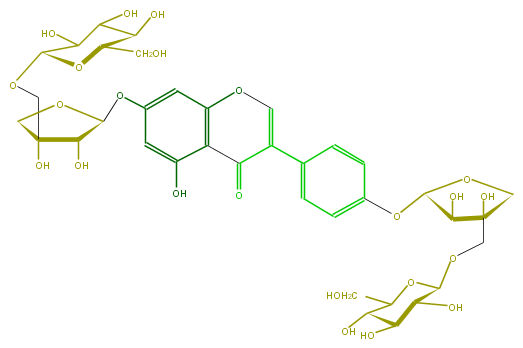
Mol:FLIAAAGS0007
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 60 66 0 0 0 0 0 0 0 0999 V2000 | + | 60 66 0 0 0 0 0 0 0 0999 V2000 |
| − | -3.3510 1.8328 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3510 1.8328 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.7453 1.5178 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.7453 1.5178 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0245 1.9340 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0245 1.9340 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3040 1.5180 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3040 1.5180 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3040 0.6551 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3040 0.6551 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5568 0.2238 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5568 0.2238 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1905 0.6551 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1905 0.6551 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1906 1.5180 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1906 1.5180 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5568 1.9495 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5568 1.9495 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.7450 0.6863 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.7450 0.6863 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0245 0.2701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0245 0.2701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5568 -0.4971 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5568 -0.4971 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9372 0.2240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9372 0.2240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9372 -0.6007 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9372 -0.6007 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6517 -1.0133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6517 -1.0133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3660 -0.6008 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3660 -0.6008 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3660 0.2240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3660 0.2240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6517 0.6365 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6517 0.6365 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1239 -0.9915 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1239 -0.9915 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.7449 1.2154 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.7449 1.2154 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.2499 0.7823 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.2499 0.7823 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.3218 0.7823 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.3218 0.7823 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.7266 1.2134 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7266 1.2134 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7549 1.6279 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7549 1.6279 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.2499 1.7723 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.2499 1.7723 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.2499 0.2048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.2499 0.2048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.3218 0.2033 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.3218 0.2033 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.1853 2.8214 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.1853 2.8214 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.3081 2.4919 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.3081 2.4919 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.7869 2.9490 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7869 2.9490 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.9839 3.2108 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.9839 3.2108 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.8254 3.4828 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.8254 3.4828 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.3232 2.9910 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.3232 2.9910 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.9428 3.2815 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.9428 3.2815 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1760 3.7665 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1760 3.7665 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5555 3.7268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5555 3.7268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.8480 2.0816 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.8480 2.0816 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.7841 -0.4853 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.7841 -0.4853 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4441 -1.0834 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4441 -1.0834 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1660 -1.0422 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1660 -1.0422 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.8480 -0.5073 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.8480 -0.5073 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7755 -0.1154 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7755 -0.1154 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4441 -0.5261 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4441 -0.5261 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1674 -1.6210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1674 -1.6210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1660 -0.5260 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1660 -0.5260 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4441 -1.9703 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4441 -1.9703 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4316 -3.2756 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4316 -3.2756 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1162 -3.5642 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1162 -3.5642 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5500 -3.0237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5500 -3.0237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1369 -2.6934 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1369 -2.6934 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4676 -2.5402 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4676 -2.5402 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0146 -3.0754 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0146 -3.0754 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9170 -3.6909 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9170 -3.6909 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.5152 -3.7665 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.5152 -3.7665 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4303 -3.1076 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4303 -3.1076 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0245 -0.4558 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0245 -0.4558 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2844 -2.8486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2844 -2.8486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4457 -1.8611 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4457 -1.8611 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.9150 2.8290 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.9150 2.8290 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.8027 2.1643 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8027 2.1643 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 7 1 0 0 0 0 | + | 6 7 1 0 0 0 0 |
| − | 7 8 2 0 0 0 0 | + | 7 8 2 0 0 0 0 |
| − | 8 9 1 0 0 0 0 | + | 8 9 1 0 0 0 0 |
| − | 9 4 1 0 0 0 0 | + | 9 4 1 0 0 0 0 |
| − | 2 10 1 0 0 0 0 | + | 2 10 1 0 0 0 0 |
| − | 10 11 2 0 0 0 0 | + | 10 11 2 0 0 0 0 |
| − | 11 5 1 0 0 0 0 | + | 11 5 1 0 0 0 0 |
| − | 6 12 2 0 0 0 0 | + | 6 12 2 0 0 0 0 |
| − | 7 13 1 0 0 0 0 | + | 7 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 17 1 0 0 0 0 | + | 16 17 1 0 0 0 0 |
| − | 17 18 2 0 0 0 0 | + | 17 18 2 0 0 0 0 |
| − | 18 13 1 0 0 0 0 | + | 18 13 1 0 0 0 0 |
| − | 19 16 1 0 0 0 0 | + | 19 16 1 0 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 21 22 1 1 0 0 0 | + | 21 22 1 1 0 0 0 |
| − | 23 22 1 1 0 0 0 | + | 23 22 1 1 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 20 1 0 0 0 0 | + | 24 20 1 0 0 0 0 |
| − | 21 25 1 0 0 0 0 | + | 21 25 1 0 0 0 0 |
| − | 21 26 1 0 0 0 0 | + | 21 26 1 0 0 0 0 |
| − | 22 27 1 0 0 0 0 | + | 22 27 1 0 0 0 0 |
| − | 23 1 1 0 0 0 0 | + | 23 1 1 0 0 0 0 |
| − | 28 29 1 1 0 0 0 | + | 28 29 1 1 0 0 0 |
| − | 29 30 1 1 0 0 0 | + | 29 30 1 1 0 0 0 |
| − | 31 30 1 1 0 0 0 | + | 31 30 1 1 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 33 28 1 0 0 0 0 | + | 33 28 1 0 0 0 0 |
| − | 33 34 1 0 0 0 0 | + | 33 34 1 0 0 0 0 |
| − | 32 35 1 0 0 0 0 | + | 32 35 1 0 0 0 0 |
| − | 31 36 1 0 0 0 0 | + | 31 36 1 0 0 0 0 |
| − | 28 37 1 0 0 0 0 | + | 28 37 1 0 0 0 0 |
| − | 37 25 1 0 0 0 0 | + | 37 25 1 0 0 0 0 |
| − | 38 39 1 1 0 0 0 | + | 38 39 1 1 0 0 0 |
| − | 39 40 1 1 0 0 0 | + | 39 40 1 1 0 0 0 |
| − | 41 40 1 1 0 0 0 | + | 41 40 1 1 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 42 38 1 0 0 0 0 | + | 42 38 1 0 0 0 0 |
| − | 39 43 1 0 0 0 0 | + | 39 43 1 0 0 0 0 |
| − | 40 44 1 0 0 0 0 | + | 40 44 1 0 0 0 0 |
| − | 40 45 1 0 0 0 0 | + | 40 45 1 0 0 0 0 |
| − | 19 38 1 0 0 0 0 | + | 19 38 1 0 0 0 0 |
| − | 44 46 1 0 0 0 0 | + | 44 46 1 0 0 0 0 |
| − | 47 48 1 1 0 0 0 | + | 47 48 1 1 0 0 0 |
| − | 48 49 1 1 0 0 0 | + | 48 49 1 1 0 0 0 |
| − | 50 49 1 1 0 0 0 | + | 50 49 1 1 0 0 0 |
| − | 50 51 1 0 0 0 0 | + | 50 51 1 0 0 0 0 |
| − | 51 52 1 0 0 0 0 | + | 51 52 1 0 0 0 0 |
| − | 52 47 1 0 0 0 0 | + | 52 47 1 0 0 0 0 |
| − | 47 53 1 0 0 0 0 | + | 47 53 1 0 0 0 0 |
| − | 48 54 1 0 0 0 0 | + | 48 54 1 0 0 0 0 |
| − | 49 55 1 0 0 0 0 | + | 49 55 1 0 0 0 0 |
| − | 50 46 1 0 0 0 0 | + | 50 46 1 0 0 0 0 |
| − | 11 56 1 0 0 0 0 | + | 11 56 1 0 0 0 0 |
| − | 57 58 1 0 0 0 0 | + | 57 58 1 0 0 0 0 |
| − | 52 57 1 0 0 0 0 | + | 52 57 1 0 0 0 0 |
| − | 59 60 1 0 0 0 0 | + | 59 60 1 0 0 0 0 |
| − | 30 59 1 0 0 0 0 | + | 30 59 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 57 58 | + | M SAL 1 2 57 58 |
| − | M SBL 1 1 64 | + | M SBL 1 1 64 |
| − | M SMT 1 ^ CH2OH | + | M SMT 1 ^ CH2OH |
| − | M SBV 1 64 0.7302 -0.2269 | + | M SBV 1 64 0.7302 -0.2269 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 59 60 | + | M SAL 2 2 59 60 |
| − | M SBL 2 1 66 | + | M SBL 2 1 66 |
| − | M SMT 2 CH2OH | + | M SMT 2 CH2OH |
| − | M SBV 2 66 -0.8720 0.1200 | + | M SBV 2 66 -0.8720 0.1200 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FLIAAAGS0007 | + | ID FLIAAAGS0007 |
| − | FORMULA C37H46O23 | + | FORMULA C37H46O23 |
| − | EXACTMASS 858.242987778 | + | EXACTMASS 858.242987778 |
| − | AVERAGEMASS 858.7473399999999 | + | AVERAGEMASS 858.7473399999999 |
| − | SMILES OC(C7O)C(CO)OC(C(O)7)OCC(C1O)(COC1Oc(c2)cc(O)c(C(=O)3)c(OC=C(c(c6)ccc(c6)OC(C(O)4)OCC4(COC(C(O)5)OC(CO)C(O)C5O)O)3)2)O | + | SMILES OC(C7O)C(CO)OC(C(O)7)OCC(C1O)(COC1Oc(c2)cc(O)c(C(=O)3)c(OC=C(c(c6)ccc(c6)OC(C(O)4)OCC4(COC(C(O)5)OC(CO)C(O)C5O)O)3)2)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
60 66 0 0 0 0 0 0 0 0999 V2000
-3.3510 1.8328 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.7453 1.5178 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.0245 1.9340 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3040 1.5180 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3040 0.6551 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5568 0.2238 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.1905 0.6551 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.1906 1.5180 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5568 1.9495 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.7450 0.6863 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.0245 0.2701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5568 -0.4971 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.9372 0.2240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9372 -0.6007 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.6517 -1.0133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3660 -0.6008 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3660 0.2240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.6517 0.6365 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1239 -0.9915 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.7449 1.2154 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.2499 0.7823 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.3218 0.7823 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.7266 1.2134 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.7549 1.6279 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.2499 1.7723 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.2499 0.2048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.3218 0.2033 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.1853 2.8214 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.3081 2.4919 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.7869 2.9490 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.9839 3.2108 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.8254 3.4828 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.3232 2.9910 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.9428 3.2815 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.1760 3.7665 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.5555 3.7268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.8480 2.0816 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.7841 -0.4853 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.4441 -1.0834 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.1660 -1.0422 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.8480 -0.5073 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.7755 -0.1154 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.4441 -0.5261 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.1674 -1.6210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.1660 -0.5260 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.4441 -1.9703 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.4316 -3.2756 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1162 -3.5642 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5500 -3.0237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1369 -2.6934 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4676 -2.5402 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0146 -3.0754 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9170 -3.6909 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.5152 -3.7665 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.4303 -3.1076 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.0245 -0.4558 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.2844 -2.8486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4457 -1.8611 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.9150 2.8290 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.8027 2.1643 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 7 1 0 0 0 0
7 8 2 0 0 0 0
8 9 1 0 0 0 0
9 4 1 0 0 0 0
2 10 1 0 0 0 0
10 11 2 0 0 0 0
11 5 1 0 0 0 0
6 12 2 0 0 0 0
7 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 17 1 0 0 0 0
17 18 2 0 0 0 0
18 13 1 0 0 0 0
19 16 1 0 0 0 0
20 21 1 1 0 0 0
21 22 1 1 0 0 0
23 22 1 1 0 0 0
23 24 1 0 0 0 0
24 20 1 0 0 0 0
21 25 1 0 0 0 0
21 26 1 0 0 0 0
22 27 1 0 0 0 0
23 1 1 0 0 0 0
28 29 1 1 0 0 0
29 30 1 1 0 0 0
31 30 1 1 0 0 0
31 32 1 0 0 0 0
32 33 1 0 0 0 0
33 28 1 0 0 0 0
33 34 1 0 0 0 0
32 35 1 0 0 0 0
31 36 1 0 0 0 0
28 37 1 0 0 0 0
37 25 1 0 0 0 0
38 39 1 1 0 0 0
39 40 1 1 0 0 0
41 40 1 1 0 0 0
41 42 1 0 0 0 0
42 38 1 0 0 0 0
39 43 1 0 0 0 0
40 44 1 0 0 0 0
40 45 1 0 0 0 0
19 38 1 0 0 0 0
44 46 1 0 0 0 0
47 48 1 1 0 0 0
48 49 1 1 0 0 0
50 49 1 1 0 0 0
50 51 1 0 0 0 0
51 52 1 0 0 0 0
52 47 1 0 0 0 0
47 53 1 0 0 0 0
48 54 1 0 0 0 0
49 55 1 0 0 0 0
50 46 1 0 0 0 0
11 56 1 0 0 0 0
57 58 1 0 0 0 0
52 57 1 0 0 0 0
59 60 1 0 0 0 0
30 59 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 57 58
M SBL 1 1 64
M SMT 1 ^ CH2OH
M SBV 1 64 0.7302 -0.2269
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 59 60
M SBL 2 1 66
M SMT 2 CH2OH
M SBV 2 66 -0.8720 0.1200
S SKP 5
ID FLIAAAGS0007
FORMULA C37H46O23
EXACTMASS 858.242987778
AVERAGEMASS 858.7473399999999
SMILES OC(C7O)C(CO)OC(C(O)7)OCC(C1O)(COC1Oc(c2)cc(O)c(C(=O)3)c(OC=C(c(c6)ccc(c6)OC(C(O)4)OCC4(COC(C(O)5)OC(CO)C(O)C5O)O)3)2)O
M END