Mol:FL5FAGGS0011
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 47 51 0 0 0 0 0 0 0 0999 V2000 | + | 47 51 0 0 0 0 0 0 0 0999 V2000 |
| − | -1.3536 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3536 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3536 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3536 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6391 -0.8081 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6391 -0.8081 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0755 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0755 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0755 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0755 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6391 0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6391 0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7900 -0.8081 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7900 -0.8081 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5046 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5046 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5046 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5046 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7900 0.8420 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7900 0.8420 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7900 -1.5325 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7900 -1.5325 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2804 0.8358 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2804 0.8358 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0087 0.4154 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0087 0.4154 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.7370 0.8358 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.7370 0.8358 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.7370 1.6767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.7370 1.6767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0087 2.0972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0087 2.0972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2804 1.6767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2804 1.6767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6391 -1.5312 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6391 -1.5312 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5164 2.1268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5164 2.1268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2071 0.9223 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2071 0.9223 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2798 -0.9107 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2798 -0.9107 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0087 2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0087 2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4650 0.4155 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4650 0.4155 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.6769 0.9617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.6769 0.9617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.2002 0.3324 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.2002 0.3324 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.5136 0.5993 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5136 0.5993 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8512 0.6065 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8512 0.6065 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.3325 1.0879 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3325 1.0879 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9331 0.7709 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9331 0.7709 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.2594 0.8223 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.2594 0.8223 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.0451 0.3567 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.0451 0.3567 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8715 0.1026 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8715 0.1026 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3576 -0.9364 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3576 -0.9364 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6884 -1.3228 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6884 -1.3228 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4379 -1.5104 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4379 -1.5104 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.9792 -2.0680 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.9792 -2.0680 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.6485 -1.6817 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.6485 -1.6817 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8989 -1.4940 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8989 -1.4940 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8269 -0.7661 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8269 -0.7661 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7256 -1.2005 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7256 -1.2005 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.0000 -2.0338 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.0000 -2.0338 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.8069 -2.4080 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.8069 -2.4080 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.7246 -2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.7246 -2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8892 -2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8892 -2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.4770 1.3633 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.4770 1.3633 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.7246 1.6683 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.7246 1.6683 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.5890 2.2913 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5890 2.2913 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 3 18 1 0 0 0 0 | + | 3 18 1 0 0 0 0 |
| − | 19 15 1 0 0 0 0 | + | 19 15 1 0 0 0 0 |
| − | 4 3 1 0 0 0 0 | + | 4 3 1 0 0 0 0 |
| − | 1 20 1 0 0 0 0 | + | 1 20 1 0 0 0 0 |
| − | 21 8 1 0 0 0 0 | + | 21 8 1 0 0 0 0 |
| − | 16 22 1 0 0 0 0 | + | 16 22 1 0 0 0 0 |
| − | 14 23 1 0 0 0 0 | + | 14 23 1 0 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 25 26 1 1 0 0 0 | + | 25 26 1 1 0 0 0 |
| − | 27 26 1 1 0 0 0 | + | 27 26 1 1 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 29 1 0 0 0 0 | + | 28 29 1 0 0 0 0 |
| − | 29 24 1 0 0 0 0 | + | 29 24 1 0 0 0 0 |
| − | 24 30 1 0 0 0 0 | + | 24 30 1 0 0 0 0 |
| − | 25 31 1 0 0 0 0 | + | 25 31 1 0 0 0 0 |
| − | 26 32 1 0 0 0 0 | + | 26 32 1 0 0 0 0 |
| − | 27 20 1 0 0 0 0 | + | 27 20 1 0 0 0 0 |
| − | 33 34 1 0 0 0 0 | + | 33 34 1 0 0 0 0 |
| − | 34 35 1 1 0 0 0 | + | 34 35 1 1 0 0 0 |
| − | 35 36 1 1 0 0 0 | + | 35 36 1 1 0 0 0 |
| − | 37 36 1 1 0 0 0 | + | 37 36 1 1 0 0 0 |
| − | 37 38 1 0 0 0 0 | + | 37 38 1 0 0 0 0 |
| − | 38 33 1 0 0 0 0 | + | 38 33 1 0 0 0 0 |
| − | 33 39 1 0 0 0 0 | + | 33 39 1 0 0 0 0 |
| − | 38 40 1 0 0 0 0 | + | 38 40 1 0 0 0 0 |
| − | 37 41 1 0 0 0 0 | + | 37 41 1 0 0 0 0 |
| − | 34 21 1 0 0 0 0 | + | 34 21 1 0 0 0 0 |
| − | 42 43 2 0 0 0 0 | + | 42 43 2 0 0 0 0 |
| − | 42 44 1 0 0 0 0 | + | 42 44 1 0 0 0 0 |
| − | 36 42 1 0 0 0 0 | + | 36 42 1 0 0 0 0 |
| − | 45 46 2 0 0 0 0 | + | 45 46 2 0 0 0 0 |
| − | 45 47 1 0 0 0 0 | + | 45 47 1 0 0 0 0 |
| − | 29 45 1 0 0 0 0 | + | 29 45 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 3 42 43 44 | + | M SAL 1 3 42 43 44 |
| − | M SBL 1 1 48 | + | M SBL 1 1 48 |
| − | M SMT 1 COOH | + | M SMT 1 COOH |
| − | M SBV 1 48 -0.8277 0.3400 | + | M SBV 1 48 -0.8277 0.3400 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 3 45 46 47 | + | M SAL 2 3 45 46 47 |
| − | M SBL 2 1 51 | + | M SBL 2 1 51 |
| − | M SMT 2 ^ COOH | + | M SMT 2 ^ COOH |
| − | M SBV 2 51 0.5439 -0.5923 | + | M SBV 2 51 0.5439 -0.5923 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL5FAGGS0011 | + | ID FL5FAGGS0011 |
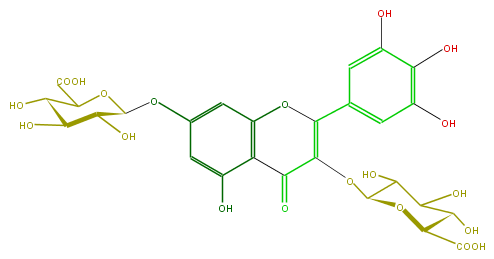
| − | FORMULA C27H26O20 | + | FORMULA C27H26O20 |
| − | EXACTMASS 670.101743272 | + | EXACTMASS 670.101743272 |
| − | AVERAGEMASS 670.48334 | + | AVERAGEMASS 670.48334 |
| − | SMILES c(c1)(OC(O5)C(C(C(O)C5C(O)=O)O)O)cc(c(C3=O)c1OC(=C3OC(C4O)OC(C(C4O)O)C(O)=O)c(c2)cc(c(c(O)2)O)O)O | + | SMILES c(c1)(OC(O5)C(C(C(O)C5C(O)=O)O)O)cc(c(C3=O)c1OC(=C3OC(C4O)OC(C(C4O)O)C(O)=O)c(c2)cc(c(c(O)2)O)O)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
47 51 0 0 0 0 0 0 0 0999 V2000
-1.3536 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3536 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6391 -0.8081 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0755 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0755 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6391 0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7900 -0.8081 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5046 -0.3956 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5046 0.4294 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7900 0.8420 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.7900 -1.5325 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.2804 0.8358 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0087 0.4154 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.7370 0.8358 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.7370 1.6767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0087 2.0972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.2804 1.6767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6391 -1.5312 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.5164 2.1268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.2071 0.9223 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.2798 -0.9107 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0087 2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.4650 0.4155 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.6769 0.9617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.2002 0.3324 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.5136 0.5993 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8512 0.6065 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.3325 1.0879 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.9331 0.7709 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.2594 0.8223 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.0451 0.3567 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.8715 0.1026 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.3576 -0.9364 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6884 -1.3228 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4379 -1.5104 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.9792 -2.0680 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.6485 -1.6817 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8989 -1.4940 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.8269 -0.7661 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.7256 -1.2005 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.0000 -2.0338 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.8069 -2.4080 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.7246 -2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.8892 -2.9379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.4770 1.3633 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.7246 1.6683 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.5890 2.2913 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
3 18 1 0 0 0 0
19 15 1 0 0 0 0
4 3 1 0 0 0 0
1 20 1 0 0 0 0
21 8 1 0 0 0 0
16 22 1 0 0 0 0
14 23 1 0 0 0 0
24 25 1 1 0 0 0
25 26 1 1 0 0 0
27 26 1 1 0 0 0
27 28 1 0 0 0 0
28 29 1 0 0 0 0
29 24 1 0 0 0 0
24 30 1 0 0 0 0
25 31 1 0 0 0 0
26 32 1 0 0 0 0
27 20 1 0 0 0 0
33 34 1 0 0 0 0
34 35 1 1 0 0 0
35 36 1 1 0 0 0
37 36 1 1 0 0 0
37 38 1 0 0 0 0
38 33 1 0 0 0 0
33 39 1 0 0 0 0
38 40 1 0 0 0 0
37 41 1 0 0 0 0
34 21 1 0 0 0 0
42 43 2 0 0 0 0
42 44 1 0 0 0 0
36 42 1 0 0 0 0
45 46 2 0 0 0 0
45 47 1 0 0 0 0
29 45 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 3 42 43 44
M SBL 1 1 48
M SMT 1 COOH
M SBV 1 48 -0.8277 0.3400
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 3 45 46 47
M SBL 2 1 51
M SMT 2 ^ COOH
M SBV 2 51 0.5439 -0.5923
S SKP 5
ID FL5FAGGS0011
FORMULA C27H26O20
EXACTMASS 670.101743272
AVERAGEMASS 670.48334
SMILES c(c1)(OC(O5)C(C(C(O)C5C(O)=O)O)O)cc(c(C3=O)c1OC(=C3OC(C4O)OC(C(C4O)O)C(O)=O)c(c2)cc(c(c(O)2)O)O)O
M END