Mol:FL5FADGS0029
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 60 65 0 0 0 0 0 0 0 0999 V2000 | + | 60 65 0 0 0 0 0 0 0 0999 V2000 |
| − | 3.3326 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3326 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6181 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6181 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6181 2.6587 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6181 2.6587 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3326 3.0712 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3326 3.0712 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0470 2.6587 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0470 2.6587 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0470 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0470 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9036 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9036 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1892 1.8337 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1892 1.8337 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4747 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4747 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4747 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4747 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1892 0.1837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1892 0.1837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9036 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9036 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2398 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2398 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9543 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9543 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9543 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9543 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2398 0.1837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2398 0.1837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1892 -0.6413 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1892 -0.6413 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6687 1.8337 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6687 1.8337 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6181 0.1837 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6181 0.1837 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2398 -0.6413 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2398 -0.6413 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7615 3.0712 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7615 3.0712 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3326 3.8962 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3326 3.8962 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0643 4.3187 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0643 4.3187 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8857 -1.6665 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8857 -1.6665 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6466 -1.9861 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6466 -1.9861 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.1559 -1.3366 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.1559 -1.3366 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9250 -1.0374 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9250 -1.0374 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.1641 -0.7177 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.1641 -0.7177 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6547 -1.3671 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6547 -1.3671 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1754 -0.9955 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1754 -0.9955 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6257 -1.0652 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6257 -1.0652 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7932 -2.3436 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7932 -2.3436 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1926 -1.9861 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1926 -1.9861 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4064 -1.9500 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4064 -1.9500 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1682 -3.6416 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1682 -3.6416 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9290 -3.9612 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9290 -3.9612 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4383 -3.3118 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4383 -3.3118 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2074 -3.0125 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2074 -3.0125 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4465 -2.6928 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4465 -2.6928 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9372 -3.3422 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9372 -3.3422 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4578 -2.9706 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4578 -2.9706 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.0919 -3.0403 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.0919 -3.0403 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0756 -4.3187 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0756 -4.3187 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4150 -4.0263 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4150 -4.0263 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6888 -3.9251 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6888 -3.9251 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2161 -1.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2161 -1.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2217 -2.2431 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2217 -2.2431 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0398 -1.7902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0398 -1.7902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4385 -1.0692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4385 -1.0692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2623 -1.0540 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2623 -1.0540 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6615 -0.3320 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6615 -0.3320 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4864 -0.3168 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4864 -0.3168 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9120 -1.0235 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9120 -1.0235 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.5127 -1.7455 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5127 -1.7455 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6879 -1.7607 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6879 -1.7607 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7357 -1.0083 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7357 -1.0083 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9378 -2.4513 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9378 -2.4513 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7615 -2.4361 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7615 -2.4361 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.8851 0.4042 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.8851 0.4042 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7088 0.4194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7088 0.4194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 2 0 0 0 0 | + | 1 2 2 0 0 0 0 |
| − | 2 3 1 0 0 0 0 | + | 2 3 1 0 0 0 0 |
| − | 3 4 2 0 0 0 0 | + | 3 4 2 0 0 0 0 |
| − | 4 5 1 0 0 0 0 | + | 4 5 1 0 0 0 0 |
| − | 5 6 2 0 0 0 0 | + | 5 6 2 0 0 0 0 |
| − | 6 1 1 0 0 0 0 | + | 6 1 1 0 0 0 0 |
| − | 2 7 1 0 0 0 0 | + | 2 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 1 0 0 0 0 | + | 8 9 1 0 0 0 0 |
| − | 9 10 2 0 0 0 0 | + | 9 10 2 0 0 0 0 |
| − | 10 11 1 0 0 0 0 | + | 10 11 1 0 0 0 0 |
| − | 11 12 1 0 0 0 0 | + | 11 12 1 0 0 0 0 |
| − | 12 7 2 0 0 0 0 | + | 12 7 2 0 0 0 0 |
| − | 9 13 1 0 0 0 0 | + | 9 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 10 1 0 0 0 0 | + | 16 10 1 0 0 0 0 |
| − | 14 18 1 0 0 0 0 | + | 14 18 1 0 0 0 0 |
| − | 11 17 2 0 0 0 0 | + | 11 17 2 0 0 0 0 |
| − | 12 19 1 0 0 0 0 | + | 12 19 1 0 0 0 0 |
| − | 16 20 1 0 0 0 0 | + | 16 20 1 0 0 0 0 |
| − | 5 21 1 0 0 0 0 | + | 5 21 1 0 0 0 0 |
| − | 4 22 1 0 0 0 0 | + | 4 22 1 0 0 0 0 |
| − | 22 23 1 0 0 0 0 | + | 22 23 1 0 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 25 26 1 1 0 0 0 | + | 25 26 1 1 0 0 0 |
| − | 27 26 1 1 0 0 0 | + | 27 26 1 1 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 29 1 0 0 0 0 | + | 28 29 1 0 0 0 0 |
| − | 29 24 1 0 0 0 0 | + | 29 24 1 0 0 0 0 |
| − | 29 30 1 0 0 0 0 | + | 29 30 1 0 0 0 0 |
| − | 30 31 1 0 0 0 0 | + | 30 31 1 0 0 0 0 |
| − | 24 32 1 0 0 0 0 | + | 24 32 1 0 0 0 0 |
| − | 25 33 1 0 0 0 0 | + | 25 33 1 0 0 0 0 |
| − | 26 34 1 0 0 0 0 | + | 26 34 1 0 0 0 0 |
| − | 35 36 1 1 0 0 0 | + | 35 36 1 1 0 0 0 |
| − | 36 37 1 1 0 0 0 | + | 36 37 1 1 0 0 0 |
| − | 38 37 1 1 0 0 0 | + | 38 37 1 1 0 0 0 |
| − | 38 39 1 0 0 0 0 | + | 38 39 1 0 0 0 0 |
| − | 39 40 1 0 0 0 0 | + | 39 40 1 0 0 0 0 |
| − | 40 35 1 0 0 0 0 | + | 40 35 1 0 0 0 0 |
| − | 40 41 1 0 0 0 0 | + | 40 41 1 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 35 43 1 0 0 0 0 | + | 35 43 1 0 0 0 0 |
| − | 36 44 1 0 0 0 0 | + | 36 44 1 0 0 0 0 |
| − | 37 45 1 0 0 0 0 | + | 37 45 1 0 0 0 0 |
| − | 38 34 1 0 0 0 0 | + | 38 34 1 0 0 0 0 |
| − | 27 19 1 0 0 0 0 | + | 27 19 1 0 0 0 0 |
| − | 46 47 2 0 0 0 0 | + | 46 47 2 0 0 0 0 |
| − | 46 48 1 0 0 0 0 | + | 46 48 1 0 0 0 0 |
| − | 48 49 2 0 0 0 0 | + | 48 49 2 0 0 0 0 |
| − | 49 50 1 0 0 0 0 | + | 49 50 1 0 0 0 0 |
| − | 50 51 2 0 0 0 0 | + | 50 51 2 0 0 0 0 |
| − | 51 52 1 0 0 0 0 | + | 51 52 1 0 0 0 0 |
| − | 52 53 2 0 0 0 0 | + | 52 53 2 0 0 0 0 |
| − | 53 54 1 0 0 0 0 | + | 53 54 1 0 0 0 0 |
| − | 54 55 2 0 0 0 0 | + | 54 55 2 0 0 0 0 |
| − | 55 50 1 0 0 0 0 | + | 55 50 1 0 0 0 0 |
| − | 53 56 1 0 0 0 0 | + | 53 56 1 0 0 0 0 |
| − | 54 57 1 0 0 0 0 | + | 54 57 1 0 0 0 0 |
| − | 57 58 1 0 0 0 0 | + | 57 58 1 0 0 0 0 |
| − | 52 59 1 0 0 0 0 | + | 52 59 1 0 0 0 0 |
| − | 59 60 1 0 0 0 0 | + | 59 60 1 0 0 0 0 |
| − | 31 46 1 0 0 0 0 | + | 31 46 1 0 0 0 0 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL5FADGS0029 | + | ID FL5FADGS0029 |
| − | KNApSAcK_ID C00013921 | + | KNApSAcK_ID C00013921 |
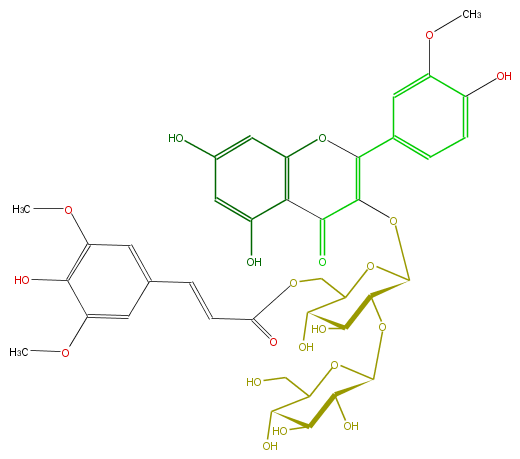
| − | NAME Isorhamnetin 3-(6''-(E)-sinapoylsophoroside);Quercetin 3'-methyl ether 3-(6''-(E)-sinapoylsophoroside) | + | NAME Isorhamnetin 3-(6''-(E)-sinapoylsophoroside);Quercetin 3'-methyl ether 3-(6''-(E)-sinapoylsophoroside) |
| − | CAS_RN - | + | CAS_RN - |
| − | FORMULA C39H42O21 | + | FORMULA C39H42O21 |
| − | EXACTMASS 846.2218584059999 | + | EXACTMASS 846.2218584059999 |
| − | AVERAGEMASS 846.73818 | + | AVERAGEMASS 846.73818 |
| − | SMILES O(C)c(c(O)1)cc(C=CC(OCC(C(O)3)OC(OC(C(=O)4)=C(c(c6)cc(OC)c(c6)O)Oc(c5)c(c(cc(O)5)O)4)C(C3O)OC(C(O)2)OC(CO)C(O)C2O)=O)cc(OC)1 | + | SMILES O(C)c(c(O)1)cc(C=CC(OCC(C(O)3)OC(OC(C(=O)4)=C(c(c6)cc(OC)c(c6)O)Oc(c5)c(c(cc(O)5)O)4)C(C3O)OC(C(O)2)OC(CO)C(O)C2O)=O)cc(OC)1 |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
60 65 0 0 0 0 0 0 0 0999 V2000
3.3326 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6181 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6181 2.6587 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.3326 3.0712 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0470 2.6587 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0470 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9036 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1892 1.8337 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.4747 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.4747 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1892 0.1837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9036 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.2398 1.8337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.9543 1.4212 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.9543 0.5962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.2398 0.1837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1892 -0.6413 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.6687 1.8337 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.6181 0.1837 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.2398 -0.6413 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.7615 3.0712 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.3326 3.8962 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.0643 4.3187 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8857 -1.6665 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.6466 -1.9861 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.1559 -1.3366 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.9250 -1.0374 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.1641 -0.7177 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.6547 -1.3671 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1754 -0.9955 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6257 -1.0652 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.7932 -2.3436 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.1926 -1.9861 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.4064 -1.9500 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.1682 -3.6416 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9290 -3.9612 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4383 -3.3118 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.2074 -3.0125 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4465 -2.6928 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.9372 -3.3422 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.4578 -2.9706 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.0919 -3.0403 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.0756 -4.3187 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.4150 -4.0263 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.6888 -3.9251 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.2161 -1.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2217 -2.2431 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.0398 -1.7902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.4385 -1.0692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2623 -1.0540 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6615 -0.3320 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.4864 -0.3168 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9120 -1.0235 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.5127 -1.7455 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6879 -1.7607 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.7357 -1.0083 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.9378 -2.4513 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.7615 -2.4361 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.8851 0.4042 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.7088 0.4194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 2 0 0 0 0
2 3 1 0 0 0 0
3 4 2 0 0 0 0
4 5 1 0 0 0 0
5 6 2 0 0 0 0
6 1 1 0 0 0 0
2 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 1 0 0 0 0
9 10 2 0 0 0 0
10 11 1 0 0 0 0
11 12 1 0 0 0 0
12 7 2 0 0 0 0
9 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 10 1 0 0 0 0
14 18 1 0 0 0 0
11 17 2 0 0 0 0
12 19 1 0 0 0 0
16 20 1 0 0 0 0
5 21 1 0 0 0 0
4 22 1 0 0 0 0
22 23 1 0 0 0 0
24 25 1 1 0 0 0
25 26 1 1 0 0 0
27 26 1 1 0 0 0
27 28 1 0 0 0 0
28 29 1 0 0 0 0
29 24 1 0 0 0 0
29 30 1 0 0 0 0
30 31 1 0 0 0 0
24 32 1 0 0 0 0
25 33 1 0 0 0 0
26 34 1 0 0 0 0
35 36 1 1 0 0 0
36 37 1 1 0 0 0
38 37 1 1 0 0 0
38 39 1 0 0 0 0
39 40 1 0 0 0 0
40 35 1 0 0 0 0
40 41 1 0 0 0 0
41 42 1 0 0 0 0
35 43 1 0 0 0 0
36 44 1 0 0 0 0
37 45 1 0 0 0 0
38 34 1 0 0 0 0
27 19 1 0 0 0 0
46 47 2 0 0 0 0
46 48 1 0 0 0 0
48 49 2 0 0 0 0
49 50 1 0 0 0 0
50 51 2 0 0 0 0
51 52 1 0 0 0 0
52 53 2 0 0 0 0
53 54 1 0 0 0 0
54 55 2 0 0 0 0
55 50 1 0 0 0 0
53 56 1 0 0 0 0
54 57 1 0 0 0 0
57 58 1 0 0 0 0
52 59 1 0 0 0 0
59 60 1 0 0 0 0
31 46 1 0 0 0 0
S SKP 8
ID FL5FADGS0029
KNApSAcK_ID C00013921
NAME Isorhamnetin 3-(6''-(E)-sinapoylsophoroside);Quercetin 3'-methyl ether 3-(6''-(E)-sinapoylsophoroside)
CAS_RN -
FORMULA C39H42O21
EXACTMASS 846.2218584059999
AVERAGEMASS 846.73818
SMILES O(C)c(c(O)1)cc(C=CC(OCC(C(O)3)OC(OC(C(=O)4)=C(c(c6)cc(OC)c(c6)O)Oc(c5)c(c(cc(O)5)O)4)C(C3O)OC(C(O)2)OC(CO)C(O)C2O)=O)cc(OC)1
M END