Mol:FL5FACGL0014
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 42 46 0 0 0 0 0 0 0 0999 V2000 | + | 42 46 0 0 0 0 0 0 0 0999 V2000 |
| − | -1.8754 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8754 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.8754 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8754 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1609 -1.5431 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1609 -1.5431 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4463 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4463 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4463 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4463 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1609 0.1070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1609 0.1070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2682 -1.5431 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2682 -1.5431 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9827 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9827 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9827 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9827 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2682 0.1070 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2682 0.1070 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2682 -2.1863 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2682 -2.1863 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8824 0.2659 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8824 0.2659 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6107 -0.1546 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6107 -0.1546 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3388 0.2659 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3388 0.2659 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3388 1.1068 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3388 1.1068 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6107 1.5272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6107 1.5272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8824 1.1068 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8824 1.1068 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1609 -2.3678 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1609 -2.3678 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1183 1.5567 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1183 1.5567 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7062 -1.6565 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7062 -1.6565 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.7289 0.1873 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.7289 0.1873 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6107 2.3678 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6107 2.3678 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7593 -1.1145 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7593 -1.1145 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3730 -1.7837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3730 -1.7837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1159 -1.5713 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1159 -1.5713 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8634 -1.7837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8634 -1.7837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.2499 -1.1145 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.2499 -1.1145 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5069 -1.3268 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5069 -1.3268 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.1462 -1.2050 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.1462 -1.2050 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.9379 -0.8188 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.9379 -0.8188 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7756 -1.1945 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7756 -1.1945 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.1756 0.2500 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.1756 0.2500 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.6988 -0.3792 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.6988 -0.3792 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0123 -0.1123 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0123 -0.1123 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.3500 -0.1052 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3500 -0.1052 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.8312 0.3764 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.8312 0.3764 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.4319 0.0594 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.4319 0.0594 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.0454 0.9384 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.0454 0.9384 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.4420 -0.4155 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.4420 -0.4155 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4513 -0.4867 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4513 -0.4867 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5244 -1.6682 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5244 -1.6682 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.4420 -2.1981 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.4420 -2.1981 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 3 18 1 0 0 0 0 | + | 3 18 1 0 0 0 0 |
| − | 19 15 1 0 0 0 0 | + | 19 15 1 0 0 0 0 |
| − | 20 8 1 0 0 0 0 | + | 20 8 1 0 0 0 0 |
| − | 4 3 1 0 0 0 0 | + | 4 3 1 0 0 0 0 |
| − | 1 21 1 0 0 0 0 | + | 1 21 1 0 0 0 0 |
| − | 16 22 1 0 0 0 0 | + | 16 22 1 0 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 25 26 1 1 0 0 0 | + | 25 26 1 1 0 0 0 |
| − | 27 26 1 1 0 0 0 | + | 27 26 1 1 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 23 1 0 0 0 0 | + | 28 23 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 28 30 1 0 0 0 0 | + | 28 30 1 0 0 0 0 |
| − | 27 31 1 0 0 0 0 | + | 27 31 1 0 0 0 0 |
| − | 24 20 1 0 0 0 0 | + | 24 20 1 0 0 0 0 |
| − | 32 33 1 1 0 0 0 | + | 32 33 1 1 0 0 0 |
| − | 33 34 1 1 0 0 0 | + | 33 34 1 1 0 0 0 |
| − | 35 34 1 1 0 0 0 | + | 35 34 1 1 0 0 0 |
| − | 35 36 1 0 0 0 0 | + | 35 36 1 0 0 0 0 |
| − | 36 37 1 0 0 0 0 | + | 36 37 1 0 0 0 0 |
| − | 37 32 1 0 0 0 0 | + | 37 32 1 0 0 0 0 |
| − | 32 38 1 0 0 0 0 | + | 32 38 1 0 0 0 0 |
| − | 33 39 1 0 0 0 0 | + | 33 39 1 0 0 0 0 |
| − | 34 40 1 0 0 0 0 | + | 34 40 1 0 0 0 0 |
| − | 35 21 1 0 0 0 0 | + | 35 21 1 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 26 41 1 0 0 0 0 | + | 26 41 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 41 42 | + | M SAL 1 2 41 42 |
| − | M SBL 1 1 46 | + | M SBL 1 1 46 |
| − | M SMT 1 CH2OH | + | M SMT 1 CH2OH |
| − | M SBV 1 46 -0.6610 -0.1154 | + | M SBV 1 46 -0.6610 -0.1154 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL5FACGL0014 | + | ID FL5FACGL0014 |
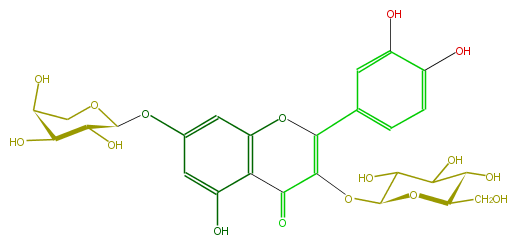
| − | FORMULA C26H28O16 | + | FORMULA C26H28O16 |
| − | EXACTMASS 596.137734848 | + | EXACTMASS 596.137734848 |
| − | AVERAGEMASS 596.49092 | + | AVERAGEMASS 596.49092 |
| − | SMILES O=C(c12)C(OC(C(O)5)OC(C(C(O)5)O)CO)=C(c(c4)ccc(O)c4O)Oc(cc(OC(O3)C(O)C(O)C(O)C3)cc(O)2)1 | + | SMILES O=C(c12)C(OC(C(O)5)OC(C(C(O)5)O)CO)=C(c(c4)ccc(O)c4O)Oc(cc(OC(O3)C(O)C(O)C(O)C3)cc(O)2)1 |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
42 46 0 0 0 0 0 0 0 0999 V2000
-1.8754 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.8754 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1609 -1.5431 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4463 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4463 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1609 0.1070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2682 -1.5431 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9827 -1.1305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9827 -0.3054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2682 0.1070 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.2682 -2.1863 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.8824 0.2659 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6107 -0.1546 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.3388 0.2659 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.3388 1.1068 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6107 1.5272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8824 1.1068 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1609 -2.3678 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.1183 1.5567 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7062 -1.6565 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.7289 0.1873 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.6107 2.3678 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.7593 -1.1145 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3730 -1.7837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1159 -1.5713 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.8634 -1.7837 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.2499 -1.1145 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5069 -1.3268 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.1462 -1.2050 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.9379 -0.8188 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.7756 -1.1945 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.1756 0.2500 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.6988 -0.3792 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.0123 -0.1123 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.3500 -0.1052 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.8312 0.3764 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.4319 0.0594 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.0454 0.9384 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.4420 -0.4155 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.4513 -0.4867 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.5244 -1.6682 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.4420 -2.1981 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
3 18 1 0 0 0 0
19 15 1 0 0 0 0
20 8 1 0 0 0 0
4 3 1 0 0 0 0
1 21 1 0 0 0 0
16 22 1 0 0 0 0
23 24 1 0 0 0 0
24 25 1 1 0 0 0
25 26 1 1 0 0 0
27 26 1 1 0 0 0
27 28 1 0 0 0 0
28 23 1 0 0 0 0
23 29 1 0 0 0 0
28 30 1 0 0 0 0
27 31 1 0 0 0 0
24 20 1 0 0 0 0
32 33 1 1 0 0 0
33 34 1 1 0 0 0
35 34 1 1 0 0 0
35 36 1 0 0 0 0
36 37 1 0 0 0 0
37 32 1 0 0 0 0
32 38 1 0 0 0 0
33 39 1 0 0 0 0
34 40 1 0 0 0 0
35 21 1 0 0 0 0
41 42 1 0 0 0 0
26 41 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 41 42
M SBL 1 1 46
M SMT 1 CH2OH
M SBV 1 46 -0.6610 -0.1154
S SKP 5
ID FL5FACGL0014
FORMULA C26H28O16
EXACTMASS 596.137734848
AVERAGEMASS 596.49092
SMILES O=C(c12)C(OC(C(O)5)OC(C(C(O)5)O)CO)=C(c(c4)ccc(O)c4O)Oc(cc(OC(O3)C(O)C(O)C(O)C3)cc(O)2)1
M END