Mol:FL5FACGA0033
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 45 49 0 0 0 0 0 0 0 0999 V2000 | + | 45 49 0 0 0 0 0 0 0 0999 V2000 |
| − | -4.5526 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.5526 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.5526 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.5526 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9963 -0.3733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9963 -0.3733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4400 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4400 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4400 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4400 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9963 0.9114 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9963 0.9114 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8837 -0.3733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8837 -0.3733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3274 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3274 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3274 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3274 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8837 0.9114 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8837 0.9114 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8837 -0.8741 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8837 -0.8741 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7713 0.9113 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7713 0.9113 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2043 0.5840 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2043 0.5840 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6374 0.9113 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6374 0.9113 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6374 1.5660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6374 1.5660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2043 1.8933 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2043 1.8933 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7713 1.5660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7713 1.5660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6793 -0.6024 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6793 -0.6024 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6339 -0.1110 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6339 -0.1110 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0215 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0215 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2760 -0.5694 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2760 -0.5694 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4739 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4739 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8617 -0.1110 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8617 -0.1110 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1161 -0.3240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1161 -0.3240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3610 -0.3058 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3610 -0.3058 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3850 0.1416 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3850 0.1416 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8617 0.6522 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8617 0.6522 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.0705 1.8932 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.0705 1.8932 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9963 -1.0154 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9963 -1.0154 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.1635 0.7887 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.1635 0.7887 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1029 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1029 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.3255 -1.6166 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.3255 -1.6166 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9030 -1.9260 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9030 -1.9260 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9030 -2.5478 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9030 -2.5478 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3997 -1.5737 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3997 -1.5737 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2043 2.5478 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2043 2.5478 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9496 -1.8912 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9496 -1.8912 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4986 -1.5742 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4986 -1.5742 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0536 -1.8947 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0536 -1.8947 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.6086 -1.5742 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.6086 -1.5742 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.6086 -0.9333 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.6086 -0.9333 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0536 -0.6129 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0536 -0.6129 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4986 -0.9333 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4986 -0.9333 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1635 -1.8946 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1635 -1.8946 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1635 -0.6130 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1635 -0.6130 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 19 20 1 0 0 0 0 | + | 19 20 1 0 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 23 22 1 1 0 0 0 | + | 23 22 1 1 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 19 1 0 0 0 0 | + | 24 19 1 0 0 0 0 |
| − | 19 25 1 0 0 0 0 | + | 19 25 1 0 0 0 0 |
| − | 24 26 1 0 0 0 0 | + | 24 26 1 0 0 0 0 |
| − | 23 27 1 0 0 0 0 | + | 23 27 1 0 0 0 0 |
| − | 20 18 1 0 0 0 0 | + | 20 18 1 0 0 0 0 |
| − | 18 8 1 0 0 0 0 | + | 18 8 1 0 0 0 0 |
| − | 22 21 1 1 0 0 0 | + | 22 21 1 1 0 0 0 |
| − | 15 28 1 0 0 0 0 | + | 15 28 1 0 0 0 0 |
| − | 3 29 1 0 0 0 0 | + | 3 29 1 0 0 0 0 |
| − | 1 30 1 0 0 0 0 | + | 1 30 1 0 0 0 0 |
| − | 22 31 1 0 0 0 0 | + | 22 31 1 0 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 33 34 2 0 0 0 0 | + | 33 34 2 0 0 0 0 |
| − | 33 35 1 0 0 0 0 | + | 33 35 1 0 0 0 0 |
| − | 16 36 1 0 0 0 0 | + | 16 36 1 0 0 0 0 |
| − | 35 37 2 0 0 0 0 | + | 35 37 2 0 0 0 0 |
| − | 37 38 1 0 0 0 0 | + | 37 38 1 0 0 0 0 |
| − | 38 39 2 0 0 0 0 | + | 38 39 2 0 0 0 0 |
| − | 39 40 1 0 0 0 0 | + | 39 40 1 0 0 0 0 |
| − | 40 41 2 0 0 0 0 | + | 40 41 2 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 42 43 2 0 0 0 0 | + | 42 43 2 0 0 0 0 |
| − | 43 38 1 0 0 0 0 | + | 43 38 1 0 0 0 0 |
| − | 40 44 1 0 0 0 0 | + | 40 44 1 0 0 0 0 |
| − | 41 45 1 0 0 0 0 | + | 41 45 1 0 0 0 0 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL5FACGA0033 | + | ID FL5FACGA0033 |
| − | KNApSAcK_ID C00005952 | + | KNApSAcK_ID C00005952 |
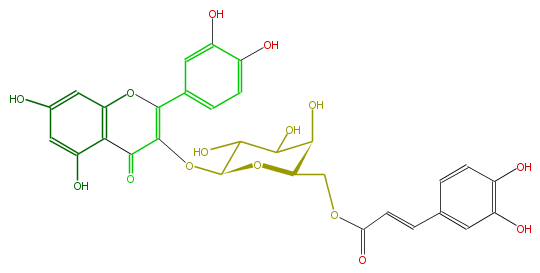
| − | NAME Quercetin 3-(6''-caffeylgalactoside) | + | NAME Quercetin 3-(6''-caffeylgalactoside) |
| − | CAS_RN 84575-22-4 | + | CAS_RN 84575-22-4 |
| − | FORMULA C30H26O15 | + | FORMULA C30H26O15 |
| − | EXACTMASS 626.127170162 | + | EXACTMASS 626.127170162 |
| − | AVERAGEMASS 626.51844 | + | AVERAGEMASS 626.51844 |
| − | SMILES O(C4COC(=O)C=Cc(c5)ccc(O)c5O)C(C(C(C(O)4)O)O)OC(C3=O)=C(Oc(c32)cc(cc2O)O)c(c1)ccc(c(O)1)O | + | SMILES O(C4COC(=O)C=Cc(c5)ccc(O)c5O)C(C(C(C(O)4)O)O)OC(C3=O)=C(Oc(c32)cc(cc2O)O)c(c1)ccc(c(O)1)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
45 49 0 0 0 0 0 0 0 0999 V2000
-4.5526 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.5526 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9963 -0.3733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.4400 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.4400 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9963 0.9114 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8837 -0.3733 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3274 -0.0521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3274 0.5902 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8837 0.9114 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.8837 -0.8741 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.7713 0.9113 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2043 0.5840 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6374 0.9113 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6374 1.5660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2043 1.8933 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.7713 1.5660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6793 -0.6024 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.6339 -0.1110 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0215 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.2760 -0.5694 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.4739 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8617 -0.1110 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.1161 -0.3240 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3610 -0.3058 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.3850 0.1416 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.8617 0.6522 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.0705 1.8932 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.9963 -1.0154 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.1635 0.7887 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.1029 -0.7824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.3255 -1.6166 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.9030 -1.9260 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9030 -2.5478 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3997 -1.5737 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2043 2.5478 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.9496 -1.8912 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4986 -1.5742 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0536 -1.8947 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.6086 -1.5742 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.6086 -0.9333 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0536 -0.6129 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4986 -0.9333 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.1635 -1.8946 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.1635 -0.6130 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
19 20 1 0 0 0 0
20 21 1 1 0 0 0
23 22 1 1 0 0 0
23 24 1 0 0 0 0
24 19 1 0 0 0 0
19 25 1 0 0 0 0
24 26 1 0 0 0 0
23 27 1 0 0 0 0
20 18 1 0 0 0 0
18 8 1 0 0 0 0
22 21 1 1 0 0 0
15 28 1 0 0 0 0
3 29 1 0 0 0 0
1 30 1 0 0 0 0
22 31 1 0 0 0 0
31 32 1 0 0 0 0
32 33 1 0 0 0 0
33 34 2 0 0 0 0
33 35 1 0 0 0 0
16 36 1 0 0 0 0
35 37 2 0 0 0 0
37 38 1 0 0 0 0
38 39 2 0 0 0 0
39 40 1 0 0 0 0
40 41 2 0 0 0 0
41 42 1 0 0 0 0
42 43 2 0 0 0 0
43 38 1 0 0 0 0
40 44 1 0 0 0 0
41 45 1 0 0 0 0
S SKP 8
ID FL5FACGA0033
KNApSAcK_ID C00005952
NAME Quercetin 3-(6''-caffeylgalactoside)
CAS_RN 84575-22-4
FORMULA C30H26O15
EXACTMASS 626.127170162
AVERAGEMASS 626.51844
SMILES O(C4COC(=O)C=Cc(c5)ccc(O)c5O)C(C(C(C(O)4)O)O)OC(C3=O)=C(Oc(c32)cc(cc2O)O)c(c1)ccc(c(O)1)O
M END