Mol:FL5FACGA0012
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 42 46 0 0 0 0 0 0 0 0999 V2000 | + | 42 46 0 0 0 0 0 0 0 0999 V2000 |
| − | -1.3474 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3474 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3474 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3474 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6329 -0.8398 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6329 -0.8398 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0816 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0816 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0816 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0816 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6329 0.8103 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6329 0.8103 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7962 -0.8398 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7962 -0.8398 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5107 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5107 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5107 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5107 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7962 0.8103 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7962 0.8103 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7962 -1.4830 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7962 -1.4830 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4104 0.9692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4104 0.9692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1387 0.5487 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1387 0.5487 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8668 0.9692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8668 0.9692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8668 1.8101 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8668 1.8101 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1387 2.2305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1387 2.2305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4104 1.8101 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4104 1.8101 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6329 -1.6645 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6329 -1.6645 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.6463 2.2600 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.6463 2.2600 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2342 -0.9532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2342 -0.9532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2009 0.8906 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2009 0.8906 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1387 3.0711 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1387 3.0711 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3454 -0.8636 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3454 -0.8636 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7535 -1.3603 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7535 -1.3603 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5243 -1.4149 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5243 -1.4149 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1541 -1.8701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1541 -1.8701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7462 -1.3734 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7462 -1.3734 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.9753 -1.3186 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.9753 -1.3186 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8542 -0.7796 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8542 -0.7796 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.3211 -0.9595 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.3211 -0.9595 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7302 -0.5325 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7302 -0.5325 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7645 0.9712 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7645 0.9712 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.2877 0.3420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.2877 0.3420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.6012 0.6089 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.6012 0.6089 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.9387 0.6161 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.9387 0.6161 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4201 1.0976 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4201 1.0976 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0207 0.7806 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0207 0.7806 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.3443 0.7483 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.3443 0.7483 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.9219 0.3670 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.9219 0.3670 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0002 0.1535 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0002 0.1535 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.3443 -1.8114 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.3443 -1.8114 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.0935 -3.0711 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.0935 -3.0711 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 3 18 1 0 0 0 0 | + | 3 18 1 0 0 0 0 |
| − | 19 15 1 0 0 0 0 | + | 19 15 1 0 0 0 0 |
| − | 20 8 1 0 0 0 0 | + | 20 8 1 0 0 0 0 |
| − | 4 3 1 0 0 0 0 | + | 4 3 1 0 0 0 0 |
| − | 1 21 1 0 0 0 0 | + | 1 21 1 0 0 0 0 |
| − | 16 22 1 0 0 0 0 | + | 16 22 1 0 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 25 26 1 1 0 0 0 | + | 25 26 1 1 0 0 0 |
| − | 27 26 1 1 0 0 0 | + | 27 26 1 1 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 23 1 0 0 0 0 | + | 28 23 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 28 30 1 0 0 0 0 | + | 28 30 1 0 0 0 0 |
| − | 27 31 1 0 0 0 0 | + | 27 31 1 0 0 0 0 |
| − | 24 20 1 0 0 0 0 | + | 24 20 1 0 0 0 0 |
| − | 32 33 1 1 0 0 0 | + | 32 33 1 1 0 0 0 |
| − | 33 34 1 1 0 0 0 | + | 33 34 1 1 0 0 0 |
| − | 35 34 1 1 0 0 0 | + | 35 34 1 1 0 0 0 |
| − | 35 36 1 0 0 0 0 | + | 35 36 1 0 0 0 0 |
| − | 36 37 1 0 0 0 0 | + | 36 37 1 0 0 0 0 |
| − | 37 32 1 0 0 0 0 | + | 37 32 1 0 0 0 0 |
| − | 32 38 1 0 0 0 0 | + | 32 38 1 0 0 0 0 |
| − | 33 39 1 0 0 0 0 | + | 33 39 1 0 0 0 0 |
| − | 34 40 1 0 0 0 0 | + | 34 40 1 0 0 0 0 |
| − | 35 21 1 0 0 0 0 | + | 35 21 1 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 26 41 1 0 0 0 0 | + | 26 41 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 41 42 | + | M SAL 1 2 41 42 |
| − | M SBL 1 1 46 | + | M SBL 1 1 46 |
| − | M SMT 1 CH2OH | + | M SMT 1 CH2OH |
| − | M SBV 1 46 -1.1902 -0.0586 | + | M SBV 1 46 -1.1902 -0.0586 |
| − | S SKP 5 | + | S SKP 5 |
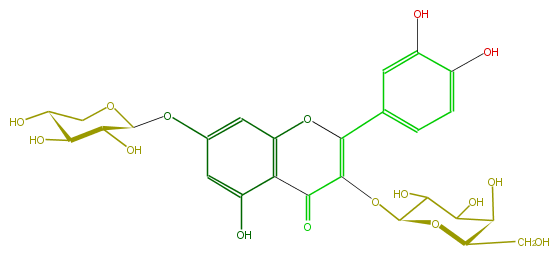
| − | ID FL5FACGA0012 | + | ID FL5FACGA0012 |
| − | FORMULA C26H28O16 | + | FORMULA C26H28O16 |
| − | EXACTMASS 596.137734848 | + | EXACTMASS 596.137734848 |
| − | AVERAGEMASS 596.49092 | + | AVERAGEMASS 596.49092 |
| − | SMILES O=C(c12)C(OC(C(O)5)OC(C(C(O)5)O)CO)=C(c(c4)ccc(O)c4O)Oc(cc(OC(O3)C(O)C(O)C(O)C3)cc(O)2)1 | + | SMILES O=C(c12)C(OC(C(O)5)OC(C(C(O)5)O)CO)=C(c(c4)ccc(O)c4O)Oc(cc(OC(O3)C(O)C(O)C(O)C3)cc(O)2)1 |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
42 46 0 0 0 0 0 0 0 0999 V2000
-1.3474 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3474 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6329 -0.8398 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0816 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0816 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6329 0.8103 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7962 -0.8398 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5107 -0.4272 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5107 0.3979 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7962 0.8103 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.7962 -1.4830 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.4104 0.9692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1387 0.5487 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8668 0.9692 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8668 1.8101 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1387 2.2305 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4104 1.8101 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6329 -1.6645 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.6463 2.2600 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.2342 -0.9532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.2009 0.8906 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.1387 3.0711 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.3454 -0.8636 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.7535 -1.3603 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5243 -1.4149 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.1541 -1.8701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.7462 -1.3734 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.9753 -1.3186 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.8542 -0.7796 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.3211 -0.9595 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.7302 -0.5325 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.7645 0.9712 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.2877 0.3420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.6012 0.6089 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.9387 0.6161 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.4201 1.0976 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.0207 0.7806 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.3443 0.7483 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.9219 0.3670 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.0002 0.1535 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.3443 -1.8114 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.0935 -3.0711 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
3 18 1 0 0 0 0
19 15 1 0 0 0 0
20 8 1 0 0 0 0
4 3 1 0 0 0 0
1 21 1 0 0 0 0
16 22 1 0 0 0 0
23 24 1 0 0 0 0
24 25 1 1 0 0 0
25 26 1 1 0 0 0
27 26 1 1 0 0 0
27 28 1 0 0 0 0
28 23 1 0 0 0 0
23 29 1 0 0 0 0
28 30 1 0 0 0 0
27 31 1 0 0 0 0
24 20 1 0 0 0 0
32 33 1 1 0 0 0
33 34 1 1 0 0 0
35 34 1 1 0 0 0
35 36 1 0 0 0 0
36 37 1 0 0 0 0
37 32 1 0 0 0 0
32 38 1 0 0 0 0
33 39 1 0 0 0 0
34 40 1 0 0 0 0
35 21 1 0 0 0 0
41 42 1 0 0 0 0
26 41 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 41 42
M SBL 1 1 46
M SMT 1 CH2OH
M SBV 1 46 -1.1902 -0.0586
S SKP 5
ID FL5FACGA0012
FORMULA C26H28O16
EXACTMASS 596.137734848
AVERAGEMASS 596.49092
SMILES O=C(c12)C(OC(C(O)5)OC(C(C(O)5)O)CO)=C(c(c4)ccc(O)c4O)Oc(cc(OC(O3)C(O)C(O)C(O)C3)cc(O)2)1
M END