Mol:FL3FAAGS0018
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 40 44 0 0 0 0 0 0 0 0999 V2000 | + | 40 44 0 0 0 0 0 0 0 0999 V2000 |
| − | -0.1829 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1829 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.1829 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1829 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5182 -0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5182 -0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2194 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2194 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2194 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2194 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5182 0.7772 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5182 0.7772 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9206 -0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9206 -0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6217 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6217 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6217 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6217 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9206 0.7772 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9206 0.7772 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9206 -1.4733 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9206 -1.4733 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3227 0.7771 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3227 0.7771 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0372 0.3646 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0372 0.3646 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7518 0.7771 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7518 0.7771 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7518 1.6023 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7518 1.6023 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0372 2.0149 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0372 2.0149 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3227 1.6023 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3227 1.6023 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8839 0.7771 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8839 0.7771 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5182 -1.6514 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5182 -1.6514 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.4662 2.0147 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.4662 2.0147 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0877 0.3236 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0877 0.3236 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.2987 -0.4084 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.2987 -0.4084 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4403 0.1126 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4403 0.1126 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5526 0.2790 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5526 0.2790 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3129 0.8114 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3129 0.8114 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1947 0.3074 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1947 0.3074 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.6187 -0.1220 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.6187 -0.1220 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0042 -0.5328 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0042 -0.5328 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5889 -0.3138 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5889 -0.3138 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.4662 -1.6544 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.4662 -1.6544 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.8762 -1.1593 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.8762 -1.1593 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0872 -1.8913 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0872 -1.8913 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.2287 -1.3703 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.2287 -1.3703 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3411 -1.2039 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3411 -1.2039 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1013 -0.6715 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1013 -0.6715 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9832 -1.1755 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9832 -1.1755 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7882 -2.0149 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7882 -2.0149 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4741 -1.6450 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4741 -1.6450 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0804 0.8187 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0804 0.8187 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1032 0.4632 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1032 0.4632 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 1 18 1 0 0 0 0 | + | 1 18 1 0 0 0 0 |
| − | 3 19 1 0 0 0 0 | + | 3 19 1 0 0 0 0 |
| − | 15 20 1 0 0 0 0 | + | 15 20 1 0 0 0 0 |
| − | 21 22 1 1 0 0 0 | + | 21 22 1 1 0 0 0 |
| − | 22 23 1 1 0 0 0 | + | 22 23 1 1 0 0 0 |
| − | 24 23 1 1 0 0 0 | + | 24 23 1 1 0 0 0 |
| − | 24 25 1 0 0 0 0 | + | 24 25 1 0 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | 26 21 1 0 0 0 0 | + | 26 21 1 0 0 0 0 |
| − | 21 27 1 0 0 0 0 | + | 21 27 1 0 0 0 0 |
| − | 22 28 1 0 0 0 0 | + | 22 28 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 24 18 1 0 0 0 0 | + | 24 18 1 0 0 0 0 |
| − | 31 32 1 1 0 0 0 | + | 31 32 1 1 0 0 0 |
| − | 32 33 1 1 0 0 0 | + | 32 33 1 1 0 0 0 |
| − | 34 33 1 1 0 0 0 | + | 34 33 1 1 0 0 0 |
| − | 34 35 1 0 0 0 0 | + | 34 35 1 0 0 0 0 |
| − | 35 36 1 0 0 0 0 | + | 35 36 1 0 0 0 0 |
| − | 36 31 1 0 0 0 0 | + | 36 31 1 0 0 0 0 |
| − | 32 37 1 0 0 0 0 | + | 32 37 1 0 0 0 0 |
| − | 33 38 1 0 0 0 0 | + | 33 38 1 0 0 0 0 |
| − | 30 31 1 0 0 0 0 | + | 30 31 1 0 0 0 0 |
| − | 34 29 1 0 0 0 0 | + | 34 29 1 0 0 0 0 |
| − | 39 40 1 0 0 0 0 | + | 39 40 1 0 0 0 0 |
| − | 26 39 1 0 0 0 0 | + | 26 39 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 39 40 | + | M SAL 1 2 39 40 |
| − | M SBL 1 1 44 | + | M SBL 1 1 44 |
| − | M SMT 1 ^CH2OH | + | M SMT 1 ^CH2OH |
| − | M SBV 1 44 0.8857 -0.5114 | + | M SBV 1 44 0.8857 -0.5114 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL3FAAGS0018 | + | ID FL3FAAGS0018 |
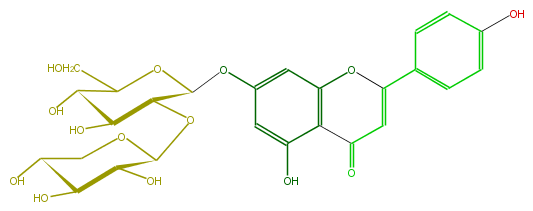
| − | FORMULA C26H28O14 | + | FORMULA C26H28O14 |
| − | EXACTMASS 564.147905604 | + | EXACTMASS 564.147905604 |
| − | AVERAGEMASS 564.49212 | + | AVERAGEMASS 564.49212 |
| − | SMILES O(C1OC(C(Oc(c5)cc(c4c(O)5)OC(=CC4=O)c(c3)ccc(c3)O)2)C(C(O)C(CO)O2)O)CC(C(O)C1O)O | + | SMILES O(C1OC(C(Oc(c5)cc(c4c(O)5)OC(=CC4=O)c(c3)ccc(c3)O)2)C(C(O)C(CO)O2)O)CC(C(O)C1O)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
40 44 0 0 0 0 0 0 0 0999 V2000
-0.1829 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.1829 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.5182 -0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2194 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2194 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.5182 0.7772 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9206 -0.8420 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6217 -0.4372 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6217 0.3724 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9206 0.7772 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.9206 -1.4733 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.3227 0.7771 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0372 0.3646 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.7518 0.7771 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.7518 1.6023 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0372 2.0149 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.3227 1.6023 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8839 0.7771 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.5182 -1.6514 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.4662 2.0147 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.0877 0.3236 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.2987 -0.4084 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.4403 0.1126 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.5526 0.2790 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3129 0.8114 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.1947 0.3074 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.6187 -0.1220 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.0042 -0.5328 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.5889 -0.3138 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.4662 -1.6544 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.8762 -1.1593 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.0872 -1.8913 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.2287 -1.3703 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3411 -1.2039 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.1013 -0.6715 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.9832 -1.1755 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.7882 -2.0149 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.4741 -1.6450 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.0804 0.8187 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.1032 0.4632 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
1 18 1 0 0 0 0
3 19 1 0 0 0 0
15 20 1 0 0 0 0
21 22 1 1 0 0 0
22 23 1 1 0 0 0
24 23 1 1 0 0 0
24 25 1 0 0 0 0
25 26 1 0 0 0 0
26 21 1 0 0 0 0
21 27 1 0 0 0 0
22 28 1 0 0 0 0
23 29 1 0 0 0 0
24 18 1 0 0 0 0
31 32 1 1 0 0 0
32 33 1 1 0 0 0
34 33 1 1 0 0 0
34 35 1 0 0 0 0
35 36 1 0 0 0 0
36 31 1 0 0 0 0
32 37 1 0 0 0 0
33 38 1 0 0 0 0
30 31 1 0 0 0 0
34 29 1 0 0 0 0
39 40 1 0 0 0 0
26 39 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 39 40
M SBL 1 1 44
M SMT 1 ^CH2OH
M SBV 1 44 0.8857 -0.5114
S SKP 5
ID FL3FAAGS0018
FORMULA C26H28O14
EXACTMASS 564.147905604
AVERAGEMASS 564.49212
SMILES O(C1OC(C(Oc(c5)cc(c4c(O)5)OC(=CC4=O)c(c3)ccc(c3)O)2)C(C(O)C(CO)O2)O)CC(C(O)C1O)O
M END