Mol:FL2F1AGSN001
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 50 56 0 0 0 0 0 0 0 0999 V2000 | + | 50 56 0 0 0 0 0 0 0 0999 V2000 |
| − | -3.4082 1.6817 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4082 1.6817 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6956 2.0974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6956 2.0974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4050 0.8567 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4050 0.8567 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6883 0.4474 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6883 0.4474 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9756 0.8631 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9756 0.8631 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9793 1.6881 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9793 1.6881 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2593 0.4537 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2593 0.4537 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5467 0.8694 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5467 0.8694 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5503 1.6944 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5503 1.6944 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2666 2.1037 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2666 2.1037 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1034 2.0752 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1034 2.0752 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8195 1.6655 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8195 1.6655 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5324 2.0807 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5324 2.0807 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5292 2.9057 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5292 2.9057 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8131 3.3155 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8131 3.3155 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1002 2.9002 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1002 2.9002 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2593 -0.2407 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2593 -0.2407 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0337 2.0428 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0337 2.0428 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2365 3.3141 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2365 3.3141 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8737 0.6816 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8737 0.6816 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6899 0.8040 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6899 0.8040 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7874 1.6235 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7874 1.6235 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.2889 2.2789 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.2889 2.2789 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4727 2.1566 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4727 2.1566 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3751 1.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3751 1.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7439 1.1860 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7439 1.1860 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4484 0.6742 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4484 0.6742 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8737 0.0098 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8737 0.0098 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3748 0.2582 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3748 0.2582 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.6414 1.8048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.6414 1.8048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8224 -1.1548 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8224 -1.1548 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0888 -1.6162 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0888 -1.6162 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0337 -0.6917 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0337 -0.6917 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3114 -0.6209 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3114 -0.6209 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.6652 0.1971 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.6652 0.1971 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3096 -1.1585 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3096 -1.1585 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.6596 -0.3176 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.6596 -0.3176 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8050 -0.2974 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8050 -0.2974 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6408 -1.0827 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6408 -1.0827 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9602 -0.6702 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9602 -0.6702 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9602 -0.0123 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9602 -0.0123 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3232 -1.0890 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3232 -1.0890 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.3500 -0.6122 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3500 -0.6122 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0116 -1.1051 0.0000 N 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0116 -1.1051 0.0000 N 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.7472 -1.8867 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.7472 -1.8867 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0777 -1.8767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0777 -1.8767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1511 -2.6060 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1511 -2.6060 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.7300 -3.3155 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.7300 -3.3155 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0950 -3.3056 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0950 -3.3056 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4988 -2.5862 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4988 -2.5862 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 2 0 0 0 0 | + | 1 2 2 0 0 0 0 |
| − | 1 3 1 0 0 0 0 | + | 1 3 1 0 0 0 0 |
| − | 3 4 2 0 0 0 0 | + | 3 4 2 0 0 0 0 |
| − | 4 5 1 0 0 0 0 | + | 4 5 1 0 0 0 0 |
| − | 5 6 2 0 0 0 0 | + | 5 6 2 0 0 0 0 |
| − | 6 2 1 0 0 0 0 | + | 6 2 1 0 0 0 0 |
| − | 5 7 1 0 0 0 0 | + | 5 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 1 0 0 0 0 | + | 8 9 1 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 6 1 0 0 0 0 | + | 10 6 1 0 0 0 0 |
| − | 9 11 1 6 0 0 0 | + | 9 11 1 6 0 0 0 |
| − | 11 12 2 0 0 0 0 | + | 11 12 2 0 0 0 0 |
| − | 12 13 1 0 0 0 0 | + | 12 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 11 1 0 0 0 0 | + | 16 11 1 0 0 0 0 |
| − | 7 17 2 0 0 0 0 | + | 7 17 2 0 0 0 0 |
| − | 1 18 1 0 0 0 0 | + | 1 18 1 0 0 0 0 |
| − | 14 19 1 0 0 0 0 | + | 14 19 1 0 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 21 22 1 1 0 0 0 | + | 21 22 1 1 0 0 0 |
| − | 23 22 1 1 0 0 0 | + | 23 22 1 1 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 25 1 0 0 0 0 | + | 24 25 1 0 0 0 0 |
| − | 25 20 1 0 0 0 0 | + | 25 20 1 0 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | 26 27 1 0 0 0 0 | + | 26 27 1 0 0 0 0 |
| − | 20 28 1 0 0 0 0 | + | 20 28 1 0 0 0 0 |
| − | 21 29 1 0 0 0 0 | + | 21 29 1 0 0 0 0 |
| − | 22 30 1 0 0 0 0 | + | 22 30 1 0 0 0 0 |
| − | 23 19 1 0 0 0 0 | + | 23 19 1 0 0 0 0 |
| − | 37 31 1 1 0 0 0 | + | 37 31 1 1 0 0 0 |
| − | 36 31 1 1 0 0 0 | + | 36 31 1 1 0 0 0 |
| − | 35 37 1 1 0 0 0 | + | 35 37 1 1 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 37 33 1 0 0 0 0 | + | 37 33 1 0 0 0 0 |
| − | 38 35 1 0 0 0 0 | + | 38 35 1 0 0 0 0 |
| − | 34 39 1 0 0 0 0 | + | 34 39 1 0 0 0 0 |
| − | 36 38 1 0 0 0 0 | + | 36 38 1 0 0 0 0 |
| − | 31 34 1 0 0 0 0 | + | 31 34 1 0 0 0 0 |
| − | 30 35 1 0 0 0 0 | + | 30 35 1 0 0 0 0 |
| − | 39 40 1 0 0 0 0 | + | 39 40 1 0 0 0 0 |
| − | 40 41 2 0 0 0 0 | + | 40 41 2 0 0 0 0 |
| − | 40 42 1 0 0 0 0 | + | 40 42 1 0 0 0 0 |
| − | 42 43 2 0 0 0 0 | + | 42 43 2 0 0 0 0 |
| − | 43 44 1 0 0 0 0 | + | 43 44 1 0 0 0 0 |
| − | 44 45 1 0 0 0 0 | + | 44 45 1 0 0 0 0 |
| − | 45 46 2 0 0 0 0 | + | 45 46 2 0 0 0 0 |
| − | 46 42 1 0 0 0 0 | + | 46 42 1 0 0 0 0 |
| − | 45 47 1 0 0 0 0 | + | 45 47 1 0 0 0 0 |
| − | 47 48 2 0 0 0 0 | + | 47 48 2 0 0 0 0 |
| − | 48 49 1 0 0 0 0 | + | 48 49 1 0 0 0 0 |
| − | 49 50 2 0 0 0 0 | + | 49 50 2 0 0 0 0 |
| − | 50 46 1 0 0 0 0 | + | 50 46 1 0 0 0 0 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL2F1AGSN001 | + | ID FL2F1AGSN001 |
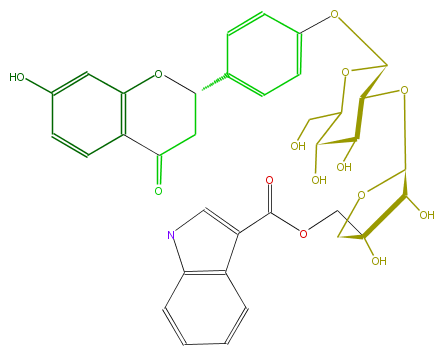
| − | FORMULA C35H35NO14 | + | FORMULA C35H35NO14 |
| − | EXACTMASS 693.205754833 | + | EXACTMASS 693.205754833 |
| − | AVERAGEMASS 693.65074 | + | AVERAGEMASS 693.65074 |
| − | SMILES c(OC(O4)C(OC(O5)C(O)C(COC(=O)c(c76)cnc6cccc7)(C5)O)C(C(C4CO)O)O)(c1)ccc(C(O2)CC(c(c3)c2cc(c3)O)=O)c1 | + | SMILES c(OC(O4)C(OC(O5)C(O)C(COC(=O)c(c76)cnc6cccc7)(C5)O)C(C(C4CO)O)O)(c1)ccc(C(O2)CC(c(c3)c2cc(c3)O)=O)c1 |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
50 56 0 0 0 0 0 0 0 0999 V2000
-3.4082 1.6817 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6956 2.0974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.4050 0.8567 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6883 0.4474 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9756 0.8631 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9793 1.6881 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2593 0.4537 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5467 0.8694 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5503 1.6944 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2666 2.1037 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.1034 2.0752 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8195 1.6655 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5324 2.0807 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5292 2.9057 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8131 3.3155 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.1002 2.9002 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2593 -0.2407 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.0337 2.0428 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.2365 3.3141 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.8737 0.6816 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.6899 0.8040 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.7874 1.6235 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.2889 2.2789 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4727 2.1566 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3751 1.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.7439 1.1860 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4484 0.6742 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.8737 0.0098 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3748 0.2582 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.6414 1.8048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.8224 -1.1548 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0888 -1.6162 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.0337 -0.6917 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3114 -0.6209 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.6652 0.1971 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3096 -1.1585 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.6596 -0.3176 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.8050 -0.2974 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.6408 -1.0827 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.9602 -0.6702 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9602 -0.0123 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.3232 -1.0890 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.3500 -0.6122 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0116 -1.1051 0.0000 N 0 0 0 0 0 0 0 0 0 0 0 0
-0.7472 -1.8867 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0777 -1.8767 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1511 -2.6060 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.7300 -3.3155 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0950 -3.3056 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.4988 -2.5862 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 2 0 0 0 0
1 3 1 0 0 0 0
3 4 2 0 0 0 0
4 5 1 0 0 0 0
5 6 2 0 0 0 0
6 2 1 0 0 0 0
5 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 1 0 0 0 0
9 10 1 0 0 0 0
10 6 1 0 0 0 0
9 11 1 6 0 0 0
11 12 2 0 0 0 0
12 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 11 1 0 0 0 0
7 17 2 0 0 0 0
1 18 1 0 0 0 0
14 19 1 0 0 0 0
20 21 1 1 0 0 0
21 22 1 1 0 0 0
23 22 1 1 0 0 0
23 24 1 0 0 0 0
24 25 1 0 0 0 0
25 20 1 0 0 0 0
25 26 1 0 0 0 0
26 27 1 0 0 0 0
20 28 1 0 0 0 0
21 29 1 0 0 0 0
22 30 1 0 0 0 0
23 19 1 0 0 0 0
37 31 1 1 0 0 0
36 31 1 1 0 0 0
35 37 1 1 0 0 0
31 32 1 0 0 0 0
37 33 1 0 0 0 0
38 35 1 0 0 0 0
34 39 1 0 0 0 0
36 38 1 0 0 0 0
31 34 1 0 0 0 0
30 35 1 0 0 0 0
39 40 1 0 0 0 0
40 41 2 0 0 0 0
40 42 1 0 0 0 0
42 43 2 0 0 0 0
43 44 1 0 0 0 0
44 45 1 0 0 0 0
45 46 2 0 0 0 0
46 42 1 0 0 0 0
45 47 1 0 0 0 0
47 48 2 0 0 0 0
48 49 1 0 0 0 0
49 50 2 0 0 0 0
50 46 1 0 0 0 0
S SKP 5
ID FL2F1AGSN001
FORMULA C35H35NO14
EXACTMASS 693.205754833
AVERAGEMASS 693.65074
SMILES c(OC(O4)C(OC(O5)C(O)C(COC(=O)c(c76)cnc6cccc7)(C5)O)C(C(C4CO)O)O)(c1)ccc(C(O2)CC(c(c3)c2cc(c3)O)=O)c1
M END