Mol:FL1C1ANI0027
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 36 38 0 0 0 0 0 0 0 0999 V2000 | + | 36 38 0 0 0 0 0 0 0 0999 V2000 |
| − | -6.2648 1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.2648 1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.2648 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.2648 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.5503 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.5503 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.8358 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.8358 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.8358 1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.8358 1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.5503 2.0821 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.5503 2.0821 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.9793 2.0821 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.9793 2.0821 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.1214 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.1214 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4069 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4069 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6924 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6924 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6924 -0.3929 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6924 -0.3929 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9780 0.8446 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9780 0.8446 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2635 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2635 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2635 -0.3929 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2635 -0.3929 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9780 -0.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9780 -0.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5490 -0.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5490 -0.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.1655 -0.3929 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1655 -0.3929 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8660 -0.7974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8660 -0.7974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8660 -1.6224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8660 -1.6224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5805 -2.0349 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5805 -2.0349 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2949 -1.6224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2949 -1.6224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2949 -0.7974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2949 -0.7974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5805 -0.3849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5805 -0.3849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2408 -1.9833 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2408 -1.9833 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5805 0.2379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5805 0.2379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9239 -0.4342 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9239 -0.4342 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9239 0.2217 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9239 0.2217 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5548 -0.7984 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5548 -0.7984 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1683 -0.4442 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1683 -0.4442 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.8619 -0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.8619 -0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.8619 -1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.8619 -1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.5763 -2.0821 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.5763 -2.0821 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.2908 -1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.2908 -1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.2908 -0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.2908 -0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.5763 -0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.5763 -0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.9793 -2.0671 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.9793 -2.0671 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 2 0 0 0 0 | + | 1 2 2 0 0 0 0 |
| − | 2 3 1 0 0 0 0 | + | 2 3 1 0 0 0 0 |
| − | 3 4 2 0 0 0 0 | + | 3 4 2 0 0 0 0 |
| − | 4 5 1 0 0 0 0 | + | 4 5 1 0 0 0 0 |
| − | 5 6 2 0 0 0 0 | + | 5 6 2 0 0 0 0 |
| − | 6 1 1 0 0 0 0 | + | 6 1 1 0 0 0 0 |
| − | 1 7 1 0 0 0 0 | + | 1 7 1 0 0 0 0 |
| − | 4 8 1 0 0 0 0 | + | 4 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 11 2 0 0 0 0 | + | 10 11 2 0 0 0 0 |
| − | 10 12 1 0 0 0 0 | + | 10 12 1 0 0 0 0 |
| − | 12 13 1 0 0 0 0 | + | 12 13 1 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 14 16 2 0 0 0 0 | + | 14 16 2 0 0 0 0 |
| − | 16 17 1 0 0 0 0 | + | 16 17 1 0 0 0 0 |
| − | 17 18 1 0 0 0 0 | + | 17 18 1 0 0 0 0 |
| − | 18 19 2 0 0 0 0 | + | 18 19 2 0 0 0 0 |
| − | 19 20 1 0 0 0 0 | + | 19 20 1 0 0 0 0 |
| − | 20 21 2 0 0 0 0 | + | 20 21 2 0 0 0 0 |
| − | 21 22 1 0 0 0 0 | + | 21 22 1 0 0 0 0 |
| − | 22 23 2 0 0 0 0 | + | 22 23 2 0 0 0 0 |
| − | 23 18 1 0 0 0 0 | + | 23 18 1 0 0 0 0 |
| − | 19 24 1 0 0 0 0 | + | 19 24 1 0 0 0 0 |
| − | 23 25 1 0 0 0 0 | + | 23 25 1 0 0 0 0 |
| − | 22 26 1 0 0 0 0 | + | 22 26 1 0 0 0 0 |
| − | 26 27 2 0 0 0 0 | + | 26 27 2 0 0 0 0 |
| − | 26 28 1 0 0 0 0 | + | 26 28 1 0 0 0 0 |
| − | 28 29 2 0 0 0 0 | + | 28 29 2 0 0 0 0 |
| − | 29 30 1 0 0 0 0 | + | 29 30 1 0 0 0 0 |
| − | 30 31 2 0 0 0 0 | + | 30 31 2 0 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 32 33 2 0 0 0 0 | + | 32 33 2 0 0 0 0 |
| − | 33 34 1 0 0 0 0 | + | 33 34 1 0 0 0 0 |
| − | 34 35 2 0 0 0 0 | + | 34 35 2 0 0 0 0 |
| − | 35 30 1 0 0 0 0 | + | 35 30 1 0 0 0 0 |
| − | 33 36 1 0 0 0 0 | + | 33 36 1 0 0 0 0 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL1C1ANI0027 | + | ID FL1C1ANI0027 |
| − | KNApSAcK_ID C00014452 | + | KNApSAcK_ID C00014452 |
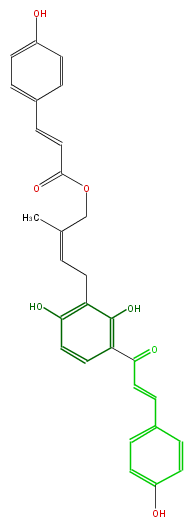
| − | NAME Gemichalcone B;3'-(4-Coumaroyloxy-3-methylbutyl-2(Z)-enyl)-4,2',4'-trihydroxychalcone | + | NAME Gemichalcone B;3'-(4-Coumaroyloxy-3-methylbutyl-2(Z)-enyl)-4,2',4'-trihydroxychalcone |
| − | CAS_RN 189031-26-3 | + | CAS_RN 189031-26-3 |
| − | FORMULA C29H26O7 | + | FORMULA C29H26O7 |
| − | EXACTMASS 486.167853186 | + | EXACTMASS 486.167853186 |
| − | AVERAGEMASS 486.51253999999994 | + | AVERAGEMASS 486.51253999999994 |
| − | SMILES c(c2C(=O)C=Cc(c3)ccc(O)c3)(O)c(c(O)cc2)CC=C(C)COC(=O)C=Cc(c1)ccc(c1)O | + | SMILES c(c2C(=O)C=Cc(c3)ccc(O)c3)(O)c(c(O)cc2)CC=C(C)COC(=O)C=Cc(c1)ccc(c1)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
36 38 0 0 0 0 0 0 0 0999 V2000
-6.2648 1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.2648 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.5503 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.8358 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.8358 1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.5503 2.0821 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.9793 2.0821 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.1214 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.4069 0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6924 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6924 -0.3929 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.9780 0.8446 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.2635 0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2635 -0.3929 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9780 -0.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5490 -0.8054 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.1655 -0.3929 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8660 -0.7974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8660 -1.6224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5805 -2.0349 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.2949 -1.6224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.2949 -0.7974 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5805 -0.3849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2408 -1.9833 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.5805 0.2379 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.9239 -0.4342 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.9239 0.2217 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.5548 -0.7984 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1683 -0.4442 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.8619 -0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.8619 -1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.5763 -2.0821 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.2908 -1.6696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.2908 -0.8446 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.5763 -0.4321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.9793 -2.0671 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 2 0 0 0 0
2 3 1 0 0 0 0
3 4 2 0 0 0 0
4 5 1 0 0 0 0
5 6 2 0 0 0 0
6 1 1 0 0 0 0
1 7 1 0 0 0 0
4 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 11 2 0 0 0 0
10 12 1 0 0 0 0
12 13 1 0 0 0 0
13 14 1 0 0 0 0
14 15 1 0 0 0 0
14 16 2 0 0 0 0
16 17 1 0 0 0 0
17 18 1 0 0 0 0
18 19 2 0 0 0 0
19 20 1 0 0 0 0
20 21 2 0 0 0 0
21 22 1 0 0 0 0
22 23 2 0 0 0 0
23 18 1 0 0 0 0
19 24 1 0 0 0 0
23 25 1 0 0 0 0
22 26 1 0 0 0 0
26 27 2 0 0 0 0
26 28 1 0 0 0 0
28 29 2 0 0 0 0
29 30 1 0 0 0 0
30 31 2 0 0 0 0
31 32 1 0 0 0 0
32 33 2 0 0 0 0
33 34 1 0 0 0 0
34 35 2 0 0 0 0
35 30 1 0 0 0 0
33 36 1 0 0 0 0
S SKP 8
ID FL1C1ANI0027
KNApSAcK_ID C00014452
NAME Gemichalcone B;3'-(4-Coumaroyloxy-3-methylbutyl-2(Z)-enyl)-4,2',4'-trihydroxychalcone
CAS_RN 189031-26-3
FORMULA C29H26O7
EXACTMASS 486.167853186
AVERAGEMASS 486.51253999999994
SMILES c(c2C(=O)C=Cc(c3)ccc(O)c3)(O)c(c(O)cc2)CC=C(C)COC(=O)C=Cc(c1)ccc(c1)O
M END