Mol:FL3FACDS0005
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 43 47 0 0 0 0 0 0 0 0999 V2000 | + | 43 47 0 0 0 0 0 0 0 0999 V2000 |
| − | -3.0339 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0339 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0339 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0339 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3194 -1.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3194 -1.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6050 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6050 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6050 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6050 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3194 -0.0161 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3194 -0.0161 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8905 -1.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8905 -1.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.1761 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1761 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.1761 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1761 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8905 -0.0161 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8905 -0.0161 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8905 -2.3092 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8905 -2.3092 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3194 -2.4907 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3194 -2.4907 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6970 0.1162 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6970 0.1162 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4500 -0.3184 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4500 -0.3184 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2029 0.1162 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2029 0.1162 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.2029 0.9856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2029 0.9856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4500 1.4203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4500 1.4203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6970 0.9856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6970 0.9856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7868 1.5905 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7868 1.5905 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.8595 -1.0931 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.8595 -1.0931 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.1973 -1.8348 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.1973 -1.8348 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.5350 -1.4375 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.5350 -1.4375 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.6344 -1.5434 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.6344 -1.5434 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.2702 -0.9607 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.2702 -0.9607 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.9854 -1.3051 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.9854 -1.3051 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.5168 -1.4727 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.5168 -1.4727 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.8445 -1.8348 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.8445 -1.8348 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.7689 -0.0041 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7689 -0.0041 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.8080 -1.8572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.8080 -1.8572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8456 2.1824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8456 2.1824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4593 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4593 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.2023 1.7256 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.2023 1.7256 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.9496 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.9496 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.3361 2.1824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.3361 2.1824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5931 1.9701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5931 1.9701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1985 2.0090 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1985 2.0090 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1137 2.4907 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1137 2.4907 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.9016 2.0309 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.9016 2.0309 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9552 -0.3181 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9552 -0.3181 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.4388 -0.8091 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.4388 -0.8091 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.1879 -0.0598 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.1879 -0.0598 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.5992 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.5992 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.5168 0.9835 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.5168 0.9835 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 3 12 1 0 0 0 0 | + | 3 12 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 17 1 0 0 0 0 | + | 16 17 1 0 0 0 0 |
| − | 17 18 2 0 0 0 0 | + | 17 18 2 0 0 0 0 |
| − | 18 13 1 0 0 0 0 | + | 18 13 1 0 0 0 0 |
| − | 9 13 1 0 0 0 0 | + | 9 13 1 0 0 0 0 |
| − | 16 19 1 0 0 0 0 | + | 16 19 1 0 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 21 22 1 1 0 0 0 | + | 21 22 1 1 0 0 0 |
| − | 23 22 1 1 0 0 0 | + | 23 22 1 1 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 25 1 0 0 0 0 | + | 24 25 1 0 0 0 0 |
| − | 25 20 1 0 0 0 0 | + | 25 20 1 0 0 0 0 |
| − | 20 26 1 0 0 0 0 | + | 20 26 1 0 0 0 0 |
| − | 21 27 1 0 0 0 0 | + | 21 27 1 0 0 0 0 |
| − | 2 23 1 0 0 0 0 | + | 2 23 1 0 0 0 0 |
| − | 1 28 1 0 0 0 0 | + | 1 28 1 0 0 0 0 |
| − | 22 29 1 0 0 0 0 | + | 22 29 1 0 0 0 0 |
| − | 30 31 1 0 0 0 0 | + | 30 31 1 0 0 0 0 |
| − | 31 32 1 1 0 0 0 | + | 31 32 1 1 0 0 0 |
| − | 32 33 1 1 0 0 0 | + | 32 33 1 1 0 0 0 |
| − | 34 33 1 1 0 0 0 | + | 34 33 1 1 0 0 0 |
| − | 34 35 1 0 0 0 0 | + | 34 35 1 0 0 0 0 |
| − | 35 30 1 0 0 0 0 | + | 35 30 1 0 0 0 0 |
| − | 30 36 1 0 0 0 0 | + | 30 36 1 0 0 0 0 |
| − | 35 37 1 0 0 0 0 | + | 35 37 1 0 0 0 0 |
| − | 34 38 1 0 0 0 0 | + | 34 38 1 0 0 0 0 |
| − | 31 19 1 0 0 0 0 | + | 31 19 1 0 0 0 0 |
| − | 15 39 1 0 0 0 0 | + | 15 39 1 0 0 0 0 |
| − | 40 41 1 0 0 0 0 | + | 40 41 1 0 0 0 0 |
| − | 25 40 1 0 0 0 0 | + | 25 40 1 0 0 0 0 |
| − | 42 43 1 0 0 0 0 | + | 42 43 1 0 0 0 0 |
| − | 33 42 1 0 0 0 0 | + | 33 42 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 40 41 | + | M SAL 1 2 40 41 |
| − | M SBL 1 1 45 | + | M SBL 1 1 45 |
| − | M SMT 1 ^CH2OH | + | M SMT 1 ^CH2OH |
| − | M SBV 1 45 0.4534 -0.4960 | + | M SBV 1 45 0.4534 -0.4960 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 42 43 | + | M SAL 2 2 42 43 |
| − | M SBL 2 1 47 | + | M SBL 2 1 47 |
| − | M SMT 2 CH2OH | + | M SMT 2 CH2OH |
| − | M SBV 2 47 -0.6495 0.0000 | + | M SBV 2 47 -0.6495 0.0000 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL3FACDS0005 | + | ID FL3FACDS0005 |
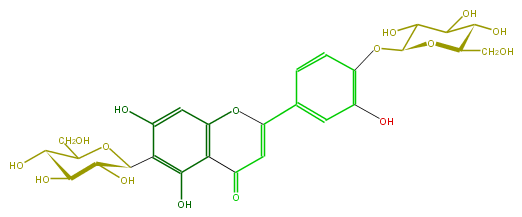
| − | FORMULA C27H30O16 | + | FORMULA C27H30O16 |
| − | EXACTMASS 610.153384912 | + | EXACTMASS 610.153384912 |
| − | AVERAGEMASS 610.5175 | + | AVERAGEMASS 610.5175 |
| − | SMILES OCC(O1)C(O)C(O)C(C(c(c5O)c(O)cc(c25)OC(c(c3)ccc(OC(O4)C(C(C(O)C(CO)4)O)O)c(O)3)=CC2=O)1)O | + | SMILES OCC(O1)C(O)C(O)C(C(c(c5O)c(O)cc(c25)OC(c(c3)ccc(OC(O4)C(C(C(O)C(CO)4)O)O)c(O)3)=CC2=O)1)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
43 47 0 0 0 0 0 0 0 0999 V2000
-3.0339 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.0339 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3194 -1.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6050 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6050 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3194 -0.0161 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8905 -1.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.1761 -1.2535 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.1761 -0.4285 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8905 -0.0161 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.8905 -2.3092 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.3194 -2.4907 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.6970 0.1162 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4500 -0.3184 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.2029 0.1162 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.2029 0.9856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4500 1.4203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6970 0.9856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.7868 1.5905 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.8595 -1.0931 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.1973 -1.8348 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.5350 -1.4375 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.6344 -1.5434 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.2702 -0.9607 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.9854 -1.3051 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.5168 -1.4727 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.8445 -1.8348 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.7689 -0.0041 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.8080 -1.8572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.8456 2.1824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4593 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.2023 1.7256 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.9496 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.3361 2.1824 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.5931 1.9701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1985 2.0090 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.1137 2.4907 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.9016 2.0309 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.9552 -0.3181 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.4388 -0.8091 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.1879 -0.0598 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.5992 1.5133 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.5168 0.9835 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
3 12 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 17 1 0 0 0 0
17 18 2 0 0 0 0
18 13 1 0 0 0 0
9 13 1 0 0 0 0
16 19 1 0 0 0 0
20 21 1 1 0 0 0
21 22 1 1 0 0 0
23 22 1 1 0 0 0
23 24 1 0 0 0 0
24 25 1 0 0 0 0
25 20 1 0 0 0 0
20 26 1 0 0 0 0
21 27 1 0 0 0 0
2 23 1 0 0 0 0
1 28 1 0 0 0 0
22 29 1 0 0 0 0
30 31 1 0 0 0 0
31 32 1 1 0 0 0
32 33 1 1 0 0 0
34 33 1 1 0 0 0
34 35 1 0 0 0 0
35 30 1 0 0 0 0
30 36 1 0 0 0 0
35 37 1 0 0 0 0
34 38 1 0 0 0 0
31 19 1 0 0 0 0
15 39 1 0 0 0 0
40 41 1 0 0 0 0
25 40 1 0 0 0 0
42 43 1 0 0 0 0
33 42 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 40 41
M SBL 1 1 45
M SMT 1 ^CH2OH
M SBV 1 45 0.4534 -0.4960
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 42 43
M SBL 2 1 47
M SMT 2 CH2OH
M SBV 2 47 -0.6495 0.0000
S SKP 5
ID FL3FACDS0005
FORMULA C27H30O16
EXACTMASS 610.153384912
AVERAGEMASS 610.5175
SMILES OCC(O1)C(O)C(O)C(C(c(c5O)c(O)cc(c25)OC(c(c3)ccc(OC(O4)C(C(C(O)C(CO)4)O)O)c(O)3)=CC2=O)1)O
M END