Mol:FL7AAAGL0054
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 83 90 0 0 0 0 0 0 0 0999 V2000 | + | 83 90 0 0 0 0 0 0 0 0999 V2000 |
| − | 2.5260 1.2029 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.5260 1.2029 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3001 1.4847 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3001 1.4847 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4432 2.2961 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4432 2.2961 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8122 2.8256 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8122 2.8256 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0380 2.5439 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.0380 2.5439 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8949 1.7325 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8949 1.7325 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1563 2.5555 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1563 2.5555 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9618 1.3928 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9618 1.3928 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3546 1.9023 0.0000 O 0 3 0 0 0 0 0 0 0 0 0 0 | + | 0.3546 1.9023 0.0000 O 0 3 0 0 0 0 0 0 0 0 0 0 |
| − | -0.3903 1.6313 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3903 1.6313 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5279 0.8507 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5279 0.8507 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0795 0.3413 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0795 0.3413 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8241 0.6123 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8241 0.6123 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9974 2.1407 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9974 2.1407 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7422 1.8696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7422 1.8696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.8799 1.0891 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8799 1.0891 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2726 0.5797 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2726 0.5797 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6146 2.5937 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6146 2.5937 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3523 0.1277 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3523 0.1277 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4950 0.0110 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4950 0.0110 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9452 0.7039 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 2.9452 0.7039 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 2.4055 0.0799 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 2.4055 0.0799 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.2273 0.1532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.2273 0.1532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.9717 -0.2025 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 3.9717 -0.2025 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 4.5114 0.4215 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 4.5114 0.4215 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.6896 0.3483 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 3.6896 0.3483 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 2.4583 0.5735 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4583 0.5735 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.9303 0.7652 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.9303 0.7652 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7702 1.3874 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7702 1.3874 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.9308 -0.4856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.9308 -0.4856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.3619 -0.1444 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.3619 -0.1444 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.1216 0.1321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.1216 0.1321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.5033 -0.4129 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.5033 -0.4129 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.1199 0.0188 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.1199 0.0188 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.6017 -0.6692 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.6017 -0.6692 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.2196 0.6883 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.2196 0.6883 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.2073 0.5141 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.2073 0.5141 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6383 5.0469 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | -0.6383 5.0469 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | -1.4351 4.8333 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -1.4351 4.8333 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.4397 4.0083 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -1.4397 4.0083 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.8640 3.3008 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -1.8640 3.3008 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.0671 3.5143 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0671 3.5143 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0625 4.3392 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | -1.0625 4.3392 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | -0.3493 5.5474 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3493 5.5474 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7658 5.1640 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7658 5.1640 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9830 4.0081 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9830 4.0081 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2712 4.1867 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2712 4.1867 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8382 4.0990 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8382 4.0990 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7569 4.8080 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7569 4.8080 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3616 4.4589 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3616 4.4589 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3580 5.6448 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3580 5.6448 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4907 6.3972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4907 6.3972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7055 6.9876 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7055 6.9876 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.2935 7.4810 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.2935 7.4810 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1603 8.2371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1603 8.2371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4388 8.4993 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4388 8.4993 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8509 8.0060 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8509 8.0060 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.9842 7.2502 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.9842 7.2502 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.6255 8.6274 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.6255 8.6274 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4389 9.0974 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4389 9.0974 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6960 10.1325 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 1.6960 10.1325 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 2.3719 9.6593 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 2.3719 9.6593 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 2.2152 10.4694 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.2152 10.4694 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4931 11.2460 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 2.4931 11.2460 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 1.8174 11.7192 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 1.8174 11.7192 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 1.9740 10.9093 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 1.9740 10.9093 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 1.2779 10.0205 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2779 10.0205 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.3613 10.9092 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.3613 10.9092 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7012 12.1528 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7012 12.1528 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9633 11.6406 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9633 11.6406 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5964 11.6960 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5964 11.6960 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.2355 11.8086 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.2355 11.8086 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.6790 11.2803 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.6790 11.2803 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5215 12.5945 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5215 12.5945 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.1595 13.0412 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.1595 13.0412 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.8108 13.4972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.8108 13.4972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.5045 13.1737 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.5045 13.1737 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.1314 13.6127 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.1314 13.6127 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.0647 14.3751 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.0647 14.3751 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.3712 14.6985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.3712 14.6985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.7441 14.2596 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.7441 14.2596 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.5103 14.6870 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.5103 14.6870 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 7.6057 13.3915 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 7.6057 13.3915 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 2 0 0 0 0 | + | 1 2 2 0 0 0 0 |
| − | 2 3 1 0 0 0 0 | + | 2 3 1 0 0 0 0 |
| − | 3 4 2 0 0 0 0 | + | 3 4 2 0 0 0 0 |
| − | 4 5 1 0 0 0 0 | + | 4 5 1 0 0 0 0 |
| − | 5 6 2 0 0 0 0 | + | 5 6 2 0 0 0 0 |
| − | 6 1 1 0 0 0 0 | + | 6 1 1 0 0 0 0 |
| − | 3 7 1 0 0 0 0 | + | 3 7 1 0 0 0 0 |
| − | 6 8 1 0 0 0 0 | + | 6 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 11 2 0 0 0 0 | + | 10 11 2 0 0 0 0 |
| − | 11 12 1 0 0 0 0 | + | 11 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 8 1 0 0 0 0 | + | 13 8 1 0 0 0 0 |
| − | 10 14 1 0 0 0 0 | + | 10 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 11 1 0 0 0 0 | + | 17 11 1 0 0 0 0 |
| − | 15 18 1 0 0 0 0 | + | 15 18 1 0 0 0 0 |
| − | 17 19 1 0 0 0 0 | + | 17 19 1 0 0 0 0 |
| − | 13 20 1 0 0 0 0 | + | 13 20 1 0 0 0 0 |
| − | 21 22 1 0 0 0 0 | + | 21 22 1 0 0 0 0 |
| − | 22 23 1 1 0 0 0 | + | 22 23 1 1 0 0 0 |
| − | 24 23 1 1 0 0 0 | + | 24 23 1 1 0 0 0 |
| − | 25 24 1 1 0 0 0 | + | 25 24 1 1 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | 26 21 1 0 0 0 0 | + | 26 21 1 0 0 0 0 |
| − | 20 22 1 0 0 0 0 | + | 20 22 1 0 0 0 0 |
| − | 21 27 1 0 0 0 0 | + | 21 27 1 0 0 0 0 |
| − | 26 28 1 0 0 0 0 | + | 26 28 1 0 0 0 0 |
| − | 25 29 1 0 0 0 0 | + | 25 29 1 0 0 0 0 |
| − | 24 30 1 0 0 0 0 | + | 24 30 1 0 0 0 0 |
| − | 30 31 1 0 0 0 0 | + | 30 31 1 0 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 33 34 1 0 0 0 0 | + | 33 34 1 0 0 0 0 |
| − | 34 35 1 0 0 0 0 | + | 34 35 1 0 0 0 0 |
| − | 32 36 2 0 0 0 0 | + | 32 36 2 0 0 0 0 |
| − | 34 37 2 0 0 0 0 | + | 34 37 2 0 0 0 0 |
| − | 38 39 1 1 0 0 0 | + | 38 39 1 1 0 0 0 |
| − | 39 40 1 1 0 0 0 | + | 39 40 1 1 0 0 0 |
| − | 41 40 1 1 0 0 0 | + | 41 40 1 1 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 42 43 1 0 0 0 0 | + | 42 43 1 0 0 0 0 |
| − | 43 38 1 0 0 0 0 | + | 43 38 1 0 0 0 0 |
| − | 18 41 1 0 0 0 0 | + | 18 41 1 0 0 0 0 |
| − | 38 44 1 0 0 0 0 | + | 38 44 1 0 0 0 0 |
| − | 39 45 1 0 0 0 0 | + | 39 45 1 0 0 0 0 |
| − | 40 46 1 0 0 0 0 | + | 40 46 1 0 0 0 0 |
| − | 43 47 1 0 0 0 0 | + | 43 47 1 0 0 0 0 |
| − | 47 48 1 0 0 0 0 | + | 47 48 1 0 0 0 0 |
| − | 48 49 1 0 0 0 0 | + | 48 49 1 0 0 0 0 |
| − | 49 50 2 0 0 0 0 | + | 49 50 2 0 0 0 0 |
| − | 49 51 1 0 0 0 0 | + | 49 51 1 0 0 0 0 |
| − | 51 52 2 0 0 0 0 | + | 51 52 2 0 0 0 0 |
| − | 52 53 1 0 0 0 0 | + | 52 53 1 0 0 0 0 |
| − | 53 54 2 0 0 0 0 | + | 53 54 2 0 0 0 0 |
| − | 54 55 1 0 0 0 0 | + | 54 55 1 0 0 0 0 |
| − | 55 56 2 0 0 0 0 | + | 55 56 2 0 0 0 0 |
| − | 56 57 1 0 0 0 0 | + | 56 57 1 0 0 0 0 |
| − | 57 58 2 0 0 0 0 | + | 57 58 2 0 0 0 0 |
| − | 58 53 1 0 0 0 0 | + | 58 53 1 0 0 0 0 |
| − | 55 59 1 0 0 0 0 | + | 55 59 1 0 0 0 0 |
| − | 56 60 1 0 0 0 0 | + | 56 60 1 0 0 0 0 |
| − | 61 62 1 0 0 0 0 | + | 61 62 1 0 0 0 0 |
| − | 62 63 1 1 0 0 0 | + | 62 63 1 1 0 0 0 |
| − | 64 63 1 1 0 0 0 | + | 64 63 1 1 0 0 0 |
| − | 65 64 1 1 0 0 0 | + | 65 64 1 1 0 0 0 |
| − | 65 66 1 0 0 0 0 | + | 65 66 1 0 0 0 0 |
| − | 66 61 1 0 0 0 0 | + | 66 61 1 0 0 0 0 |
| − | 60 62 1 0 0 0 0 | + | 60 62 1 0 0 0 0 |
| − | 61 67 1 0 0 0 0 | + | 61 67 1 0 0 0 0 |
| − | 66 68 1 0 0 0 0 | + | 66 68 1 0 0 0 0 |
| − | 65 69 1 0 0 0 0 | + | 65 69 1 0 0 0 0 |
| − | 64 70 1 0 0 0 0 | + | 64 70 1 0 0 0 0 |
| − | 70 71 1 0 0 0 0 | + | 70 71 1 0 0 0 0 |
| − | 71 72 1 0 0 0 0 | + | 71 72 1 0 0 0 0 |
| − | 72 73 2 0 0 0 0 | + | 72 73 2 0 0 0 0 |
| − | 72 74 1 0 0 0 0 | + | 72 74 1 0 0 0 0 |
| − | 74 75 2 0 0 0 0 | + | 74 75 2 0 0 0 0 |
| − | 75 76 1 0 0 0 0 | + | 75 76 1 0 0 0 0 |
| − | 76 77 2 0 0 0 0 | + | 76 77 2 0 0 0 0 |
| − | 77 78 1 0 0 0 0 | + | 77 78 1 0 0 0 0 |
| − | 78 79 2 0 0 0 0 | + | 78 79 2 0 0 0 0 |
| − | 79 80 1 0 0 0 0 | + | 79 80 1 0 0 0 0 |
| − | 80 81 2 0 0 0 0 | + | 80 81 2 0 0 0 0 |
| − | 81 76 1 0 0 0 0 | + | 81 76 1 0 0 0 0 |
| − | 79 82 1 0 0 0 0 | + | 79 82 1 0 0 0 0 |
| − | 78 83 1 0 0 0 0 | + | 78 83 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 3 34 37 35 | + | M SAL 1 3 34 37 35 |
| − | M SBL 1 1 37 | + | M SBL 1 1 37 |
| − | M SMT 1 COOH | + | M SMT 1 COOH |
| − | M SVB 1 37 6.5817 0.1284 | + | M SVB 1 37 6.5817 0.1284 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL7AAAGL0054 | + | ID FL7AAAGL0054 |
| − | KNApSAcK_ID C00011185 | + | KNApSAcK_ID C00011185 |
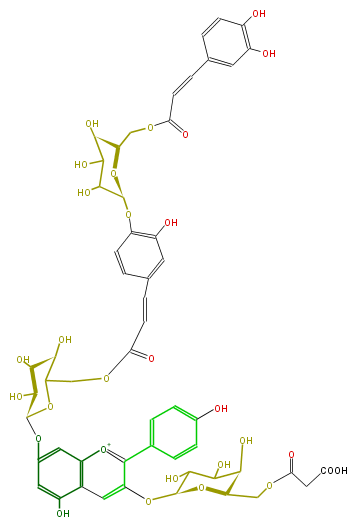
| − | NAME Pelargonidin 3-O-(6-O-malonyl-beta-D-glucopyranoside)-7-O-(6-O-(4-O-(trans-caffeyl)-beta-D-glucopyranosyl)-trans-caffeyl)-beta-D-glucopyranoside) | + | NAME Pelargonidin 3-O-(6-O-malonyl-beta-D-glucopyranoside)-7-O-(6-O-(4-O-(trans-caffeyl)-beta-D-glucopyranosyl)-trans-caffeyl)-beta-D-glucopyranoside) |
| − | CAS_RN 165070-66-6 | + | CAS_RN 165070-66-6 |
| − | FORMULA C54H55O29 | + | FORMULA C54H55O29 |
| − | EXACTMASS 1167.282900798 | + | EXACTMASS 1167.282900798 |
| − | AVERAGEMASS 1167.9971 | + | AVERAGEMASS 1167.9971 |
| − | SMILES C([C@H]1O)(O)C(O)[C@H](Oc(c(c(c8)ccc(O)c8)7)cc(c([o+1]7)2)c(cc(O[C@H](O3)[C@@H](O)[C@H]([C@H](C3COC(=O)C=Cc(c6)ccc(c(O)6)O[C@H](O4)C(O)C(O)[C@@H](O)[C@H]4COC(C=Cc(c5)ccc(O)c5O)=O)O)O)c2)O)O[C@@H]1COC(CC(O)=O)=O | + | SMILES C([C@H]1O)(O)C(O)[C@H](Oc(c(c(c8)ccc(O)c8)7)cc(c([o+1]7)2)c(cc(O[C@H](O3)[C@@H](O)[C@H]([C@H](C3COC(=O)C=Cc(c6)ccc(c(O)6)O[C@H](O4)C(O)C(O)[C@@H](O)[C@H]4COC(C=Cc(c5)ccc(O)c5O)=O)O)O)c2)O)O[C@@H]1COC(CC(O)=O)=O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
83 90 0 0 0 0 0 0 0 0999 V2000
2.5260 1.2029 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.3001 1.4847 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4432 2.2961 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.8122 2.8256 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.0380 2.5439 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8949 1.7325 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1563 2.5555 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.9618 1.3928 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.3546 1.9023 0.0000 O 0 3 0 0 0 0 0 0 0 0 0 0
-0.3903 1.6313 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.5279 0.8507 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0795 0.3413 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8241 0.6123 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.9974 2.1407 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.7422 1.8696 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.8799 1.0891 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2726 0.5797 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6146 2.5937 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.3523 0.1277 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.4950 0.0110 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.9452 0.7039 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
2.4055 0.0799 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.2273 0.1532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.9717 -0.2025 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
4.5114 0.4215 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.6896 0.3483 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
2.4583 0.5735 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.9303 0.7652 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.7702 1.3874 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.9308 -0.4856 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.3619 -0.1444 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
6.1216 0.1321 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.5033 -0.4129 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
7.1199 0.0188 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
7.6017 -0.6692 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
6.2196 0.6883 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
7.2073 0.5141 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.6383 5.0469 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
-1.4351 4.8333 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.4397 4.0083 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.8640 3.3008 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.0671 3.5143 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.0625 4.3392 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
-0.3493 5.5474 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.7658 5.1640 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.9830 4.0081 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.2712 4.1867 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8382 4.0990 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7569 4.8080 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3616 4.4589 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3580 5.6448 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4907 6.3972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.7055 6.9876 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.2935 7.4810 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1603 8.2371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4388 8.4993 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8509 8.0060 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.9842 7.2502 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.6255 8.6274 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.4389 9.0974 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.6960 10.1325 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
2.3719 9.6593 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
2.2152 10.4694 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.4931 11.2460 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
1.8174 11.7192 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
1.9740 10.9093 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
1.2779 10.0205 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.3613 10.9092 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7012 12.1528 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.9633 11.6406 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5964 11.6960 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.2355 11.8086 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.6790 11.2803 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.5215 12.5945 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.1595 13.0412 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.8108 13.4972 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.5045 13.1737 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
7.1314 13.6127 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
7.0647 14.3751 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.3712 14.6985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.7441 14.2596 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
7.5103 14.6870 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
7.6057 13.3915 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 2 0 0 0 0
2 3 1 0 0 0 0
3 4 2 0 0 0 0
4 5 1 0 0 0 0
5 6 2 0 0 0 0
6 1 1 0 0 0 0
3 7 1 0 0 0 0
6 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 11 2 0 0 0 0
11 12 1 0 0 0 0
12 13 2 0 0 0 0
13 8 1 0 0 0 0
10 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 11 1 0 0 0 0
15 18 1 0 0 0 0
17 19 1 0 0 0 0
13 20 1 0 0 0 0
21 22 1 0 0 0 0
22 23 1 1 0 0 0
24 23 1 1 0 0 0
25 24 1 1 0 0 0
25 26 1 0 0 0 0
26 21 1 0 0 0 0
20 22 1 0 0 0 0
21 27 1 0 0 0 0
26 28 1 0 0 0 0
25 29 1 0 0 0 0
24 30 1 0 0 0 0
30 31 1 0 0 0 0
31 32 1 0 0 0 0
32 33 1 0 0 0 0
33 34 1 0 0 0 0
34 35 1 0 0 0 0
32 36 2 0 0 0 0
34 37 2 0 0 0 0
38 39 1 1 0 0 0
39 40 1 1 0 0 0
41 40 1 1 0 0 0
41 42 1 0 0 0 0
42 43 1 0 0 0 0
43 38 1 0 0 0 0
18 41 1 0 0 0 0
38 44 1 0 0 0 0
39 45 1 0 0 0 0
40 46 1 0 0 0 0
43 47 1 0 0 0 0
47 48 1 0 0 0 0
48 49 1 0 0 0 0
49 50 2 0 0 0 0
49 51 1 0 0 0 0
51 52 2 0 0 0 0
52 53 1 0 0 0 0
53 54 2 0 0 0 0
54 55 1 0 0 0 0
55 56 2 0 0 0 0
56 57 1 0 0 0 0
57 58 2 0 0 0 0
58 53 1 0 0 0 0
55 59 1 0 0 0 0
56 60 1 0 0 0 0
61 62 1 0 0 0 0
62 63 1 1 0 0 0
64 63 1 1 0 0 0
65 64 1 1 0 0 0
65 66 1 0 0 0 0
66 61 1 0 0 0 0
60 62 1 0 0 0 0
61 67 1 0 0 0 0
66 68 1 0 0 0 0
65 69 1 0 0 0 0
64 70 1 0 0 0 0
70 71 1 0 0 0 0
71 72 1 0 0 0 0
72 73 2 0 0 0 0
72 74 1 0 0 0 0
74 75 2 0 0 0 0
75 76 1 0 0 0 0
76 77 2 0 0 0 0
77 78 1 0 0 0 0
78 79 2 0 0 0 0
79 80 1 0 0 0 0
80 81 2 0 0 0 0
81 76 1 0 0 0 0
79 82 1 0 0 0 0
78 83 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 3 34 37 35
M SBL 1 1 37
M SMT 1 COOH
M SVB 1 37 6.5817 0.1284
S SKP 8
ID FL7AAAGL0054
KNApSAcK_ID C00011185
NAME Pelargonidin 3-O-(6-O-malonyl-beta-D-glucopyranoside)-7-O-(6-O-(4-O-(trans-caffeyl)-beta-D-glucopyranosyl)-trans-caffeyl)-beta-D-glucopyranoside)
CAS_RN 165070-66-6
FORMULA C54H55O29
EXACTMASS 1167.282900798
AVERAGEMASS 1167.9971
SMILES C([C@H]1O)(O)C(O)[C@H](Oc(c(c(c8)ccc(O)c8)7)cc(c([o+1]7)2)c(cc(O[C@H](O3)[C@@H](O)[C@H]([C@H](C3COC(=O)C=Cc(c6)ccc(c(O)6)O[C@H](O4)C(O)C(O)[C@@H](O)[C@H]4COC(C=Cc(c5)ccc(O)c5O)=O)O)O)c2)O)O[C@@H]1COC(CC(O)=O)=O
M END