Mol:FLIAACCS0005
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 43 47 0 0 0 0 0 0 0 0999 V2000 | + | 43 47 0 0 0 0 0 0 0 0999 V2000 |
| − | -1.0296 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0296 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0296 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0296 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4733 -1.6295 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4733 -1.6295 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0830 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0830 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0830 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0830 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4733 -0.3448 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4733 -0.3448 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6393 -1.6295 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6393 -1.6295 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1956 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1956 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1956 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1956 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6393 -0.3448 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6393 -0.3448 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6393 -2.1303 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6393 -2.1303 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5857 -0.3449 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5857 -0.3449 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2485 2.1334 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | -0.2485 2.1334 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | -0.8541 1.6747 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -0.8541 1.6747 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -0.5971 1.0140 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -0.5971 1.0140 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -0.5903 0.3766 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -0.5903 0.3766 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -0.1269 0.8398 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1269 0.8398 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4320 1.4177 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | -0.4320 1.4177 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | -0.1909 2.7904 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1909 2.7904 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4243 2.1078 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4243 2.1078 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2326 0.6355 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2326 0.6355 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4733 -2.2716 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4733 -2.2716 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.9826 -1.7002 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | -2.9826 -1.7002 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | -2.6115 -2.1901 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -2.6115 -2.1901 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -2.0770 -1.9823 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -2.0770 -1.9823 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.5612 -1.9767 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -1.5612 -1.9767 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.9360 -1.6019 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9360 -1.6019 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4036 -1.8487 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | -2.4036 -1.8487 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | -3.5925 -1.8636 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5925 -1.8636 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1901 -2.2183 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1901 -2.2183 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7707 -2.4964 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7707 -2.4964 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8342 -2.3661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8342 -2.3661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4205 -2.7046 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4205 -2.7046 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0067 -2.3661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0067 -2.3661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0067 -1.6892 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0067 -1.6892 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4205 -1.3508 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4205 -1.3508 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8342 -1.6892 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8342 -1.6892 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5925 -1.3510 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5925 -1.3510 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5925 -2.7044 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5925 -2.7044 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3649 1.4177 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3649 1.4177 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8649 2.2837 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8649 2.2837 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4675 -1.3342 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4675 -1.3342 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6106 -0.5218 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6106 -0.5218 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 1 12 1 0 0 0 0 | + | 1 12 1 0 0 0 0 |
| − | 13 14 1 1 0 0 0 | + | 13 14 1 1 0 0 0 |
| − | 14 15 1 1 0 0 0 | + | 14 15 1 1 0 0 0 |
| − | 16 15 1 1 0 0 0 | + | 16 15 1 1 0 0 0 |
| − | 16 17 1 0 0 0 0 | + | 16 17 1 0 0 0 0 |
| − | 17 18 1 0 0 0 0 | + | 17 18 1 0 0 0 0 |
| − | 18 13 1 0 0 0 0 | + | 18 13 1 0 0 0 0 |
| − | 13 19 1 0 0 0 0 | + | 13 19 1 0 0 0 0 |
| − | 14 20 1 0 0 0 0 | + | 14 20 1 0 0 0 0 |
| − | 15 21 1 0 0 0 0 | + | 15 21 1 0 0 0 0 |
| − | 6 16 1 0 0 0 0 | + | 6 16 1 0 0 0 0 |
| − | 3 22 1 0 0 0 0 | + | 3 22 1 0 0 0 0 |
| − | 23 24 1 1 0 0 0 | + | 23 24 1 1 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 26 25 1 1 0 0 0 | + | 26 25 1 1 0 0 0 |
| − | 26 27 1 0 0 0 0 | + | 26 27 1 0 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 23 1 0 0 0 0 | + | 28 23 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 24 30 1 0 0 0 0 | + | 24 30 1 0 0 0 0 |
| − | 25 31 1 0 0 0 0 | + | 25 31 1 0 0 0 0 |
| − | 26 2 1 0 0 0 0 | + | 26 2 1 0 0 0 0 |
| − | 32 33 2 0 0 0 0 | + | 32 33 2 0 0 0 0 |
| − | 33 34 1 0 0 0 0 | + | 33 34 1 0 0 0 0 |
| − | 34 35 2 0 0 0 0 | + | 34 35 2 0 0 0 0 |
| − | 35 36 1 0 0 0 0 | + | 35 36 1 0 0 0 0 |
| − | 36 37 2 0 0 0 0 | + | 36 37 2 0 0 0 0 |
| − | 37 32 1 0 0 0 0 | + | 37 32 1 0 0 0 0 |
| − | 35 38 1 0 0 0 0 | + | 35 38 1 0 0 0 0 |
| − | 8 37 1 0 0 0 0 | + | 8 37 1 0 0 0 0 |
| − | 34 39 1 0 0 0 0 | + | 34 39 1 0 0 0 0 |
| − | 18 40 1 0 0 0 0 | + | 18 40 1 0 0 0 0 |
| − | 40 41 1 0 0 0 0 | + | 40 41 1 0 0 0 0 |
| − | 28 42 1 0 0 0 0 | + | 28 42 1 0 0 0 0 |
| − | 42 43 1 0 0 0 0 | + | 42 43 1 0 0 0 0 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 42 43 | + | M SAL 2 2 42 43 |
| − | M SBL 2 1 46 | + | M SBL 2 1 46 |
| − | M SMT 2 CH2OH | + | M SMT 2 CH2OH |
| − | M SVB 2 46 -2.751 -1.4639 | + | M SVB 2 46 -2.751 -1.4639 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 40 41 | + | M SAL 1 2 40 41 |
| − | M SBL 1 1 44 | + | M SBL 1 1 44 |
| − | M SMT 1 CH2OH | + | M SMT 1 CH2OH |
| − | M SVB 1 44 0.3649 1.4177 | + | M SVB 1 44 0.3649 1.4177 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FLIAACCS0005 | + | ID FLIAACCS0005 |
| − | KNApSAcK_ID C00006245 | + | KNApSAcK_ID C00006245 |
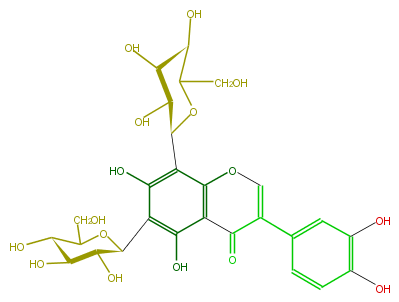
| − | NAME Orobol 6,8-di-C-glucoside | + | NAME Orobol 6,8-di-C-glucoside |
| − | CAS_RN 118949-94-3 | + | CAS_RN 118949-94-3 |
| − | FORMULA C27H30O16 | + | FORMULA C27H30O16 |
| − | EXACTMASS 610.153384912 | + | EXACTMASS 610.153384912 |
| − | AVERAGEMASS 610.5175 | + | AVERAGEMASS 610.5175 |
| − | SMILES C(O)C([C@H](O)1)O[C@@H](c(c(O)3)c(c(c(O5)c(C(C(=C5)c(c4)ccc(O)c(O)4)=O)3)[C@H](O2)[C@H]([C@@H](O)[C@H](C2CO)O)O)O)[C@@H](O)[C@H]1O | + | SMILES C(O)C([C@H](O)1)O[C@@H](c(c(O)3)c(c(c(O5)c(C(C(=C5)c(c4)ccc(O)c(O)4)=O)3)[C@H](O2)[C@H]([C@@H](O)[C@H](C2CO)O)O)O)[C@@H](O)[C@H]1O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
43 47 0 0 0 0 0 0 0 0999 V2000
-1.0296 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0296 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4733 -1.6295 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0830 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0830 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4733 -0.3448 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6393 -1.6295 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1956 -1.3083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1956 -0.6660 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6393 -0.3448 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.6393 -2.1303 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.5857 -0.3449 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.2485 2.1334 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
-0.8541 1.6747 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-0.5971 1.0140 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-0.5903 0.3766 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-0.1269 0.8398 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.4320 1.4177 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
-0.1909 2.7904 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.4243 2.1078 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.2326 0.6355 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.4733 -2.2716 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.9826 -1.7002 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
-2.6115 -2.1901 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-2.0770 -1.9823 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.5612 -1.9767 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.9360 -1.6019 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.4036 -1.8487 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
-3.5925 -1.8636 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.1901 -2.2183 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.7707 -2.4964 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.8342 -2.3661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4205 -2.7046 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0067 -2.3661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0067 -1.6892 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4205 -1.3508 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8342 -1.6892 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5925 -1.3510 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.5925 -2.7044 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.3649 1.4177 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8649 2.2837 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.4675 -1.3342 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.6106 -0.5218 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
1 12 1 0 0 0 0
13 14 1 1 0 0 0
14 15 1 1 0 0 0
16 15 1 1 0 0 0
16 17 1 0 0 0 0
17 18 1 0 0 0 0
18 13 1 0 0 0 0
13 19 1 0 0 0 0
14 20 1 0 0 0 0
15 21 1 0 0 0 0
6 16 1 0 0 0 0
3 22 1 0 0 0 0
23 24 1 1 0 0 0
24 25 1 1 0 0 0
26 25 1 1 0 0 0
26 27 1 0 0 0 0
27 28 1 0 0 0 0
28 23 1 0 0 0 0
23 29 1 0 0 0 0
24 30 1 0 0 0 0
25 31 1 0 0 0 0
26 2 1 0 0 0 0
32 33 2 0 0 0 0
33 34 1 0 0 0 0
34 35 2 0 0 0 0
35 36 1 0 0 0 0
36 37 2 0 0 0 0
37 32 1 0 0 0 0
35 38 1 0 0 0 0
8 37 1 0 0 0 0
34 39 1 0 0 0 0
18 40 1 0 0 0 0
40 41 1 0 0 0 0
28 42 1 0 0 0 0
42 43 1 0 0 0 0
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 42 43
M SBL 2 1 46
M SMT 2 CH2OH
M SVB 2 46 -2.751 -1.4639
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 40 41
M SBL 1 1 44
M SMT 1 CH2OH
M SVB 1 44 0.3649 1.4177
S SKP 8
ID FLIAACCS0005
KNApSAcK_ID C00006245
NAME Orobol 6,8-di-C-glucoside
CAS_RN 118949-94-3
FORMULA C27H30O16
EXACTMASS 610.153384912
AVERAGEMASS 610.5175
SMILES C(O)C([C@H](O)1)O[C@@H](c(c(O)3)c(c(c(O5)c(C(C(=C5)c(c4)ccc(O)c(O)4)=O)3)[C@H](O2)[C@H]([C@@H](O)[C@H](C2CO)O)O)O)[C@@H](O)[C@H]1O
M END