Mol:FLIA2GNS0001
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 26 29 0 0 0 0 0 0 0 0999 V2000 | + | 26 29 0 0 0 0 0 0 0 0999 V2000 |
| − | -2.1566 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1566 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.1566 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1566 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6003 0.0159 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6003 0.0159 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0440 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0440 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0440 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0440 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6003 1.3006 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6003 1.3006 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4877 0.0159 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4877 0.0159 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0686 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0686 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0686 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0686 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4877 1.3006 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4877 1.3006 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6247 0.0160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6247 0.0160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6247 -0.6708 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6247 -0.6708 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2194 -1.0142 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2194 -1.0142 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8142 -0.6708 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8142 -0.6708 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8142 0.0160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8142 0.0160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2194 0.3594 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2194 0.3594 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4877 -0.6262 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4877 -0.6262 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4674 -0.8830 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4674 -0.8830 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8711 -0.3274 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8711 -0.3274 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4674 0.2283 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4674 0.2283 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5139 1.5982 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5139 1.5982 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0140 2.4642 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0140 2.4642 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8021 -1.1857 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8021 -1.1857 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5166 -1.5982 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5166 -1.5982 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8444 0.5512 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8444 0.5512 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2122 0.0210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2122 0.0210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 8 11 1 0 0 0 0 | + | 8 11 1 0 0 0 0 |
| − | 11 12 2 0 0 0 0 | + | 11 12 2 0 0 0 0 |
| − | 12 13 1 0 0 0 0 | + | 12 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 11 1 0 0 0 0 | + | 16 11 1 0 0 0 0 |
| − | 7 17 2 0 0 0 0 | + | 7 17 2 0 0 0 0 |
| − | 14 18 1 0 0 0 0 | + | 14 18 1 0 0 0 0 |
| − | 18 19 1 0 0 0 0 | + | 18 19 1 0 0 0 0 |
| − | 19 20 1 0 0 0 0 | + | 19 20 1 0 0 0 0 |
| − | 20 15 1 0 0 0 0 | + | 20 15 1 0 0 0 0 |
| − | 1 21 1 0 0 0 0 | + | 1 21 1 0 0 0 0 |
| − | 21 22 1 0 0 0 0 | + | 21 22 1 0 0 0 0 |
| − | 13 23 1 0 0 0 0 | + | 13 23 1 0 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 2 25 1 0 0 0 0 | + | 2 25 1 0 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | M STY 1 3 SUP | + | M STY 1 3 SUP |
| − | M SLB 1 3 3 | + | M SLB 1 3 3 |
| − | M SAL 3 2 25 26 | + | M SAL 3 2 25 26 |
| − | M SBL 3 1 28 | + | M SBL 3 1 28 |
| − | M SMT 3 OCH3 | + | M SMT 3 OCH3 |
| − | M SVB 3 28 -2.8711 0.4285 | + | M SVB 3 28 -2.8711 0.4285 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 23 24 | + | M SAL 2 2 23 24 |
| − | M SBL 2 1 26 | + | M SBL 2 1 26 |
| − | M SMT 2 OCH3 | + | M SMT 2 OCH3 |
| − | M SVB 2 26 0.8021 -1.1857 | + | M SVB 2 26 0.8021 -1.1857 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 21 22 | + | M SAL 1 2 21 22 |
| − | M SBL 1 1 24 | + | M SBL 1 1 24 |
| − | M SMT 1 OCH3 | + | M SMT 1 OCH3 |
| − | M SVB 1 24 -2.5139 1.5982 | + | M SVB 1 24 -2.5139 1.5982 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FLIA2GNS0001 | + | ID FLIA2GNS0001 |
| − | KNApSAcK_ID C00009422 | + | KNApSAcK_ID C00009422 |
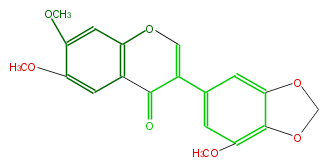
| − | NAME 6,7,3'-Trimethoxy-4',5'-methylenedioxyisoflavone | + | NAME 6,7,3'-Trimethoxy-4',5'-methylenedioxyisoflavone |
| − | CAS_RN 24203-70-1 | + | CAS_RN 24203-70-1 |
| − | FORMULA C19H16O7 | + | FORMULA C19H16O7 |
| − | EXACTMASS 356.089602866 | + | EXACTMASS 356.089602866 |
| − | AVERAGEMASS 356.32614 | + | AVERAGEMASS 356.32614 |
| − | SMILES c(c(OC)4)(OC)cc(c3c4)OC=C(C3=O)c(c2)cc(c(c(OC)2)1)OCO1 | + | SMILES c(c(OC)4)(OC)cc(c3c4)OC=C(C3=O)c(c2)cc(c(c(OC)2)1)OCO1 |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
26 29 0 0 0 0 0 0 0 0999 V2000
-2.1566 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.1566 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6003 0.0159 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0440 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0440 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6003 1.3006 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4877 0.0159 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0686 0.3371 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0686 0.9795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4877 1.3006 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.6247 0.0160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6247 -0.6708 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2194 -1.0142 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8142 -0.6708 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8142 0.0160 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2194 0.3594 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4877 -0.6262 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.4674 -0.8830 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.8711 -0.3274 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4674 0.2283 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.5139 1.5982 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.0140 2.4642 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.8021 -1.1857 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.5166 -1.5982 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8444 0.5512 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.2122 0.0210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
8 11 1 0 0 0 0
11 12 2 0 0 0 0
12 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 11 1 0 0 0 0
7 17 2 0 0 0 0
14 18 1 0 0 0 0
18 19 1 0 0 0 0
19 20 1 0 0 0 0
20 15 1 0 0 0 0
1 21 1 0 0 0 0
21 22 1 0 0 0 0
13 23 1 0 0 0 0
23 24 1 0 0 0 0
2 25 1 0 0 0 0
25 26 1 0 0 0 0
M STY 1 3 SUP
M SLB 1 3 3
M SAL 3 2 25 26
M SBL 3 1 28
M SMT 3 OCH3
M SVB 3 28 -2.8711 0.4285
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 23 24
M SBL 2 1 26
M SMT 2 OCH3
M SVB 2 26 0.8021 -1.1857
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 21 22
M SBL 1 1 24
M SMT 1 OCH3
M SVB 1 24 -2.5139 1.5982
S SKP 8
ID FLIA2GNS0001
KNApSAcK_ID C00009422
NAME 6,7,3'-Trimethoxy-4',5'-methylenedioxyisoflavone
CAS_RN 24203-70-1
FORMULA C19H16O7
EXACTMASS 356.089602866
AVERAGEMASS 356.32614
SMILES c(c(OC)4)(OC)cc(c3c4)OC=C(C3=O)c(c2)cc(c(c(OC)2)1)OCO1
M END