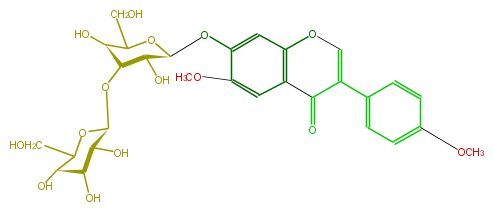
Mol:FLIA2AGS0005
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 44 48 0 0 0 0 0 0 0 0999 V2000 | + | 44 48 0 0 0 0 0 0 0 0999 V2000 |
| − | -0.3559 1.0715 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3559 1.0715 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2004 0.7503 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2004 0.7503 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7567 1.0715 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7567 1.0715 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.3128 0.7504 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.3128 0.7504 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.3128 0.0845 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.3128 0.0845 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8895 -0.2485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8895 -0.2485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4662 0.0845 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4662 0.0845 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.4662 0.7504 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.4662 0.7504 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8895 1.0834 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8895 1.0834 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2006 0.1083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2006 0.1083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7567 -0.2127 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7567 -0.2127 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8895 -0.9140 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8895 -0.9140 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0426 -0.2483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0426 -0.2483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0426 -0.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0426 -0.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5939 -1.2032 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5939 -1.2032 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1453 -0.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1453 -0.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1453 -0.2483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1453 -0.2483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5939 0.0701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5939 0.0701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4598 0.8677 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | -2.4598 0.8677 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | -2.1136 0.4107 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -2.1136 0.4107 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.6150 0.6046 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -1.6150 0.6046 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.0954 0.5989 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -1.0954 0.5989 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -1.4835 0.9595 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4835 0.9595 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9928 0.7766 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | -1.9928 0.7766 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | -2.8468 1.0912 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8468 1.0912 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4404 -0.0196 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4404 -0.0196 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3293 0.1250 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3293 0.1250 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4728 -1.7815 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | -3.4728 -1.7815 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | -2.9002 -1.8100 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -2.9002 -1.8100 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -2.7282 -1.3035 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -2.7282 -1.3035 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -2.3898 -0.9090 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | -2.3898 -0.9090 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | -2.9156 -0.9746 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.9156 -0.9746 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1028 -1.4823 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | -3.1028 -1.4823 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | -3.7887 -2.0975 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7887 -2.0975 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.7806 -2.3368 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.7806 -2.3368 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.1772 -1.3929 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1772 -1.3929 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.8331 -1.2216 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.8331 -1.2216 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.5953 -1.8690 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.5953 -1.8690 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.0113 -1.3849 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.0113 -1.3849 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.8774 -1.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.8774 -1.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2624 1.5037 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2624 1.5037 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6242 2.2736 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6242 2.2736 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5139 0.2004 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5139 0.2004 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5139 -0.6246 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5139 -0.6246 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 7 1 0 0 0 0 | + | 6 7 1 0 0 0 0 |
| − | 7 8 2 0 0 0 0 | + | 7 8 2 0 0 0 0 |
| − | 8 9 1 0 0 0 0 | + | 8 9 1 0 0 0 0 |
| − | 9 4 1 0 0 0 0 | + | 9 4 1 0 0 0 0 |
| − | 2 10 1 0 0 0 0 | + | 2 10 1 0 0 0 0 |
| − | 10 11 2 0 0 0 0 | + | 10 11 2 0 0 0 0 |
| − | 11 5 1 0 0 0 0 | + | 11 5 1 0 0 0 0 |
| − | 6 12 2 0 0 0 0 | + | 6 12 2 0 0 0 0 |
| − | 7 13 1 0 0 0 0 | + | 7 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 17 1 0 0 0 0 | + | 16 17 1 0 0 0 0 |
| − | 17 18 2 0 0 0 0 | + | 17 18 2 0 0 0 0 |
| − | 18 13 1 0 0 0 0 | + | 18 13 1 0 0 0 0 |
| − | 19 20 1 1 0 0 0 | + | 19 20 1 1 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 22 21 1 1 0 0 0 | + | 22 21 1 1 0 0 0 |
| − | 22 23 1 0 0 0 0 | + | 22 23 1 0 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 19 1 0 0 0 0 | + | 24 19 1 0 0 0 0 |
| − | 19 25 1 0 0 0 0 | + | 19 25 1 0 0 0 0 |
| − | 20 26 1 0 0 0 0 | + | 20 26 1 0 0 0 0 |
| − | 21 27 1 0 0 0 0 | + | 21 27 1 0 0 0 0 |
| − | 22 1 1 0 0 0 0 | + | 22 1 1 0 0 0 0 |
| − | 28 29 1 1 0 0 0 | + | 28 29 1 1 0 0 0 |
| − | 29 30 1 1 0 0 0 | + | 29 30 1 1 0 0 0 |
| − | 31 30 1 1 0 0 0 | + | 31 30 1 1 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 33 28 1 0 0 0 0 | + | 33 28 1 0 0 0 0 |
| − | 28 34 1 0 0 0 0 | + | 28 34 1 0 0 0 0 |
| − | 29 35 1 0 0 0 0 | + | 29 35 1 0 0 0 0 |
| − | 30 36 1 0 0 0 0 | + | 30 36 1 0 0 0 0 |
| − | 31 26 1 0 0 0 0 | + | 31 26 1 0 0 0 0 |
| − | 33 37 1 0 0 0 0 | + | 33 37 1 0 0 0 0 |
| − | 37 38 1 0 0 0 0 | + | 37 38 1 0 0 0 0 |
| − | 16 39 1 0 0 0 0 | + | 16 39 1 0 0 0 0 |
| − | 39 40 1 0 0 0 0 | + | 39 40 1 0 0 0 0 |
| − | 24 41 1 0 0 0 0 | + | 24 41 1 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 10 43 1 0 0 0 0 | + | 10 43 1 0 0 0 0 |
| − | 43 44 1 0 0 0 0 | + | 43 44 1 0 0 0 0 |
| − | M STY 1 4 SUP | + | M STY 1 4 SUP |
| − | M SLB 1 4 4 | + | M SLB 1 4 4 |
| − | M SAL 4 2 41 42 | + | M SAL 4 2 41 42 |
| − | M SBL 4 1 45 | + | M SBL 4 1 45 |
| − | M SMT 4 CH2OH | + | M SMT 4 CH2OH |
| − | M SVB 4 45 -2.2624 1.5037 | + | M SVB 4 45 -2.2624 1.5037 |
| − | M STY 1 3 SUP | + | M STY 1 3 SUP |
| − | M SLB 1 3 3 | + | M SLB 1 3 3 |
| − | M SAL 3 2 37 38 | + | M SAL 3 2 37 38 |
| − | M SBL 3 1 41 | + | M SBL 3 1 41 |
| − | M SMT 3 CH2OH | + | M SMT 3 CH2OH |
| − | M SVB 3 41 -4.4693 0.6787 | + | M SVB 3 41 -4.4693 0.6787 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 43 44 | + | M SAL 2 2 43 44 |
| − | M SBL 2 1 47 | + | M SBL 2 1 47 |
| − | M SMT 2 OCH3 | + | M SMT 2 OCH3 |
| − | M SVB 2 47 -0.5139 0.2004 | + | M SVB 2 47 -0.5139 0.2004 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 39 40 | + | M SAL 1 2 39 40 |
| − | M SBL 1 1 43 | + | M SBL 1 1 43 |
| − | M SMT 1 OCH3 | + | M SMT 1 OCH3 |
| − | M SVB 1 43 4.3394 -1.0912 | + | M SVB 1 43 4.3394 -1.0912 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FLIA2AGS0005 | + | ID FLIA2AGS0005 |
| − | KNApSAcK_ID C00010094 | + | KNApSAcK_ID C00010094 |
| − | NAME Afrormosin 7-O-laminaribioside | + | NAME Afrormosin 7-O-laminaribioside |
| − | CAS_RN 68862-17-9 | + | CAS_RN 68862-17-9 |
| − | FORMULA C29H34O15 | + | FORMULA C29H34O15 |
| − | EXACTMASS 622.189770418 | + | EXACTMASS 622.189770418 |
| − | AVERAGEMASS 622.5712599999999 | + | AVERAGEMASS 622.5712599999999 |
| − | SMILES [C@@H]([C@@H]1O)(O[C@@H]([C@H]5O)OC([C@@H]([C@H](O)5)O)CO)[C@H](C(O[C@H]1Oc(c4)c(cc(c34)C(=O)C(=CO3)c(c2)ccc(c2)OC)OC)CO)O | + | SMILES [C@@H]([C@@H]1O)(O[C@@H]([C@H]5O)OC([C@@H]([C@H](O)5)O)CO)[C@H](C(O[C@H]1Oc(c4)c(cc(c34)C(=O)C(=CO3)c(c2)ccc(c2)OC)OC)CO)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
44 48 0 0 0 0 0 0 0 0999 V2000
-0.3559 1.0715 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.2004 0.7503 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7567 1.0715 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.3128 0.7504 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.3128 0.0845 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8895 -0.2485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4662 0.0845 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.4662 0.7504 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8895 1.0834 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.2006 0.1083 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7567 -0.2127 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8895 -0.9140 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0426 -0.2483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0426 -0.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5939 -1.2032 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1453 -0.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1453 -0.2483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5939 0.0701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.4598 0.8677 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
-2.1136 0.4107 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.6150 0.6046 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.0954 0.5989 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-1.4835 0.9595 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.9928 0.7766 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
-2.8468 1.0912 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.4404 -0.0196 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.3293 0.1250 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.4728 -1.7815 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
-2.9002 -1.8100 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-2.7282 -1.3035 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-2.3898 -0.9090 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
-2.9156 -0.9746 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.1028 -1.4823 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
-3.7887 -2.0975 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.7806 -2.3368 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.1772 -1.3929 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.8331 -1.2216 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.5953 -1.8690 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.0113 -1.3849 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.8774 -1.8849 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2624 1.5037 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6242 2.2736 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.5139 0.2004 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.5139 -0.6246 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 7 1 0 0 0 0
7 8 2 0 0 0 0
8 9 1 0 0 0 0
9 4 1 0 0 0 0
2 10 1 0 0 0 0
10 11 2 0 0 0 0
11 5 1 0 0 0 0
6 12 2 0 0 0 0
7 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 17 1 0 0 0 0
17 18 2 0 0 0 0
18 13 1 0 0 0 0
19 20 1 1 0 0 0
20 21 1 1 0 0 0
22 21 1 1 0 0 0
22 23 1 0 0 0 0
23 24 1 0 0 0 0
24 19 1 0 0 0 0
19 25 1 0 0 0 0
20 26 1 0 0 0 0
21 27 1 0 0 0 0
22 1 1 0 0 0 0
28 29 1 1 0 0 0
29 30 1 1 0 0 0
31 30 1 1 0 0 0
31 32 1 0 0 0 0
32 33 1 0 0 0 0
33 28 1 0 0 0 0
28 34 1 0 0 0 0
29 35 1 0 0 0 0
30 36 1 0 0 0 0
31 26 1 0 0 0 0
33 37 1 0 0 0 0
37 38 1 0 0 0 0
16 39 1 0 0 0 0
39 40 1 0 0 0 0
24 41 1 0 0 0 0
41 42 1 0 0 0 0
10 43 1 0 0 0 0
43 44 1 0 0 0 0
M STY 1 4 SUP
M SLB 1 4 4
M SAL 4 2 41 42
M SBL 4 1 45
M SMT 4 CH2OH
M SVB 4 45 -2.2624 1.5037
M STY 1 3 SUP
M SLB 1 3 3
M SAL 3 2 37 38
M SBL 3 1 41
M SMT 3 CH2OH
M SVB 3 41 -4.4693 0.6787
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 43 44
M SBL 2 1 47
M SMT 2 OCH3
M SVB 2 47 -0.5139 0.2004
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 39 40
M SBL 1 1 43
M SMT 1 OCH3
M SVB 1 43 4.3394 -1.0912
S SKP 8
ID FLIA2AGS0005
KNApSAcK_ID C00010094
NAME Afrormosin 7-O-laminaribioside
CAS_RN 68862-17-9
FORMULA C29H34O15
EXACTMASS 622.189770418
AVERAGEMASS 622.5712599999999
SMILES [C@@H]([C@@H]1O)(O[C@@H]([C@H]5O)OC([C@@H]([C@H](O)5)O)CO)[C@H](C(O[C@H]1Oc(c4)c(cc(c34)C(=O)C(=CO3)c(c2)ccc(c2)OC)OC)CO)O
M END