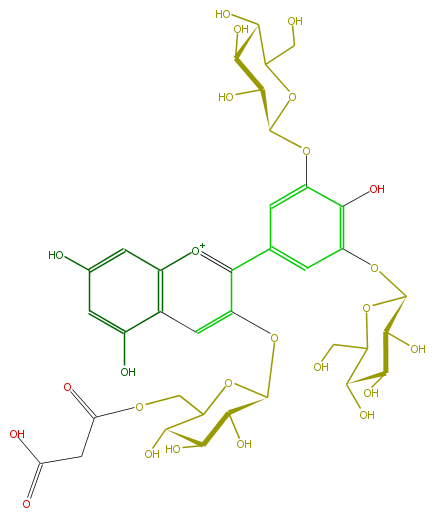
Mol:FL7AAGGL0057
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 61 66 0 0 0 0 0 0 0 0999 V2000 | + | 61 66 0 0 0 0 0 0 0 0999 V2000 |
| − | -2.5047 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5047 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5047 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5047 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7903 -1.4905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7903 -1.4905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0758 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0758 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0758 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0758 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7903 0.1595 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7903 0.1595 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.3613 -1.4905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3613 -1.4905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3531 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3531 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3531 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3531 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.3613 0.1595 0.0000 O 0 3 0 0 0 0 0 0 0 0 0 0 | + | -0.3613 0.1595 0.0000 O 0 3 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1297 0.1953 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1297 0.1953 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8441 -0.2172 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8441 -0.2172 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.5586 0.1953 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.5586 0.1953 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.5586 1.0203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.5586 1.0203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8441 1.4328 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8441 1.4328 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1297 1.0203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1297 1.0203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.1988 1.3899 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.1988 1.3899 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2116 -1.5737 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2116 -1.5737 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0847 0.0818 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0847 0.0818 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.7903 -2.2532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.7903 -2.2532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.8441 2.1640 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.8441 2.1640 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.2236 -0.1886 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.2236 -0.1886 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9828 -3.4224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9828 -3.4224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2230 -3.7444 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2230 -3.7444 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2884 -3.0967 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2884 -3.0967 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.0585 -2.7999 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.0585 -2.7999 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2986 -2.4778 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2986 -2.4778 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2128 -3.1255 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2128 -3.1255 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6909 -2.7524 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6909 -2.7524 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3006 -3.9053 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3006 -3.9053 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.7372 -3.8078 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.7372 -3.8078 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.5369 -3.7108 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.5369 -3.7108 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.6375 -2.5237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6375 -2.5237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4325 -2.3022 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4325 -2.3022 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4290 -1.4770 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4290 -1.4770 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8465 -0.7651 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8465 -0.7651 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0514 -0.9865 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0514 -0.9865 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0549 -1.8118 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0549 -1.8118 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.9851 -3.1121 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.9851 -3.1121 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0698 -2.6722 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0698 -2.6722 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0060 -1.8025 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0060 -1.8025 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3775 -1.7392 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3775 -1.7392 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0744 -2.1547 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.0744 -2.1547 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.7417 -4.8984 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7417 -4.8984 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4690 -4.1210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4690 -4.1210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0060 -3.4961 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0060 -3.4961 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6594 -3.9684 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6594 -3.9684 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3867 -3.1909 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3867 -3.1909 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.9237 -2.5661 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.9237 -2.5661 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4820 -2.9565 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4820 -2.9565 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.8908 4.6751 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.8908 4.6751 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4284 3.9915 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4284 3.9915 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9656 3.3649 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9656 3.3649 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.1084 2.5521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.1084 2.5521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5709 3.2356 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5709 3.2356 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.0338 3.8623 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.0338 3.8623 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2450 4.8984 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2450 4.8984 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.4666 4.6059 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.4666 4.6059 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3150 3.2394 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3150 3.2394 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5970 4.2457 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5970 4.2457 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5589 4.7585 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5589 4.7585 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 2 0 0 0 0 | + | 7 8 2 0 0 0 0 |
| − | 8 9 1 0 0 0 0 | + | 8 9 1 0 0 0 0 |
| − | 9 10 2 0 0 0 0 | + | 9 10 2 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 9 11 1 0 0 0 0 | + | 9 11 1 0 0 0 0 |
| − | 11 12 2 0 0 0 0 | + | 11 12 2 0 0 0 0 |
| − | 12 13 1 0 0 0 0 | + | 12 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 11 1 0 0 0 0 | + | 16 11 1 0 0 0 0 |
| − | 14 17 1 0 0 0 0 | + | 14 17 1 0 0 0 0 |
| − | 8 18 1 0 0 0 0 | + | 8 18 1 0 0 0 0 |
| − | 1 19 1 0 0 0 0 | + | 1 19 1 0 0 0 0 |
| − | 3 20 1 0 0 0 0 | + | 3 20 1 0 0 0 0 |
| − | 15 21 1 0 0 0 0 | + | 15 21 1 0 0 0 0 |
| − | 13 22 1 0 0 0 0 | + | 13 22 1 0 0 0 0 |
| − | 23 24 1 1 0 0 0 | + | 23 24 1 1 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 26 25 1 1 0 0 0 | + | 26 25 1 1 0 0 0 |
| − | 26 27 1 0 0 0 0 | + | 26 27 1 0 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 23 1 0 0 0 0 | + | 28 23 1 0 0 0 0 |
| − | 28 29 1 0 0 0 0 | + | 28 29 1 0 0 0 0 |
| − | 23 30 1 0 0 0 0 | + | 23 30 1 0 0 0 0 |
| − | 24 31 1 0 0 0 0 | + | 24 31 1 0 0 0 0 |
| − | 25 32 1 0 0 0 0 | + | 25 32 1 0 0 0 0 |
| − | 26 18 1 0 0 0 0 | + | 26 18 1 0 0 0 0 |
| − | 33 34 1 1 0 0 0 | + | 33 34 1 1 0 0 0 |
| − | 34 35 1 1 0 0 0 | + | 34 35 1 1 0 0 0 |
| − | 36 35 1 1 0 0 0 | + | 36 35 1 1 0 0 0 |
| − | 36 37 1 0 0 0 0 | + | 36 37 1 0 0 0 0 |
| − | 37 38 1 0 0 0 0 | + | 37 38 1 0 0 0 0 |
| − | 38 33 1 0 0 0 0 | + | 38 33 1 0 0 0 0 |
| − | 33 39 1 0 0 0 0 | + | 33 39 1 0 0 0 0 |
| − | 34 40 1 0 0 0 0 | + | 34 40 1 0 0 0 0 |
| − | 35 41 1 0 0 0 0 | + | 35 41 1 0 0 0 0 |
| − | 36 22 1 0 0 0 0 | + | 36 22 1 0 0 0 0 |
| − | 38 42 1 0 0 0 0 | + | 38 42 1 0 0 0 0 |
| − | 42 43 1 0 0 0 0 | + | 42 43 1 0 0 0 0 |
| − | 44 45 2 0 0 0 0 | + | 44 45 2 0 0 0 0 |
| − | 45 46 1 0 0 0 0 | + | 45 46 1 0 0 0 0 |
| − | 45 47 1 0 0 0 0 | + | 45 47 1 0 0 0 0 |
| − | 47 48 1 0 0 0 0 | + | 47 48 1 0 0 0 0 |
| − | 48 49 2 0 0 0 0 | + | 48 49 2 0 0 0 0 |
| − | 48 50 1 0 0 0 0 | + | 48 50 1 0 0 0 0 |
| − | 50 29 1 0 0 0 0 | + | 50 29 1 0 0 0 0 |
| − | 51 52 1 1 0 0 0 | + | 51 52 1 1 0 0 0 |
| − | 52 53 1 1 0 0 0 | + | 52 53 1 1 0 0 0 |
| − | 54 53 1 1 0 0 0 | + | 54 53 1 1 0 0 0 |
| − | 54 55 1 0 0 0 0 | + | 54 55 1 0 0 0 0 |
| − | 55 56 1 0 0 0 0 | + | 55 56 1 0 0 0 0 |
| − | 56 51 1 0 0 0 0 | + | 56 51 1 0 0 0 0 |
| − | 51 57 1 0 0 0 0 | + | 51 57 1 0 0 0 0 |
| − | 52 58 1 0 0 0 0 | + | 52 58 1 0 0 0 0 |
| − | 53 59 1 0 0 0 0 | + | 53 59 1 0 0 0 0 |
| − | 56 60 1 0 0 0 0 | + | 56 60 1 0 0 0 0 |
| − | 60 61 1 0 0 0 0 | + | 60 61 1 0 0 0 0 |
| − | 21 54 1 0 0 0 0 | + | 21 54 1 0 0 0 0 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL7AAGGL0057 | + | ID FL7AAGGL0057 |
| − | KNApSAcK_ID C00014808 | + | KNApSAcK_ID C00014808 |
| − | NAME Ternatin C5 | + | NAME Ternatin C5 |
| − | CAS_RN 215378-78-2 | + | CAS_RN 215378-78-2 |
| − | FORMULA C36H43O25 | + | FORMULA C36H43O25 |
| − | EXACTMASS 875.209341926 | + | EXACTMASS 875.209341926 |
| − | AVERAGEMASS 875.71162 | + | AVERAGEMASS 875.71162 |
| − | SMILES C(O)(C1O)C(C(CO)OC1Oc(c3)c(O)c(cc3c(c4OC(O6)C(C(O)C(C6COC(=O)CC(O)=O)O)O)[o+1]c(c5)c(c(cc(O)5)O)c4)OC(O2)C(C(O)C(C(CO)2)O)O)O | + | SMILES C(O)(C1O)C(C(CO)OC1Oc(c3)c(O)c(cc3c(c4OC(O6)C(C(O)C(C6COC(=O)CC(O)=O)O)O)[o+1]c(c5)c(c(cc(O)5)O)c4)OC(O2)C(C(O)C(C(CO)2)O)O)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
61 66 0 0 0 0 0 0 0 0999 V2000
-2.5047 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.5047 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.7903 -1.4905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0758 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0758 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.7903 0.1595 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.3613 -1.4905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.3531 -1.0780 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.3531 -0.2530 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.3613 0.1595 0.0000 O 0 3 0 0 0 0 0 0 0 0 0 0
1.1297 0.1953 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8441 -0.2172 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.5586 0.1953 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.5586 1.0203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.8441 1.4328 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1297 1.0203 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.1988 1.3899 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.2116 -1.5737 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.0847 0.0818 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.7903 -2.2532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.8441 2.1640 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.2236 -0.1886 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.9828 -3.4224 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.2230 -3.7444 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2884 -3.0967 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.0585 -2.7999 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2986 -2.4778 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.2128 -3.1255 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6909 -2.7524 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3006 -3.9053 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.7372 -3.8078 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.5369 -3.7108 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.6375 -2.5237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4325 -2.3022 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4290 -1.4770 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8465 -0.7651 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0514 -0.9865 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0549 -1.8118 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.9851 -3.1121 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0698 -2.6722 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.0060 -1.8025 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3775 -1.7392 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.0744 -2.1547 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.7417 -4.8984 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.4690 -4.1210 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.0060 -3.4961 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.6594 -3.9684 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.3867 -3.1909 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.9237 -2.5661 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.4820 -2.9565 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.8908 4.6751 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.4284 3.9915 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9656 3.3649 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.1084 2.5521 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5709 3.2356 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.0338 3.8623 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2450 4.8984 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.4666 4.6059 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.3150 3.2394 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.5970 4.2457 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.5589 4.7585 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 2 0 0 0 0
8 9 1 0 0 0 0
9 10 2 0 0 0 0
10 5 1 0 0 0 0
9 11 1 0 0 0 0
11 12 2 0 0 0 0
12 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 11 1 0 0 0 0
14 17 1 0 0 0 0
8 18 1 0 0 0 0
1 19 1 0 0 0 0
3 20 1 0 0 0 0
15 21 1 0 0 0 0
13 22 1 0 0 0 0
23 24 1 1 0 0 0
24 25 1 1 0 0 0
26 25 1 1 0 0 0
26 27 1 0 0 0 0
27 28 1 0 0 0 0
28 23 1 0 0 0 0
28 29 1 0 0 0 0
23 30 1 0 0 0 0
24 31 1 0 0 0 0
25 32 1 0 0 0 0
26 18 1 0 0 0 0
33 34 1 1 0 0 0
34 35 1 1 0 0 0
36 35 1 1 0 0 0
36 37 1 0 0 0 0
37 38 1 0 0 0 0
38 33 1 0 0 0 0
33 39 1 0 0 0 0
34 40 1 0 0 0 0
35 41 1 0 0 0 0
36 22 1 0 0 0 0
38 42 1 0 0 0 0
42 43 1 0 0 0 0
44 45 2 0 0 0 0
45 46 1 0 0 0 0
45 47 1 0 0 0 0
47 48 1 0 0 0 0
48 49 2 0 0 0 0
48 50 1 0 0 0 0
50 29 1 0 0 0 0
51 52 1 1 0 0 0
52 53 1 1 0 0 0
54 53 1 1 0 0 0
54 55 1 0 0 0 0
55 56 1 0 0 0 0
56 51 1 0 0 0 0
51 57 1 0 0 0 0
52 58 1 0 0 0 0
53 59 1 0 0 0 0
56 60 1 0 0 0 0
60 61 1 0 0 0 0
21 54 1 0 0 0 0
S SKP 8
ID FL7AAGGL0057
KNApSAcK_ID C00014808
NAME Ternatin C5
CAS_RN 215378-78-2
FORMULA C36H43O25
EXACTMASS 875.209341926
AVERAGEMASS 875.71162
SMILES C(O)(C1O)C(C(CO)OC1Oc(c3)c(O)c(cc3c(c4OC(O6)C(C(O)C(C6COC(=O)CC(O)=O)O)O)[o+1]c(c5)c(c(cc(O)5)O)c4)OC(O2)C(C(O)C(C(CO)2)O)O)O
M END