Mol:FL5FACGL0010
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 44 48 0 0 0 0 0 0 0 0999 V2000 | + | 44 48 0 0 0 0 0 0 0 0999 V2000 |
| − | -3.1250 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1250 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1250 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1250 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5687 -1.2014 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5687 -1.2014 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0124 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0124 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0124 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0124 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5687 0.0833 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5687 0.0833 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4561 -1.2014 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4561 -1.2014 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8998 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8998 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8998 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8998 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4561 0.0833 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4561 0.0833 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4561 -1.7022 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4561 -1.7022 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.1993 0.2070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1993 0.2070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3677 -0.1204 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3677 -0.1204 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9347 0.2070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9347 0.2070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9347 0.8617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9347 0.8617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3677 1.1890 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3677 1.1890 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.1993 0.8617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.1993 0.8617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5687 -1.8435 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5687 -1.8435 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5415 1.2120 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.5415 1.2120 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.3365 -1.2897 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3365 -1.2897 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.7895 0.1458 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7895 0.1458 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.3677 1.8435 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.3677 1.8435 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6738 -0.9090 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 0.6738 -0.9090 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 0.3729 -1.4300 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 0.3729 -1.4300 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 0.9514 -1.2647 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9514 -1.2647 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.5334 -1.4300 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 1.5334 -1.4300 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 1.8343 -0.9090 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 1.8343 -0.9090 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 1.2558 -1.0742 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 1.2558 -1.0742 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 0.1151 -1.0587 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.1151 -1.0587 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4939 -0.6617 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4939 -0.6617 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.5515 -1.3231 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.5515 -1.3231 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0499 -0.0629 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | 2.0499 -0.0629 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | 2.6629 -0.3213 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 2.6629 -0.3213 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.0514 0.1628 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 3.0514 0.1628 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.5318 0.4471 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 3.5318 0.4471 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 2.9777 0.5956 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 2.9777 0.5956 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 2.6729 0.1113 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6729 0.1113 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0887 -0.7814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0887 -0.7814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.6166 -0.1534 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.6166 -0.1534 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.7895 0.8934 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.7895 0.8934 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3065 1.5400 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3065 1.5400 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.2888 1.7274 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.2888 1.7274 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3886 -1.9483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3886 -1.9483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3673 -2.9481 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3673 -2.9481 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 3 18 1 0 0 0 0 | + | 3 18 1 0 0 0 0 |
| − | 19 15 1 0 0 0 0 | + | 19 15 1 0 0 0 0 |
| − | 20 8 1 0 0 0 0 | + | 20 8 1 0 0 0 0 |
| − | 4 3 1 0 0 0 0 | + | 4 3 1 0 0 0 0 |
| − | 1 21 1 0 0 0 0 | + | 1 21 1 0 0 0 0 |
| − | 16 22 1 0 0 0 0 | + | 16 22 1 0 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 25 1 1 0 0 0 | + | 24 25 1 1 0 0 0 |
| − | 25 26 1 1 0 0 0 | + | 25 26 1 1 0 0 0 |
| − | 27 26 1 1 0 0 0 | + | 27 26 1 1 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 28 23 1 0 0 0 0 | + | 28 23 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 28 30 1 0 0 0 0 | + | 28 30 1 0 0 0 0 |
| − | 27 31 1 0 0 0 0 | + | 27 31 1 0 0 0 0 |
| − | 24 20 1 0 0 0 0 | + | 24 20 1 0 0 0 0 |
| − | 32 33 1 1 0 0 0 | + | 32 33 1 1 0 0 0 |
| − | 33 34 1 1 0 0 0 | + | 33 34 1 1 0 0 0 |
| − | 35 34 1 1 0 0 0 | + | 35 34 1 1 0 0 0 |
| − | 35 36 1 0 0 0 0 | + | 35 36 1 0 0 0 0 |
| − | 36 37 1 0 0 0 0 | + | 36 37 1 0 0 0 0 |
| − | 37 32 1 0 0 0 0 | + | 37 32 1 0 0 0 0 |
| − | 33 38 1 0 0 0 0 | + | 33 38 1 0 0 0 0 |
| − | 34 39 1 0 0 0 0 | + | 34 39 1 0 0 0 0 |
| − | 30 32 1 0 0 0 0 | + | 30 32 1 0 0 0 0 |
| − | 35 40 1 0 0 0 0 | + | 35 40 1 0 0 0 0 |
| − | 36 41 1 0 0 0 0 | + | 36 41 1 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 26 43 1 0 0 0 0 | + | 26 43 1 0 0 0 0 |
| − | 43 44 1 0 0 0 0 | + | 43 44 1 0 0 0 0 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 43 44 | + | M SAL 2 2 43 44 |
| − | M SBL 2 1 47 | + | M SBL 2 1 47 |
| − | M SMT 2 CH2OH | + | M SMT 2 CH2OH |
| − | M SVB 2 47 1.7428 -1.5874 | + | M SVB 2 47 1.7428 -1.5874 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 41 42 | + | M SAL 1 2 41 42 |
| − | M SBL 1 1 45 | + | M SBL 1 1 45 |
| − | M SMT 1 CH2OH | + | M SMT 1 CH2OH |
| − | M SVB 1 45 3.5053 0.6187 | + | M SVB 1 45 3.5053 0.6187 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL5FACGL0010 | + | ID FL5FACGL0010 |
| − | KNApSAcK_ID C00005410 | + | KNApSAcK_ID C00005410 |
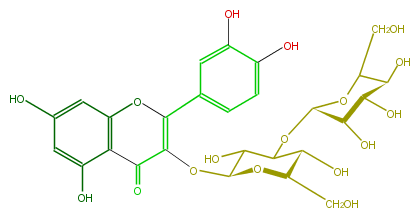
| − | NAME Quercetin 3-laminaribioside | + | NAME Quercetin 3-laminaribioside |
| − | CAS_RN 171828-58-3 | + | CAS_RN 171828-58-3 |
| − | FORMULA C27H30O17 | + | FORMULA C27H30O17 |
| − | EXACTMASS 626.148299534 | + | EXACTMASS 626.148299534 |
| − | AVERAGEMASS 626.5169000000001 | + | AVERAGEMASS 626.5169000000001 |
| − | SMILES O=C(C(O[C@H](O5)C(O)C([C@H]([C@H]5CO)O)O[C@H]([C@H](O)4)OC([C@@H](O)[C@@H](O)4)CO)=1)c(c(O)3)c(cc(O)c3)OC1c(c2)ccc(O)c2O | + | SMILES O=C(C(O[C@H](O5)C(O)C([C@H]([C@H]5CO)O)O[C@H]([C@H](O)4)OC([C@@H](O)[C@@H](O)4)CO)=1)c(c(O)3)c(cc(O)c3)OC1c(c2)ccc(O)c2O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
44 48 0 0 0 0 0 0 0 0999 V2000
-3.1250 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.1250 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.5687 -1.2014 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.0124 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.0124 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.5687 0.0833 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.4561 -1.2014 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8998 -0.8802 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8998 -0.2378 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.4561 0.0833 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.4561 -1.7022 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.1993 0.2070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.3677 -0.1204 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9347 0.2070 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9347 0.8617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.3677 1.1890 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.1993 0.8617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.5687 -1.8435 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.5415 1.2120 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.3365 -1.2897 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.7895 0.1458 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.3677 1.8435 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.6738 -0.9090 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
0.3729 -1.4300 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
0.9514 -1.2647 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.5334 -1.4300 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
1.8343 -0.9090 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
1.2558 -1.0742 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
0.1151 -1.0587 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.4939 -0.6617 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.5515 -1.3231 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.0499 -0.0629 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
2.6629 -0.3213 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.0514 0.1628 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.5318 0.4471 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
2.9777 0.5956 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
2.6729 0.1113 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0887 -0.7814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.6166 -0.1534 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.7895 0.8934 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.3065 1.5400 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.2888 1.7274 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3886 -1.9483 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3673 -2.9481 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
3 18 1 0 0 0 0
19 15 1 0 0 0 0
20 8 1 0 0 0 0
4 3 1 0 0 0 0
1 21 1 0 0 0 0
16 22 1 0 0 0 0
23 24 1 0 0 0 0
24 25 1 1 0 0 0
25 26 1 1 0 0 0
27 26 1 1 0 0 0
27 28 1 0 0 0 0
28 23 1 0 0 0 0
23 29 1 0 0 0 0
28 30 1 0 0 0 0
27 31 1 0 0 0 0
24 20 1 0 0 0 0
32 33 1 1 0 0 0
33 34 1 1 0 0 0
35 34 1 1 0 0 0
35 36 1 0 0 0 0
36 37 1 0 0 0 0
37 32 1 0 0 0 0
33 38 1 0 0 0 0
34 39 1 0 0 0 0
30 32 1 0 0 0 0
35 40 1 0 0 0 0
36 41 1 0 0 0 0
41 42 1 0 0 0 0
26 43 1 0 0 0 0
43 44 1 0 0 0 0
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 43 44
M SBL 2 1 47
M SMT 2 CH2OH
M SVB 2 47 1.7428 -1.5874
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 41 42
M SBL 1 1 45
M SMT 1 CH2OH
M SVB 1 45 3.5053 0.6187
S SKP 8
ID FL5FACGL0010
KNApSAcK_ID C00005410
NAME Quercetin 3-laminaribioside
CAS_RN 171828-58-3
FORMULA C27H30O17
EXACTMASS 626.148299534
AVERAGEMASS 626.5169000000001
SMILES O=C(C(O[C@H](O5)C(O)C([C@H]([C@H]5CO)O)O[C@H]([C@H](O)4)OC([C@@H](O)[C@@H](O)4)CO)=1)c(c(O)3)c(cc(O)c3)OC1c(c2)ccc(O)c2O
M END