Mol:FL5FAAGS0059
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 43 47 0 0 0 0 0 0 0 0999 V2000 | + | 43 47 0 0 0 0 0 0 0 0999 V2000 |
| − | 0.0973 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0973 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0973 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0973 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6536 -1.3672 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6536 -1.3672 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2099 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2099 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2099 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2099 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6536 -0.0825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6536 -0.0825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7662 -1.3672 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7662 -1.3672 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3225 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3225 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3225 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3225 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7662 -0.0825 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7662 -0.0825 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7662 -1.8680 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7662 -1.8680 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8786 -0.0826 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8786 -0.0826 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4456 -0.4099 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4456 -0.4099 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0126 -0.0826 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0126 -0.0826 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0126 0.5721 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0126 0.5721 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4456 0.8994 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4456 0.8994 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.8786 0.5721 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.8786 0.5721 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6536 -2.0093 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6536 -2.0093 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.8063 0.9514 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.8063 0.9514 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.3976 -0.0825 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.3976 -0.0825 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.2610 -1.3978 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.2610 -1.3978 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4126 -0.3241 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4126 -0.3241 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0415 -0.8141 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0415 -0.8141 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5070 -0.6062 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5070 -0.6062 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9912 -0.6007 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9912 -0.6007 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3660 -0.2258 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3660 -0.2258 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.8336 -0.4726 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8336 -0.4726 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.9265 -0.6208 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.9265 -0.6208 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6201 -0.8423 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6201 -0.8423 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2007 -1.1203 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2007 -1.1203 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.1924 0.1489 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1924 0.1489 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.1924 0.6503 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1924 0.6503 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5295 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5295 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.2773 1.4243 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.2773 1.4243 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0363 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0363 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.3313 1.4985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3313 1.4985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9214 1.4985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9214 1.4985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.2164 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.2164 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9214 0.4765 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9214 0.4765 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.3313 0.4765 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3313 0.4765 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.8063 0.9875 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.8063 0.9875 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.2163 2.0093 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.2163 2.0093 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.2163 -0.0344 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.2163 -0.0344 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 3 18 1 0 0 0 0 | + | 3 18 1 0 0 0 0 |
| − | 19 15 1 0 0 0 0 | + | 19 15 1 0 0 0 0 |
| − | 20 1 1 0 0 0 0 | + | 20 1 1 0 0 0 0 |
| − | 21 8 1 0 0 0 0 | + | 21 8 1 0 0 0 0 |
| − | 22 23 1 1 0 0 0 | + | 22 23 1 1 0 0 0 |
| − | 23 24 1 1 0 0 0 | + | 23 24 1 1 0 0 0 |
| − | 25 24 1 1 0 0 0 | + | 25 24 1 1 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | 26 27 1 0 0 0 0 | + | 26 27 1 0 0 0 0 |
| − | 27 22 1 0 0 0 0 | + | 27 22 1 0 0 0 0 |
| − | 22 28 1 0 0 0 0 | + | 22 28 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 24 30 1 0 0 0 0 | + | 24 30 1 0 0 0 0 |
| − | 25 20 1 0 0 0 0 | + | 25 20 1 0 0 0 0 |
| − | 27 31 1 0 0 0 0 | + | 27 31 1 0 0 0 0 |
| − | 31 32 1 0 0 0 0 | + | 31 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 33 34 2 0 0 0 0 | + | 33 34 2 0 0 0 0 |
| − | 33 35 1 0 0 0 0 | + | 33 35 1 0 0 0 0 |
| − | 35 36 2 0 0 0 0 | + | 35 36 2 0 0 0 0 |
| − | 36 37 1 0 0 0 0 | + | 36 37 1 0 0 0 0 |
| − | 37 38 2 0 0 0 0 | + | 37 38 2 0 0 0 0 |
| − | 38 39 1 0 0 0 0 | + | 38 39 1 0 0 0 0 |
| − | 39 40 2 0 0 0 0 | + | 39 40 2 0 0 0 0 |
| − | 40 35 1 0 0 0 0 | + | 40 35 1 0 0 0 0 |
| − | 38 41 1 0 0 0 0 | + | 38 41 1 0 0 0 0 |
| − | 37 42 1 0 0 0 0 | + | 37 42 1 0 0 0 0 |
| − | 39 43 1 0 0 0 0 | + | 39 43 1 0 0 0 0 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL5FAAGS0059 | + | ID FL5FAAGS0059 |
| − | KNApSAcK_ID C00005872 | + | KNApSAcK_ID C00005872 |
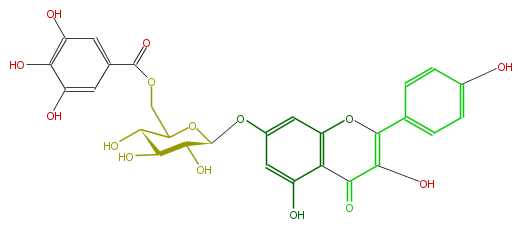
| − | NAME Kaempferol 7-(6''-galloylglucoside) | + | NAME Kaempferol 7-(6''-galloylglucoside) |
| − | CAS_RN 85933-23-9 | + | CAS_RN 85933-23-9 |
| − | FORMULA C28H24O15 | + | FORMULA C28H24O15 |
| − | EXACTMASS 600.111520098 | + | EXACTMASS 600.111520098 |
| − | AVERAGEMASS 600.48116 | + | AVERAGEMASS 600.48116 |
| − | SMILES C(C(O)4)(O)C(C(OC4COC(=O)c(c5)cc(O)c(c(O)5)O)Oc(c1)cc(O)c(C(=O)3)c1OC(=C3O)c(c2)ccc(c2)O)O | + | SMILES C(C(O)4)(O)C(C(OC4COC(=O)c(c5)cc(O)c(c(O)5)O)Oc(c1)cc(O)c(C(=O)3)c1OC(=C3O)c(c2)ccc(c2)O)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
43 47 0 0 0 0 0 0 0 0999 V2000
0.0973 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0973 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6536 -1.3672 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2099 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2099 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6536 -0.0825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.7662 -1.3672 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3225 -1.0460 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3225 -0.4036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.7662 -0.0825 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7662 -1.8680 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.8786 -0.0826 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4456 -0.4099 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0126 -0.0826 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0126 0.5721 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4456 0.8994 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.8786 0.5721 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.6536 -2.0093 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.8063 0.9514 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.3976 -0.0825 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.2610 -1.3978 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.4126 -0.3241 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.0415 -0.8141 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.5070 -0.6062 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.9912 -0.6007 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3660 -0.2258 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.8336 -0.4726 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.9265 -0.6208 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.6201 -0.8423 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.2007 -1.1203 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.1924 0.1489 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.1924 0.6503 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.5295 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.2773 1.4243 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.0363 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.3313 1.4985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9214 1.4985 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.2164 0.9875 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9214 0.4765 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.3313 0.4765 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.8063 0.9875 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.2163 2.0093 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.2163 -0.0344 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
3 18 1 0 0 0 0
19 15 1 0 0 0 0
20 1 1 0 0 0 0
21 8 1 0 0 0 0
22 23 1 1 0 0 0
23 24 1 1 0 0 0
25 24 1 1 0 0 0
25 26 1 0 0 0 0
26 27 1 0 0 0 0
27 22 1 0 0 0 0
22 28 1 0 0 0 0
23 29 1 0 0 0 0
24 30 1 0 0 0 0
25 20 1 0 0 0 0
27 31 1 0 0 0 0
31 32 1 0 0 0 0
32 33 1 0 0 0 0
33 34 2 0 0 0 0
33 35 1 0 0 0 0
35 36 2 0 0 0 0
36 37 1 0 0 0 0
37 38 2 0 0 0 0
38 39 1 0 0 0 0
39 40 2 0 0 0 0
40 35 1 0 0 0 0
38 41 1 0 0 0 0
37 42 1 0 0 0 0
39 43 1 0 0 0 0
S SKP 8
ID FL5FAAGS0059
KNApSAcK_ID C00005872
NAME Kaempferol 7-(6''-galloylglucoside)
CAS_RN 85933-23-9
FORMULA C28H24O15
EXACTMASS 600.111520098
AVERAGEMASS 600.48116
SMILES C(C(O)4)(O)C(C(OC4COC(=O)c(c5)cc(O)c(c(O)5)O)Oc(c1)cc(O)c(C(=O)3)c1OC(=C3O)c(c2)ccc(c2)O)O
M END