Mol:FL3FAIGS0010
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 56 61 0 0 0 0 0 0 0 0999 V2000 | + | 56 61 0 0 0 0 0 0 0 0999 V2000 |
| − | -1.8635 -1.4795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8635 -1.4795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.8634 -2.3485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8634 -2.3485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1660 -2.7513 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1660 -2.7513 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4687 -2.3486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4687 -2.3486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4687 -1.5433 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4687 -1.5433 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1661 -1.1405 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1661 -1.1405 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2290 -2.7513 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2290 -2.7513 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9264 -2.3485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9264 -2.3485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.9264 -1.5433 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.9264 -1.5433 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2290 -1.1405 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2290 -1.1405 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2483 -3.5896 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2483 -3.5896 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6235 -1.1406 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6235 -1.1406 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3343 -1.5511 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3343 -1.5511 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0452 -1.1407 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0452 -1.1407 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0453 -0.3200 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0453 -0.3200 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3343 0.0905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3343 0.0905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6235 -0.3199 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6235 -0.3199 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.1660 -3.5550 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.1660 -3.5550 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5228 -1.1487 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5228 -1.1487 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.8824 2.7748 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.8824 2.7748 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0277 2.5457 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0277 2.5457 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.0227 1.6606 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.0227 1.6606 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5803 0.8943 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5803 0.8943 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4351 1.1232 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4351 1.1232 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.4401 2.0084 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.4401 2.0084 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.8913 3.5896 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.8913 3.5896 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.2689 3.2194 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.2689 3.2194 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.2420 1.2831 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.2420 1.2831 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.7266 0.0821 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.7266 0.0821 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.6056 -1.0284 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.6056 -1.0284 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.0077 -1.8178 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.0077 -1.8178 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.1466 -1.4830 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.1466 -1.4830 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.3157 -1.4741 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.3157 -1.4741 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9195 -0.8701 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9195 -0.8701 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7990 -1.1859 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7990 -1.1859 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.1932 -1.2963 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.1932 -1.2963 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.7394 -1.8048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.7394 -1.8048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.5324 -2.0338 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5324 -2.0338 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.4504 2.7401 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.4504 2.7401 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.1594 2.0311 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.1594 2.0311 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.6630 1.1600 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.6630 1.1600 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.6629 0.1575 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.6629 0.1575 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9539 0.8663 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9539 0.8663 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.4505 1.7376 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.4505 1.7376 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.7272 3.4034 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.7272 3.4034 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.1980 2.8167 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.1980 2.8167 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.0959 2.4877 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.0959 2.4877 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.5645 0.0380 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.5645 0.0380 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.5472 -0.6900 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.5472 -0.6900 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.2569 1.1817 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.2569 1.1817 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.3545 0.8148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.3545 0.8148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.7164 1.9194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.7164 1.9194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.0773 2.2922 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.0773 2.2922 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.1932 2.9364 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.1932 2.9364 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.6986 -1.5134 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.6986 -1.5134 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.0377 -2.2866 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.0377 -2.2866 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 9 12 1 0 0 0 0 | + | 9 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 16 1 0 0 0 0 | + | 15 16 1 0 0 0 0 |
| − | 16 17 2 0 0 0 0 | + | 16 17 2 0 0 0 0 |
| − | 17 12 1 0 0 0 0 | + | 17 12 1 0 0 0 0 |
| − | 3 18 1 0 0 0 0 | + | 3 18 1 0 0 0 0 |
| − | 19 1 1 0 0 0 0 | + | 19 1 1 0 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 21 22 1 1 0 0 0 | + | 21 22 1 1 0 0 0 |
| − | 23 22 1 1 0 0 0 | + | 23 22 1 1 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 25 1 0 0 0 0 | + | 24 25 1 0 0 0 0 |
| − | 25 20 1 0 0 0 0 | + | 25 20 1 0 0 0 0 |
| − | 20 26 1 0 0 0 0 | + | 20 26 1 0 0 0 0 |
| − | 21 27 1 0 0 0 0 | + | 21 27 1 0 0 0 0 |
| − | 22 28 1 0 0 0 0 | + | 22 28 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 29 15 1 0 0 0 0 | + | 29 15 1 0 0 0 0 |
| − | 30 31 1 1 0 0 0 | + | 30 31 1 1 0 0 0 |
| − | 31 32 1 1 0 0 0 | + | 31 32 1 1 0 0 0 |
| − | 33 32 1 1 0 0 0 | + | 33 32 1 1 0 0 0 |
| − | 33 34 1 0 0 0 0 | + | 33 34 1 0 0 0 0 |
| − | 34 35 1 0 0 0 0 | + | 34 35 1 0 0 0 0 |
| − | 35 30 1 0 0 0 0 | + | 35 30 1 0 0 0 0 |
| − | 30 36 1 0 0 0 0 | + | 30 36 1 0 0 0 0 |
| − | 31 37 1 0 0 0 0 | + | 31 37 1 0 0 0 0 |
| − | 32 38 1 0 0 0 0 | + | 32 38 1 0 0 0 0 |
| − | 39 40 1 1 0 0 0 | + | 39 40 1 1 0 0 0 |
| − | 40 41 1 1 0 0 0 | + | 40 41 1 1 0 0 0 |
| − | 42 41 1 1 0 0 0 | + | 42 41 1 1 0 0 0 |
| − | 42 43 1 0 0 0 0 | + | 42 43 1 0 0 0 0 |
| − | 43 44 1 0 0 0 0 | + | 43 44 1 0 0 0 0 |
| − | 44 39 1 0 0 0 0 | + | 44 39 1 0 0 0 0 |
| − | 39 45 1 0 0 0 0 | + | 39 45 1 0 0 0 0 |
| − | 40 46 1 0 0 0 0 | + | 40 46 1 0 0 0 0 |
| − | 44 47 1 0 0 0 0 | + | 44 47 1 0 0 0 0 |
| − | 42 48 1 0 0 0 0 | + | 42 48 1 0 0 0 0 |
| − | 35 49 1 0 0 0 0 | + | 35 49 1 0 0 0 0 |
| − | 49 48 1 0 0 0 0 | + | 49 48 1 0 0 0 0 |
| − | 43 50 1 0 0 0 0 | + | 43 50 1 0 0 0 0 |
| − | 33 19 1 0 0 0 0 | + | 33 19 1 0 0 0 0 |
| − | 51 52 1 0 0 0 0 | + | 51 52 1 0 0 0 0 |
| − | 16 51 1 0 0 0 0 | + | 16 51 1 0 0 0 0 |
| − | 53 54 1 0 0 0 0 | + | 53 54 1 0 0 0 0 |
| − | 25 53 1 0 0 0 0 | + | 25 53 1 0 0 0 0 |
| − | 55 56 1 0 0 0 0 | + | 55 56 1 0 0 0 0 |
| − | 14 55 1 0 0 0 0 | + | 14 55 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 51 52 | + | M SAL 1 2 51 52 |
| − | M SBL 1 1 57 | + | M SBL 1 1 57 |
| − | M SMT 1 OCH3 | + | M SMT 1 OCH3 |
| − | M SBV 1 57 -0.0202 -0.7244 | + | M SBV 1 57 -0.0202 -0.7244 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 53 54 | + | M SAL 2 2 53 54 |
| − | M SBL 2 1 59 | + | M SBL 2 1 59 |
| − | M SMT 2 CH2OH | + | M SMT 2 CH2OH |
| − | M SBV 2 59 -0.6373 -0.2837 | + | M SBV 2 59 -0.6373 -0.2837 |
| − | M STY 1 3 SUP | + | M STY 1 3 SUP |
| − | M SLB 1 3 3 | + | M SLB 1 3 3 |
| − | M SAL 3 2 55 56 | + | M SAL 3 2 55 56 |
| − | M SBL 3 1 61 | + | M SBL 3 1 61 |
| − | M SMT 3 OCH3 | + | M SMT 3 OCH3 |
| − | M SBV 3 61 -0.6534 0.3727 | + | M SBV 3 61 -0.6534 0.3727 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL3FAIGS0010 | + | ID FL3FAIGS0010 |
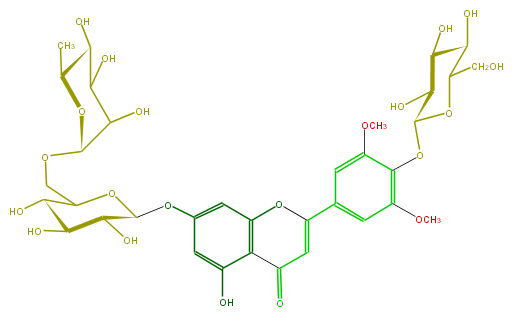
| − | FORMULA C35H44O21 | + | FORMULA C35H44O21 |
| − | EXACTMASS 800.23750847 | + | EXACTMASS 800.23750847 |
| − | AVERAGEMASS 800.71126 | + | AVERAGEMASS 800.71126 |
| − | SMILES O(c(c2)c(c(OC)cc2C(=C6)Oc(c5C(=O)6)cc(cc5O)OC(O3)C(O)C(C(C3COC(O4)C(O)C(O)C(C(C)4)O)O)O)OC(C(O)1)OC(CO)C(C(O)1)O)C | + | SMILES O(c(c2)c(c(OC)cc2C(=C6)Oc(c5C(=O)6)cc(cc5O)OC(O3)C(O)C(C(C3COC(O4)C(O)C(O)C(C(C)4)O)O)O)OC(C(O)1)OC(CO)C(C(O)1)O)C |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
56 61 0 0 0 0 0 0 0 0999 V2000
-1.8635 -1.4795 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.8634 -2.3485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1660 -2.7513 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4687 -2.3486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4687 -1.5433 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1661 -1.1405 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2290 -2.7513 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9264 -2.3485 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.9264 -1.5433 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2290 -1.1405 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.2483 -3.5896 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.6235 -1.1406 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3343 -1.5511 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0452 -1.1407 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0453 -0.3200 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.3343 0.0905 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.6235 -0.3199 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.1660 -3.5550 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.5228 -1.1487 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.8824 2.7748 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0277 2.5457 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.0227 1.6606 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5803 0.8943 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.4351 1.1232 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.4401 2.0084 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.8913 3.5896 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.2689 3.2194 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.2420 1.2831 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.7266 0.0821 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.6056 -1.0284 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.0077 -1.8178 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.1466 -1.4830 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.3157 -1.4741 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9195 -0.8701 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.7990 -1.1859 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.1932 -1.2963 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.7394 -1.8048 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.5324 -2.0338 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.4504 2.7401 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.1594 2.0311 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.6630 1.1600 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.6629 0.1575 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.9539 0.8663 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.4505 1.7376 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.7272 3.4034 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.1980 2.8167 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.0959 2.4877 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.5645 0.0380 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-5.5472 -0.6900 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.2569 1.1817 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.3545 0.8148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.7164 1.9194 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.0773 2.2922 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.1932 2.9364 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.6986 -1.5134 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.0377 -2.2866 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
9 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 16 1 0 0 0 0
16 17 2 0 0 0 0
17 12 1 0 0 0 0
3 18 1 0 0 0 0
19 1 1 0 0 0 0
20 21 1 1 0 0 0
21 22 1 1 0 0 0
23 22 1 1 0 0 0
23 24 1 0 0 0 0
24 25 1 0 0 0 0
25 20 1 0 0 0 0
20 26 1 0 0 0 0
21 27 1 0 0 0 0
22 28 1 0 0 0 0
23 29 1 0 0 0 0
29 15 1 0 0 0 0
30 31 1 1 0 0 0
31 32 1 1 0 0 0
33 32 1 1 0 0 0
33 34 1 0 0 0 0
34 35 1 0 0 0 0
35 30 1 0 0 0 0
30 36 1 0 0 0 0
31 37 1 0 0 0 0
32 38 1 0 0 0 0
39 40 1 1 0 0 0
40 41 1 1 0 0 0
42 41 1 1 0 0 0
42 43 1 0 0 0 0
43 44 1 0 0 0 0
44 39 1 0 0 0 0
39 45 1 0 0 0 0
40 46 1 0 0 0 0
44 47 1 0 0 0 0
42 48 1 0 0 0 0
35 49 1 0 0 0 0
49 48 1 0 0 0 0
43 50 1 0 0 0 0
33 19 1 0 0 0 0
51 52 1 0 0 0 0
16 51 1 0 0 0 0
53 54 1 0 0 0 0
25 53 1 0 0 0 0
55 56 1 0 0 0 0
14 55 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 51 52
M SBL 1 1 57
M SMT 1 OCH3
M SBV 1 57 -0.0202 -0.7244
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 53 54
M SBL 2 1 59
M SMT 2 CH2OH
M SBV 2 59 -0.6373 -0.2837
M STY 1 3 SUP
M SLB 1 3 3
M SAL 3 2 55 56
M SBL 3 1 61
M SMT 3 OCH3
M SBV 3 61 -0.6534 0.3727
S SKP 5
ID FL3FAIGS0010
FORMULA C35H44O21
EXACTMASS 800.23750847
AVERAGEMASS 800.71126
SMILES O(c(c2)c(c(OC)cc2C(=C6)Oc(c5C(=O)6)cc(cc5O)OC(O3)C(O)C(C(C3COC(O4)C(O)C(O)C(C(C)4)O)O)O)OC(C(O)1)OC(CO)C(C(O)1)O)C
M END