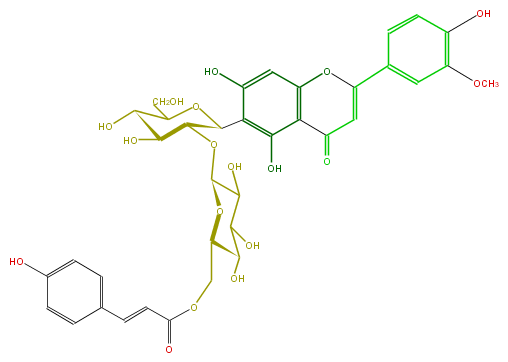
Mol:FL3FADCS0015
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 55 60 0 0 0 0 0 0 0 0999 V2000 | + | 55 60 0 0 0 0 0 0 0 0999 V2000 |
| − | -0.6806 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6806 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.6806 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.6806 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0338 1.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0338 1.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7483 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7483 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7483 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7483 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0338 2.8200 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0338 2.8200 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4629 1.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4629 1.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.1774 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.1774 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.1774 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.1774 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4629 2.8200 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4629 2.8200 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.4629 0.5268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.4629 0.5268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.0338 0.3453 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.0338 0.3453 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0504 2.9523 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0504 2.9523 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8033 2.5176 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8033 2.5176 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5562 2.9523 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5562 2.9523 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5562 3.8217 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5562 3.8217 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8033 4.2563 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8033 4.2563 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.0504 3.8217 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.0504 3.8217 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.4103 4.3148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.4103 4.3148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4156 2.8318 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4156 2.8318 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4825 1.7989 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4825 1.7989 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.8203 1.0572 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.8203 1.0572 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.1581 1.4545 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1581 1.4545 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2574 1.3486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2574 1.3486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.8931 1.9313 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.8931 1.9313 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.6084 1.5870 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.6084 1.5870 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.1398 1.4194 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.1398 1.4194 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.4931 1.0572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.4931 1.0572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4302 0.9501 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4302 0.9501 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.7899 -0.3785 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.7899 -0.3785 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5005 0.0317 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5005 0.0317 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2750 -0.7572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2750 -0.7572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5005 -1.5508 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5005 -1.5508 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.7899 -1.9612 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.7899 -1.9612 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.0153 -1.1722 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.0153 -1.1722 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9941 0.3834 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9941 0.3834 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.5505 -1.6370 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.5505 -1.6370 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.9330 -2.4951 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.9330 -2.4951 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.5005 -2.5715 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.5005 -2.5715 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9639 -3.2412 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9639 -3.2412 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5848 -3.5996 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5848 -3.5996 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1682 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1682 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.7509 -3.5991 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.7509 -3.5991 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.3336 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.3336 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5848 -4.3148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5848 -4.3148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.3336 -2.4558 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.3336 -2.4558 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.0324 -2.0524 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.0324 -2.0524 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.7312 -2.4558 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.7312 -2.4558 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.7312 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.7312 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.0324 -3.6661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.0324 -3.6661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.4286 -2.0532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.4286 -2.0532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.3163 2.5135 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.3163 2.5135 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.4286 1.8713 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.4286 1.8713 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0726 2.0512 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0726 2.0512 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.2565 3.0945 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.2565 3.0945 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 1 0 0 0 0 | + | 1 2 1 0 0 0 0 |
| − | 2 3 2 0 0 0 0 | + | 2 3 2 0 0 0 0 |
| − | 3 4 1 0 0 0 0 | + | 3 4 1 0 0 0 0 |
| − | 4 5 2 0 0 0 0 | + | 4 5 2 0 0 0 0 |
| − | 5 6 1 0 0 0 0 | + | 5 6 1 0 0 0 0 |
| − | 6 1 2 0 0 0 0 | + | 6 1 2 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 5 1 0 0 0 0 | + | 10 5 1 0 0 0 0 |
| − | 7 11 2 0 0 0 0 | + | 7 11 2 0 0 0 0 |
| − | 3 12 1 0 0 0 0 | + | 3 12 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 17 1 0 0 0 0 | + | 16 17 1 0 0 0 0 |
| − | 17 18 2 0 0 0 0 | + | 17 18 2 0 0 0 0 |
| − | 18 13 1 0 0 0 0 | + | 18 13 1 0 0 0 0 |
| − | 9 13 1 0 0 0 0 | + | 9 13 1 0 0 0 0 |
| − | 16 19 1 0 0 0 0 | + | 16 19 1 0 0 0 0 |
| − | 1 20 1 0 0 0 0 | + | 1 20 1 0 0 0 0 |
| − | 21 22 1 1 0 0 0 | + | 21 22 1 1 0 0 0 |
| − | 22 23 1 1 0 0 0 | + | 22 23 1 1 0 0 0 |
| − | 24 23 1 1 0 0 0 | + | 24 23 1 1 0 0 0 |
| − | 24 25 1 0 0 0 0 | + | 24 25 1 0 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | 26 21 1 0 0 0 0 | + | 26 21 1 0 0 0 0 |
| − | 21 27 1 0 0 0 0 | + | 21 27 1 0 0 0 0 |
| − | 22 28 1 0 0 0 0 | + | 22 28 1 0 0 0 0 |
| − | 23 29 1 0 0 0 0 | + | 23 29 1 0 0 0 0 |
| − | 24 2 1 0 0 0 0 | + | 24 2 1 0 0 0 0 |
| − | 30 31 1 0 0 0 0 | + | 30 31 1 0 0 0 0 |
| − | 31 32 1 1 0 0 0 | + | 31 32 1 1 0 0 0 |
| − | 32 33 1 1 0 0 0 | + | 32 33 1 1 0 0 0 |
| − | 34 33 1 1 0 0 0 | + | 34 33 1 1 0 0 0 |
| − | 34 35 1 0 0 0 0 | + | 34 35 1 0 0 0 0 |
| − | 35 30 1 0 0 0 0 | + | 35 30 1 0 0 0 0 |
| − | 30 36 1 0 0 0 0 | + | 30 36 1 0 0 0 0 |
| − | 35 37 1 0 0 0 0 | + | 35 37 1 0 0 0 0 |
| − | 34 38 1 0 0 0 0 | + | 34 38 1 0 0 0 0 |
| − | 33 39 1 0 0 0 0 | + | 33 39 1 0 0 0 0 |
| − | 31 29 1 0 0 0 0 | + | 31 29 1 0 0 0 0 |
| − | 39 40 1 0 0 0 0 | + | 39 40 1 0 0 0 0 |
| − | 40 41 1 0 0 0 0 | + | 40 41 1 0 0 0 0 |
| − | 41 42 1 0 0 0 0 | + | 41 42 1 0 0 0 0 |
| − | 42 43 2 0 0 0 0 | + | 42 43 2 0 0 0 0 |
| − | 43 44 1 0 0 0 0 | + | 43 44 1 0 0 0 0 |
| − | 41 45 2 0 0 0 0 | + | 41 45 2 0 0 0 0 |
| − | 44 46 2 0 0 0 0 | + | 44 46 2 0 0 0 0 |
| − | 46 47 1 0 0 0 0 | + | 46 47 1 0 0 0 0 |
| − | 47 48 2 0 0 0 0 | + | 47 48 2 0 0 0 0 |
| − | 48 49 1 0 0 0 0 | + | 48 49 1 0 0 0 0 |
| − | 49 50 2 0 0 0 0 | + | 49 50 2 0 0 0 0 |
| − | 50 44 1 0 0 0 0 | + | 50 44 1 0 0 0 0 |
| − | 48 51 1 0 0 0 0 | + | 48 51 1 0 0 0 0 |
| − | 52 53 1 0 0 0 0 | + | 52 53 1 0 0 0 0 |
| − | 15 52 1 0 0 0 0 | + | 15 52 1 0 0 0 0 |
| − | 54 55 1 0 0 0 0 | + | 54 55 1 0 0 0 0 |
| − | 26 54 1 0 0 0 0 | + | 26 54 1 0 0 0 0 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 52 53 | + | M SAL 1 2 52 53 |
| − | M SBL 1 1 58 | + | M SBL 1 1 58 |
| − | M SMT 1 OCH3 | + | M SMT 1 OCH3 |
| − | M SBV 1 58 -0.7601 0.4388 | + | M SBV 1 58 -0.7601 0.4388 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 54 55 | + | M SAL 2 2 54 55 |
| − | M SBL 2 1 60 | + | M SBL 2 1 60 |
| − | M SMT 2 ^ CH2OH | + | M SMT 2 ^ CH2OH |
| − | M SBV 2 60 0.4642 -0.4642 | + | M SBV 2 60 0.4642 -0.4642 |
| − | S SKP 5 | + | S SKP 5 |
| − | ID FL3FADCS0015 | + | ID FL3FADCS0015 |
| − | FORMULA C37H38O18 | + | FORMULA C37H38O18 |
| − | EXACTMASS 770.205814412 | + | EXACTMASS 770.205814412 |
| − | AVERAGEMASS 770.6868199999999 | + | AVERAGEMASS 770.6868199999999 |
| − | SMILES C(C(O)4)(O)C(CO)OC(C4OC(O5)C(O)C(O)C(C5COC(=O)C=Cc(c6)ccc(c6)O)O)c(c3O)c(cc(c13)OC(c(c2)ccc(c2OC)O)=CC1=O)O | + | SMILES C(C(O)4)(O)C(CO)OC(C4OC(O5)C(O)C(O)C(C5COC(=O)C=Cc(c6)ccc(c6)O)O)c(c3O)c(cc(c13)OC(c(c2)ccc(c2OC)O)=CC1=O)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
55 60 0 0 0 0 0 0 0 0999 V2000
-0.6806 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.6806 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0338 1.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7483 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7483 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.0338 2.8200 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4629 1.1701 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.1774 1.5825 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.1774 2.4075 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.4629 2.8200 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.4629 0.5268 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.0338 0.3453 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.0504 2.9523 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8033 2.5176 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.5562 2.9523 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.5562 3.8217 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8033 4.2563 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.0504 3.8217 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.4103 4.3148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.4156 2.8318 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.4825 1.7989 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.8203 1.0572 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.1581 1.4545 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2574 1.3486 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.8931 1.9313 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.6084 1.5870 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.1398 1.4194 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.4931 1.0572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.4302 0.9501 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.7899 -0.3785 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.5005 0.0317 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.2750 -0.7572 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.5005 -1.5508 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.7899 -1.9612 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.0153 -1.1722 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.9941 0.3834 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.5505 -1.6370 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.9330 -2.4951 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.5005 -2.5715 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9639 -3.2412 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.5848 -3.5996 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.1682 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.7509 -3.5991 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.3336 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.5848 -4.3148 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.3336 -2.4558 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.0324 -2.0524 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.7312 -2.4558 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.7312 -3.2627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.0324 -3.6661 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.4286 -2.0532 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
5.3163 2.5135 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
6.4286 1.8713 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.0726 2.0512 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.2565 3.0945 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 1 0 0 0 0
2 3 2 0 0 0 0
3 4 1 0 0 0 0
4 5 2 0 0 0 0
5 6 1 0 0 0 0
6 1 2 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 5 1 0 0 0 0
7 11 2 0 0 0 0
3 12 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 17 1 0 0 0 0
17 18 2 0 0 0 0
18 13 1 0 0 0 0
9 13 1 0 0 0 0
16 19 1 0 0 0 0
1 20 1 0 0 0 0
21 22 1 1 0 0 0
22 23 1 1 0 0 0
24 23 1 1 0 0 0
24 25 1 0 0 0 0
25 26 1 0 0 0 0
26 21 1 0 0 0 0
21 27 1 0 0 0 0
22 28 1 0 0 0 0
23 29 1 0 0 0 0
24 2 1 0 0 0 0
30 31 1 0 0 0 0
31 32 1 1 0 0 0
32 33 1 1 0 0 0
34 33 1 1 0 0 0
34 35 1 0 0 0 0
35 30 1 0 0 0 0
30 36 1 0 0 0 0
35 37 1 0 0 0 0
34 38 1 0 0 0 0
33 39 1 0 0 0 0
31 29 1 0 0 0 0
39 40 1 0 0 0 0
40 41 1 0 0 0 0
41 42 1 0 0 0 0
42 43 2 0 0 0 0
43 44 1 0 0 0 0
41 45 2 0 0 0 0
44 46 2 0 0 0 0
46 47 1 0 0 0 0
47 48 2 0 0 0 0
48 49 1 0 0 0 0
49 50 2 0 0 0 0
50 44 1 0 0 0 0
48 51 1 0 0 0 0
52 53 1 0 0 0 0
15 52 1 0 0 0 0
54 55 1 0 0 0 0
26 54 1 0 0 0 0
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 52 53
M SBL 1 1 58
M SMT 1 OCH3
M SBV 1 58 -0.7601 0.4388
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 54 55
M SBL 2 1 60
M SMT 2 ^ CH2OH
M SBV 2 60 0.4642 -0.4642
S SKP 5
ID FL3FADCS0015
FORMULA C37H38O18
EXACTMASS 770.205814412
AVERAGEMASS 770.6868199999999
SMILES C(C(O)4)(O)C(CO)OC(C4OC(O5)C(O)C(O)C(C5COC(=O)C=Cc(c6)ccc(c6)O)O)c(c3O)c(cc(c13)OC(c(c2)ccc(c2OC)O)=CC1=O)O
M END