Mol:FL2FACGS0017
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 43 47 0 0 0 0 0 0 0 0999 V2000 | + | 43 47 0 0 0 0 0 0 0 0999 V2000 |
| − | 1.2875 -0.3163 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2875 -0.3163 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0002 0.0994 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.0002 0.0994 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.2907 -1.1413 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.2907 -1.1413 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0075 -1.5506 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.0075 -1.5506 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7201 -1.1350 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7201 -1.1350 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.7165 -0.3100 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.7165 -0.3100 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4364 -1.5443 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4364 -1.5443 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1490 -1.1286 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1490 -1.1286 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.1454 -0.3036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.1454 -0.3036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4291 0.1057 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4291 0.1057 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7992 0.0772 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7992 0.0772 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.5152 -0.3325 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.5152 -0.3325 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.2281 0.0827 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.2281 0.0827 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.2249 0.9077 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.2249 0.9077 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 5.5088 1.3174 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 5.5088 1.3174 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.7960 0.9022 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.7960 0.9022 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.4375 -2.1875 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.4375 -2.1875 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.6621 0.0448 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.6621 0.0448 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0075 -2.2752 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.0075 -2.2752 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.8808 1.2864 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.8808 1.2864 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 6.8587 -0.2814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 6.8587 -0.2814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.0837 0.1819 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.0837 0.1819 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.6710 -0.5328 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.6710 -0.5328 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8727 -0.3237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8727 -0.3237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.0792 -0.5505 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.0792 -0.5505 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4918 0.1642 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4918 0.1642 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2902 -0.0449 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2902 -0.0449 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.4370 0.5032 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.4370 0.5032 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.5093 -0.2438 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.5093 -0.2438 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.1230 -0.4117 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.1230 -0.4117 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.4938 -0.9800 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.4938 -0.9800 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9353 0.8482 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9353 0.8482 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.3472 1.5617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.3472 1.5617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9353 2.2752 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9353 2.2752 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.1711 1.5617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.1711 1.5617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.5830 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.5830 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.4069 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.4069 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.8194 1.5627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.8194 1.5627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.6444 1.5627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.6444 1.5627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.0569 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.0569 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -5.6444 0.1337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -5.6444 0.1337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.8194 0.1337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.8194 0.1337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -6.8808 0.8482 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -6.8808 0.8482 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 2 0 0 0 0 | + | 1 2 2 0 0 0 0 |
| − | 1 3 1 0 0 0 0 | + | 1 3 1 0 0 0 0 |
| − | 3 4 2 0 0 0 0 | + | 3 4 2 0 0 0 0 |
| − | 4 5 1 0 0 0 0 | + | 4 5 1 0 0 0 0 |
| − | 5 6 2 0 0 0 0 | + | 5 6 2 0 0 0 0 |
| − | 6 2 1 0 0 0 0 | + | 6 2 1 0 0 0 0 |
| − | 5 7 1 0 0 0 0 | + | 5 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 1 0 0 0 0 | + | 8 9 1 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 6 1 0 0 0 0 | + | 10 6 1 0 0 0 0 |
| − | 9 11 1 6 0 0 0 | + | 9 11 1 6 0 0 0 |
| − | 11 12 2 0 0 0 0 | + | 11 12 2 0 0 0 0 |
| − | 12 13 1 0 0 0 0 | + | 12 13 1 0 0 0 0 |
| − | 13 14 2 0 0 0 0 | + | 13 14 2 0 0 0 0 |
| − | 14 15 1 0 0 0 0 | + | 14 15 1 0 0 0 0 |
| − | 15 16 2 0 0 0 0 | + | 15 16 2 0 0 0 0 |
| − | 16 11 1 0 0 0 0 | + | 16 11 1 0 0 0 0 |
| − | 7 17 2 0 0 0 0 | + | 7 17 2 0 0 0 0 |
| − | 1 18 1 0 0 0 0 | + | 1 18 1 0 0 0 0 |
| − | 4 19 1 0 0 0 0 | + | 4 19 1 0 0 0 0 |
| − | 14 20 1 0 0 0 0 | + | 14 20 1 0 0 0 0 |
| − | 13 21 1 0 0 0 0 | + | 13 21 1 0 0 0 0 |
| − | 22 23 1 1 0 0 0 | + | 22 23 1 1 0 0 0 |
| − | 23 24 1 1 0 0 0 | + | 23 24 1 1 0 0 0 |
| − | 25 24 1 1 0 0 0 | + | 25 24 1 1 0 0 0 |
| − | 25 26 1 0 0 0 0 | + | 25 26 1 0 0 0 0 |
| − | 26 27 1 0 0 0 0 | + | 26 27 1 0 0 0 0 |
| − | 27 22 1 0 0 0 0 | + | 27 22 1 0 0 0 0 |
| − | 27 28 1 0 0 0 0 | + | 27 28 1 0 0 0 0 |
| − | 22 29 1 0 0 0 0 | + | 22 29 1 0 0 0 0 |
| − | 23 30 1 0 0 0 0 | + | 23 30 1 0 0 0 0 |
| − | 24 31 1 0 0 0 0 | + | 24 31 1 0 0 0 0 |
| − | 25 18 1 0 0 0 0 | + | 25 18 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 33 34 2 0 0 0 0 | + | 33 34 2 0 0 0 0 |
| − | 33 35 1 0 0 0 0 | + | 33 35 1 0 0 0 0 |
| − | 35 36 2 0 0 0 0 | + | 35 36 2 0 0 0 0 |
| − | 36 37 1 0 0 0 0 | + | 36 37 1 0 0 0 0 |
| − | 37 38 2 0 0 0 0 | + | 37 38 2 0 0 0 0 |
| − | 38 39 1 0 0 0 0 | + | 38 39 1 0 0 0 0 |
| − | 39 40 2 0 0 0 0 | + | 39 40 2 0 0 0 0 |
| − | 40 41 1 0 0 0 0 | + | 40 41 1 0 0 0 0 |
| − | 41 42 2 0 0 0 0 | + | 41 42 2 0 0 0 0 |
| − | 42 37 1 0 0 0 0 | + | 42 37 1 0 0 0 0 |
| − | 40 43 1 0 0 0 0 | + | 40 43 1 0 0 0 0 |
| − | 32 28 1 0 0 0 0 | + | 32 28 1 0 0 0 0 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL2FACGS0017 | + | ID FL2FACGS0017 |
| − | KNApSAcK_ID C00014338 | + | KNApSAcK_ID C00014338 |
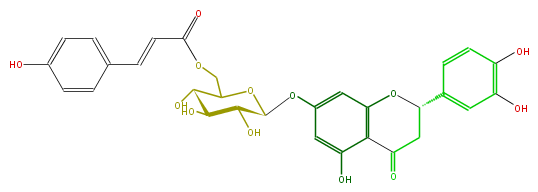
| − | NAME (2S)-5,7,3',4'-Tetrahydroxyflavanone 7-(6-p-coumaroylglucoside) | + | NAME (2S)-5,7,3',4'-Tetrahydroxyflavanone 7-(6-p-coumaroylglucoside) |
| − | CAS_RN 467437-59-8 | + | CAS_RN 467437-59-8 |
| − | FORMULA C30H28O13 | + | FORMULA C30H28O13 |
| − | EXACTMASS 596.152990982 | + | EXACTMASS 596.152990982 |
| − | AVERAGEMASS 596.53552 | + | AVERAGEMASS 596.53552 |
| − | SMILES O(C(COC(C=Cc(c5)ccc(O)c5)=O)1)C(Oc(c4)cc(O)c(c42)C(CC(c(c3)cc(O)c(c3)O)O2)=O)C(C(O)C1O)O | + | SMILES O(C(COC(C=Cc(c5)ccc(O)c5)=O)1)C(Oc(c4)cc(O)c(c42)C(CC(c(c3)cc(O)c(c3)O)O2)=O)C(C(O)C1O)O |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
43 47 0 0 0 0 0 0 0 0999 V2000
1.2875 -0.3163 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.0002 0.0994 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.2907 -1.1413 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.0075 -1.5506 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.7201 -1.1350 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
2.7165 -0.3100 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4364 -1.5443 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1490 -1.1286 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.1454 -0.3036 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4291 0.1057 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.7992 0.0772 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.5152 -0.3325 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.2281 0.0827 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
6.2249 0.9077 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
5.5088 1.3174 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
4.7960 0.9022 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.4375 -2.1875 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
0.6621 0.0448 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.0075 -2.2752 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
6.8808 1.2864 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
6.8587 -0.2814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.0837 0.1819 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.6710 -0.5328 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8727 -0.3237 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.0792 -0.5505 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.4918 0.1642 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.2902 -0.0449 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.4370 0.5032 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.5093 -0.2438 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.1230 -0.4117 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-0.4938 -0.9800 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.9353 0.8482 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-2.3472 1.5617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9353 2.2752 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.1711 1.5617 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.5830 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.4069 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.8194 1.5627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.6444 1.5627 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.0569 0.8482 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-5.6444 0.1337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-4.8194 0.1337 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-6.8808 0.8482 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1 2 2 0 0 0 0
1 3 1 0 0 0 0
3 4 2 0 0 0 0
4 5 1 0 0 0 0
5 6 2 0 0 0 0
6 2 1 0 0 0 0
5 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 1 0 0 0 0
9 10 1 0 0 0 0
10 6 1 0 0 0 0
9 11 1 6 0 0 0
11 12 2 0 0 0 0
12 13 1 0 0 0 0
13 14 2 0 0 0 0
14 15 1 0 0 0 0
15 16 2 0 0 0 0
16 11 1 0 0 0 0
7 17 2 0 0 0 0
1 18 1 0 0 0 0
4 19 1 0 0 0 0
14 20 1 0 0 0 0
13 21 1 0 0 0 0
22 23 1 1 0 0 0
23 24 1 1 0 0 0
25 24 1 1 0 0 0
25 26 1 0 0 0 0
26 27 1 0 0 0 0
27 22 1 0 0 0 0
27 28 1 0 0 0 0
22 29 1 0 0 0 0
23 30 1 0 0 0 0
24 31 1 0 0 0 0
25 18 1 0 0 0 0
32 33 1 0 0 0 0
33 34 2 0 0 0 0
33 35 1 0 0 0 0
35 36 2 0 0 0 0
36 37 1 0 0 0 0
37 38 2 0 0 0 0
38 39 1 0 0 0 0
39 40 2 0 0 0 0
40 41 1 0 0 0 0
41 42 2 0 0 0 0
42 37 1 0 0 0 0
40 43 1 0 0 0 0
32 28 1 0 0 0 0
S SKP 8
ID FL2FACGS0017
KNApSAcK_ID C00014338
NAME (2S)-5,7,3',4'-Tetrahydroxyflavanone 7-(6-p-coumaroylglucoside)
CAS_RN 467437-59-8
FORMULA C30H28O13
EXACTMASS 596.152990982
AVERAGEMASS 596.53552
SMILES O(C(COC(C=Cc(c5)ccc(O)c5)=O)1)C(Oc(c4)cc(O)c(c42)C(CC(c(c3)cc(O)c(c3)O)O2)=O)C(C(O)C1O)O
M END