Mol:FL1CDDGS0001
From Metabolomics.JP
(Difference between revisions)
| Line 1: | Line 1: | ||
| − | + | ||
| − | + | ||
| − | Copyright: ARM project http://www.metabolome.jp/ | + | Copyright: ARM project http://www.metabolome.jp/ |
| − | 35 37 0 0 0 0 0 0 0 0999 V2000 | + | 35 37 0 0 0 0 0 0 0 0999 V2000 |
| − | -3.6062 0.4901 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.6062 0.4901 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.6062 -0.1496 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.6062 -0.1496 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0522 -0.4695 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0522 -0.4695 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4982 -0.1496 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4982 -0.1496 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -2.4982 0.4901 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -2.4982 0.4901 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0522 0.8099 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0522 0.8099 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9445 -0.4693 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9445 -0.4693 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.3920 -0.1503 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.3920 -0.1503 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.8407 -0.4686 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.8407 -0.4686 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2905 -0.1510 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2905 -0.1510 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2479 -0.4618 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2479 -0.4618 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7862 -0.1510 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7862 -0.1510 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.7862 0.4707 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.7862 0.4707 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 0.2479 0.7815 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 0.2479 0.7815 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -0.2905 0.4707 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -0.2905 0.4707 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9445 -1.1073 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9445 -1.1073 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.0522 -1.1088 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.0522 -1.1088 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.3245 0.7814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.3245 0.7814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.1328 0.9850 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 | + | 2.1328 0.9850 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0 |
| − | 2.4930 0.5097 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 2.4930 0.5097 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.0144 0.6963 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 3.0144 0.6963 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.6331 0.5520 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 | + | 3.6331 0.5520 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0 |
| − | 3.1483 1.0804 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 | + | 3.1483 1.0804 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0 |
| − | 2.6946 0.8410 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.6946 0.8410 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.0263 0.3846 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.0263 0.3846 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.3372 0.1372 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.3372 0.1372 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 4.5938 0.2745 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 4.5938 0.2745 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.9445 0.8098 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.9445 0.8098 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -1.2300 0.3973 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -1.2300 0.3973 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1.6522 -0.6511 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 1.6522 -0.6511 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 2.5182 -1.1511 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 2.5182 -1.1511 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.8466 1.7962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.8466 1.7962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 3.5759 2.7588 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | 3.5759 2.7588 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -3.9635 1.1088 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 | + | -3.9635 1.1088 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | -4.4636 1.9748 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 | + | -4.4636 1.9748 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0 |
| − | 1 2 2 0 0 0 0 | + | 1 2 2 0 0 0 0 |
| − | 2 3 1 0 0 0 0 | + | 2 3 1 0 0 0 0 |
| − | 3 4 2 0 0 0 0 | + | 3 4 2 0 0 0 0 |
| − | 4 5 1 0 0 0 0 | + | 4 5 1 0 0 0 0 |
| − | 5 6 2 0 0 0 0 | + | 5 6 2 0 0 0 0 |
| − | 6 1 1 0 0 0 0 | + | 6 1 1 0 0 0 0 |
| − | 4 7 1 0 0 0 0 | + | 4 7 1 0 0 0 0 |
| − | 7 8 1 0 0 0 0 | + | 7 8 1 0 0 0 0 |
| − | 8 9 2 0 0 0 0 | + | 8 9 2 0 0 0 0 |
| − | 9 10 1 0 0 0 0 | + | 9 10 1 0 0 0 0 |
| − | 10 11 2 0 0 0 0 | + | 10 11 2 0 0 0 0 |
| − | 11 12 1 0 0 0 0 | + | 11 12 1 0 0 0 0 |
| − | 12 13 2 0 0 0 0 | + | 12 13 2 0 0 0 0 |
| − | 13 14 1 0 0 0 0 | + | 13 14 1 0 0 0 0 |
| − | 14 15 2 0 0 0 0 | + | 14 15 2 0 0 0 0 |
| − | 15 10 1 0 0 0 0 | + | 15 10 1 0 0 0 0 |
| − | 7 16 2 0 0 0 0 | + | 7 16 2 0 0 0 0 |
| − | 3 17 1 0 0 0 0 | + | 3 17 1 0 0 0 0 |
| − | 13 18 1 0 0 0 0 | + | 13 18 1 0 0 0 0 |
| − | 19 20 1 1 0 0 0 | + | 19 20 1 1 0 0 0 |
| − | 20 21 1 1 0 0 0 | + | 20 21 1 1 0 0 0 |
| − | 22 21 1 1 0 0 0 | + | 22 21 1 1 0 0 0 |
| − | 22 23 1 0 0 0 0 | + | 22 23 1 0 0 0 0 |
| − | 23 24 1 0 0 0 0 | + | 23 24 1 0 0 0 0 |
| − | 24 19 1 0 0 0 0 | + | 24 19 1 0 0 0 0 |
| − | 20 25 1 0 0 0 0 | + | 20 25 1 0 0 0 0 |
| − | 21 26 1 0 0 0 0 | + | 21 26 1 0 0 0 0 |
| − | 22 27 1 0 0 0 0 | + | 22 27 1 0 0 0 0 |
| − | 19 18 1 0 0 0 0 | + | 19 18 1 0 0 0 0 |
| − | 5 28 1 0 0 0 0 | + | 5 28 1 0 0 0 0 |
| − | 28 29 1 0 0 0 0 | + | 28 29 1 0 0 0 0 |
| − | 12 30 1 0 0 0 0 | + | 12 30 1 0 0 0 0 |
| − | 30 31 1 0 0 0 0 | + | 30 31 1 0 0 0 0 |
| − | 23 32 1 0 0 0 0 | + | 23 32 1 0 0 0 0 |
| − | 32 33 1 0 0 0 0 | + | 32 33 1 0 0 0 0 |
| − | 1 34 1 0 0 0 0 | + | 1 34 1 0 0 0 0 |
| − | 34 35 1 0 0 0 0 | + | 34 35 1 0 0 0 0 |
| − | M STY 1 4 SUP | + | M STY 1 4 SUP |
| − | M SLB 1 4 4 | + | M SLB 1 4 4 |
| − | M SAL 4 2 32 33 | + | M SAL 4 2 32 33 |
| − | M SBL 4 1 34 | + | M SBL 4 1 34 |
| − | M SMT 4 CH2OH | + | M SMT 4 CH2OH |
| − | M SVB 4 34 3.8637 0.5558 | + | M SVB 4 34 3.8637 0.5558 |
| − | M STY 1 3 SUP | + | M STY 1 3 SUP |
| − | M SLB 1 3 3 | + | M SLB 1 3 3 |
| − | M SAL 3 2 34 35 | + | M SAL 3 2 34 35 |
| − | M SBL 3 1 36 | + | M SBL 3 1 36 |
| − | M SMT 3 OCH3 | + | M SMT 3 OCH3 |
| − | M SVB 3 36 -3.9635 1.1088 | + | M SVB 3 36 -3.9635 1.1088 |
| − | M STY 1 2 SUP | + | M STY 1 2 SUP |
| − | M SLB 1 2 2 | + | M SLB 1 2 2 |
| − | M SAL 2 2 30 31 | + | M SAL 2 2 30 31 |
| − | M SBL 2 1 32 | + | M SBL 2 1 32 |
| − | M SMT 2 OCH3 | + | M SMT 2 OCH3 |
| − | M SVB 2 32 0.9672 -0.3572 | + | M SVB 2 32 0.9672 -0.3572 |
| − | M STY 1 1 SUP | + | M STY 1 1 SUP |
| − | M SLB 1 1 1 | + | M SLB 1 1 1 |
| − | M SAL 1 2 28 29 | + | M SAL 1 2 28 29 |
| − | M SBL 1 1 30 | + | M SBL 1 1 30 |
| − | M SMT 1 OCH3 | + | M SMT 1 OCH3 |
| − | M SVB 1 30 -1.9445 0.8098 | + | M SVB 1 30 -1.9445 0.8098 |
| − | S SKP 8 | + | S SKP 8 |
| − | ID FL1CDDGS0001 | + | ID FL1CDDGS0001 |
| − | KNApSAcK_ID C00007917 | + | KNApSAcK_ID C00007917 |
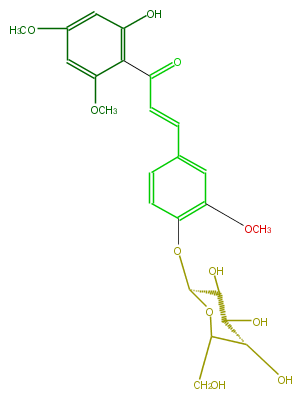
| − | NAME 4,2'-Dihydroxy-3,4',6'-trimethoxychalcone 4-glucoside | + | NAME 4,2'-Dihydroxy-3,4',6'-trimethoxychalcone 4-glucoside |
| − | CAS_RN 112572-59-5 | + | CAS_RN 112572-59-5 |
| − | FORMULA C24H28O11 | + | FORMULA C24H28O11 |
| − | EXACTMASS 492.163161738 | + | EXACTMASS 492.163161738 |
| − | AVERAGEMASS 492.47252000000003 | + | AVERAGEMASS 492.47252000000003 |
| − | SMILES [C@H]([C@@H]3O)(OC([C@H]([C@@H](O)3)O)CO)Oc(c1)c(cc(C=CC(=O)c(c(O)2)c(OC)cc(OC)c2)c1)OC | + | SMILES [C@H]([C@@H]3O)(OC([C@H]([C@@H](O)3)O)CO)Oc(c1)c(cc(C=CC(=O)c(c(O)2)c(OC)cc(OC)c2)c1)OC |
M END | M END | ||
| − | |||
Latest revision as of 09:00, 14 March 2009
Copyright: ARM project http://www.metabolome.jp/
35 37 0 0 0 0 0 0 0 0999 V2000
-3.6062 0.4901 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.6062 -0.1496 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.0522 -0.4695 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.4982 -0.1496 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-2.4982 0.4901 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-3.0522 0.8099 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9445 -0.4693 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.3920 -0.1503 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.8407 -0.4686 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.2905 -0.1510 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2479 -0.4618 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7862 -0.1510 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.7862 0.4707 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
0.2479 0.7815 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-0.2905 0.4707 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
-1.9445 -1.1073 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.0522 -1.1088 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
1.3245 0.7814 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.1328 0.9850 0.0000 C 0 0 2 0 0 0 0 0 0 0 0 0
2.4930 0.5097 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.0144 0.6963 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.6331 0.5520 0.0000 C 0 0 1 0 0 0 0 0 0 0 0 0
3.1483 1.0804 0.0000 C 0 0 3 0 0 0 0 0 0 0 0 0
2.6946 0.8410 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.0263 0.3846 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
3.3372 0.1372 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
4.5938 0.2745 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.9445 0.8098 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-1.2300 0.3973 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1.6522 -0.6511 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
2.5182 -1.1511 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.8466 1.7962 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
3.5759 2.7588 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-3.9635 1.1088 0.0000 O 0 0 0 0 0 0 0 0 0 0 0 0
-4.4636 1.9748 0.0000 C 0 0 0 0 0 0 0 0 0 0 0 0
1 2 2 0 0 0 0
2 3 1 0 0 0 0
3 4 2 0 0 0 0
4 5 1 0 0 0 0
5 6 2 0 0 0 0
6 1 1 0 0 0 0
4 7 1 0 0 0 0
7 8 1 0 0 0 0
8 9 2 0 0 0 0
9 10 1 0 0 0 0
10 11 2 0 0 0 0
11 12 1 0 0 0 0
12 13 2 0 0 0 0
13 14 1 0 0 0 0
14 15 2 0 0 0 0
15 10 1 0 0 0 0
7 16 2 0 0 0 0
3 17 1 0 0 0 0
13 18 1 0 0 0 0
19 20 1 1 0 0 0
20 21 1 1 0 0 0
22 21 1 1 0 0 0
22 23 1 0 0 0 0
23 24 1 0 0 0 0
24 19 1 0 0 0 0
20 25 1 0 0 0 0
21 26 1 0 0 0 0
22 27 1 0 0 0 0
19 18 1 0 0 0 0
5 28 1 0 0 0 0
28 29 1 0 0 0 0
12 30 1 0 0 0 0
30 31 1 0 0 0 0
23 32 1 0 0 0 0
32 33 1 0 0 0 0
1 34 1 0 0 0 0
34 35 1 0 0 0 0
M STY 1 4 SUP
M SLB 1 4 4
M SAL 4 2 32 33
M SBL 4 1 34
M SMT 4 CH2OH
M SVB 4 34 3.8637 0.5558
M STY 1 3 SUP
M SLB 1 3 3
M SAL 3 2 34 35
M SBL 3 1 36
M SMT 3 OCH3
M SVB 3 36 -3.9635 1.1088
M STY 1 2 SUP
M SLB 1 2 2
M SAL 2 2 30 31
M SBL 2 1 32
M SMT 2 OCH3
M SVB 2 32 0.9672 -0.3572
M STY 1 1 SUP
M SLB 1 1 1
M SAL 1 2 28 29
M SBL 1 1 30
M SMT 1 OCH3
M SVB 1 30 -1.9445 0.8098
S SKP 8
ID FL1CDDGS0001
KNApSAcK_ID C00007917
NAME 4,2'-Dihydroxy-3,4',6'-trimethoxychalcone 4-glucoside
CAS_RN 112572-59-5
FORMULA C24H28O11
EXACTMASS 492.163161738
AVERAGEMASS 492.47252000000003
SMILES [C@H]([C@@H]3O)(OC([C@H]([C@@H](O)3)O)CO)Oc(c1)c(cc(C=CC(=O)c(c(O)2)c(OC)cc(OC)c2)c1)OC
M END